+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | 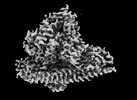 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | CryoEM structure of PI3Kalpha | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | PI3Kalapha / isoform selective /  structure-based drug design. (医薬品設計) / structure-based drug design. (医薬品設計) /  CYTOSOLIC PROTEIN (細胞質基質) CYTOSOLIC PROTEIN (細胞質基質) | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報perinuclear endoplasmic reticulum membrane / response to muscle inactivity / negative regulation of actin filament depolymerization / regulation of toll-like receptor 4 signaling pathway / response to L-leucine / phosphatidylinositol kinase activity / regulation of actin filament organization / phosphatidylinositol 3-kinase regulator activity / response to butyrate / autosome genomic imprinting ...perinuclear endoplasmic reticulum membrane / response to muscle inactivity / negative regulation of actin filament depolymerization / regulation of toll-like receptor 4 signaling pathway / response to L-leucine / phosphatidylinositol kinase activity / regulation of actin filament organization / phosphatidylinositol 3-kinase regulator activity / response to butyrate / autosome genomic imprinting / positive regulation of focal adhesion disassembly / IRS-mediated signalling / cellular response to hydrostatic pressure / phosphatidylinositol 3-kinase activator activity / interleukin-18-mediated signaling pathway / PI3K events in ERBB4 signaling / myeloid leukocyte migration / phosphatidylinositol 3-kinase regulatory subunit binding / 1-phosphatidylinositol-3-kinase regulator activity / neurotrophin TRKA receptor binding / Activated NTRK2 signals through PI3K / positive regulation of protein localization to membrane / cis-Golgi network / Activated NTRK3 signals through PI3K / kinase activator activity / ErbB-3 class receptor binding / negative regulation of fibroblast apoptotic process / RHOF GTPase cycle / cardiac muscle cell contraction / phosphatidylinositol 3-kinase complex, class IB / vasculature development /  transmembrane receptor protein tyrosine kinase adaptor activity / RHOD GTPase cycle / positive regulation of endoplasmic reticulum unfolded protein response / Signaling by cytosolic FGFR1 fusion mutants / transmembrane receptor protein tyrosine kinase adaptor activity / RHOD GTPase cycle / positive regulation of endoplasmic reticulum unfolded protein response / Signaling by cytosolic FGFR1 fusion mutants /  regulation of cellular respiration / enzyme-substrate adaptor activity / regulation of cellular respiration / enzyme-substrate adaptor activity /  phosphatidylinositol 3-kinase complex / phosphatidylinositol 3-kinase complex /  anoikis / Nephrin family interactions / 1-phosphatidylinositol-4-phosphate 3-kinase activity / RND1 GTPase cycle / Costimulation by the CD28 family / vascular endothelial growth factor signaling pathway / 1-phosphatidylinositol-4,5-bisphosphate 3-kinase activity / RND2 GTPase cycle / MET activates PI3K/AKT signaling / PI3K/AKT activation / RND3 GTPase cycle / positive regulation of leukocyte migration / anoikis / Nephrin family interactions / 1-phosphatidylinositol-4-phosphate 3-kinase activity / RND1 GTPase cycle / Costimulation by the CD28 family / vascular endothelial growth factor signaling pathway / 1-phosphatidylinositol-4,5-bisphosphate 3-kinase activity / RND2 GTPase cycle / MET activates PI3K/AKT signaling / PI3K/AKT activation / RND3 GTPase cycle / positive regulation of leukocyte migration /  phosphatidylinositol-4,5-bisphosphate 3-kinase / positive regulation of filopodium assembly / phosphatidylinositol 3-kinase complex, class IA / negative regulation of stress fiber assembly / phosphatidylinositol-4,5-bisphosphate 3-kinase / positive regulation of filopodium assembly / phosphatidylinositol 3-kinase complex, class IA / negative regulation of stress fiber assembly /  PI3キナーゼ / relaxation of cardiac muscle / growth hormone receptor signaling pathway / phosphatidylinositol-3-phosphate biosynthetic process / PI3キナーゼ / relaxation of cardiac muscle / growth hormone receptor signaling pathway / phosphatidylinositol-3-phosphate biosynthetic process /  insulin binding / 1-phosphatidylinositol-3-kinase activity / RHOV GTPase cycle / negative regulation of macroautophagy / RHOB GTPase cycle / Signaling by ALK / negative regulation of cell-matrix adhesion / GP1b-IX-V activation signalling / PI-3K cascade:FGFR3 / Erythropoietin activates Phosphoinositide-3-kinase (PI3K) / protein kinase activator activity / response to dexamethasone / PI-3K cascade:FGFR2 / PI-3K cascade:FGFR4 / RHOJ GTPase cycle / RHOC GTPase cycle / PI-3K cascade:FGFR1 / negative regulation of osteoclast differentiation / intracellular glucose homeostasis / CD28 dependent PI3K/Akt signaling / Synthesis of PIPs at the plasma membrane / phosphatidylinositol phosphate biosynthetic process / CDC42 GTPase cycle / RHOU GTPase cycle / PI3K events in ERBB2 signaling / Signaling by ALK fusions and activated point mutants / RHOG GTPase cycle / negative regulation of anoikis / RET signaling / T cell differentiation / regulation of multicellular organism growth / extrinsic apoptotic signaling pathway via death domain receptors / insulin binding / 1-phosphatidylinositol-3-kinase activity / RHOV GTPase cycle / negative regulation of macroautophagy / RHOB GTPase cycle / Signaling by ALK / negative regulation of cell-matrix adhesion / GP1b-IX-V activation signalling / PI-3K cascade:FGFR3 / Erythropoietin activates Phosphoinositide-3-kinase (PI3K) / protein kinase activator activity / response to dexamethasone / PI-3K cascade:FGFR2 / PI-3K cascade:FGFR4 / RHOJ GTPase cycle / RHOC GTPase cycle / PI-3K cascade:FGFR1 / negative regulation of osteoclast differentiation / intracellular glucose homeostasis / CD28 dependent PI3K/Akt signaling / Synthesis of PIPs at the plasma membrane / phosphatidylinositol phosphate biosynthetic process / CDC42 GTPase cycle / RHOU GTPase cycle / PI3K events in ERBB2 signaling / Signaling by ALK fusions and activated point mutants / RHOG GTPase cycle / negative regulation of anoikis / RET signaling / T cell differentiation / regulation of multicellular organism growth / extrinsic apoptotic signaling pathway via death domain receptors /  insulin receptor substrate binding / insulin receptor substrate binding /  Interleukin-3, Interleukin-5 and GM-CSF signaling / PI3K Cascade / Interleukin-3, Interleukin-5 and GM-CSF signaling / PI3K Cascade /  介在板 / RHOA GTPase cycle / positive regulation of TOR signaling / endothelial cell migration / RAC2 GTPase cycle / RAC3 GTPase cycle / GAB1 signalosome 介在板 / RHOA GTPase cycle / positive regulation of TOR signaling / endothelial cell migration / RAC2 GTPase cycle / RAC3 GTPase cycle / GAB1 signalosome類似検索 - 分子機能 | |||||||||
| 生物種 |   Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
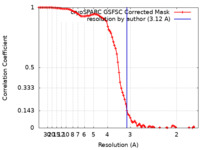
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 3.12 Å クライオ電子顕微鏡法 / 解像度: 3.12 Å | |||||||||
 データ登録者 データ登録者 | Valverde R / Shi H / Holliday M / Sun M | |||||||||
| 資金援助 | 1件
| |||||||||
 引用 引用 |  ジャーナル: Cancer Discov / 年: 2024 ジャーナル: Cancer Discov / 年: 2024タイトル: Discovery and Clinical Proof-of-Concept of RLY-2608, a First-in-Class Mutant-Selective Allosteric PI3Kα Inhibitor That Decouples Antitumor Activity from Hyperinsulinemia. 著者: Andreas Varkaris / Ermira Pazolli / Hakan Gunaydin / Qi Wang / Levi Pierce / Alessandro A Boezio / Artemisa Bulku / Lucian DiPietro / Cary Fridrich / Adam Frost / Fabrizio Giordanetto / Erika ...著者: Andreas Varkaris / Ermira Pazolli / Hakan Gunaydin / Qi Wang / Levi Pierce / Alessandro A Boezio / Artemisa Bulku / Lucian DiPietro / Cary Fridrich / Adam Frost / Fabrizio Giordanetto / Erika P Hamilton / Katherine Harris / Michael Holliday / Tamieka L Hunter / Amanda Iskandar / Yongli Ji / Alexandre Larivée / Jonathan R LaRochelle / André Lescarbeau / Fabien Llambi / Brenda Lormil / Mary M Mader / Brenton G Mar / Iain Martin / Thomas H McLean / Klaus Michelsen / Yakov Pechersky / Erika Puente-Poushnejad / Kevin Raynor / Dipali Rogala / Ramin Samadani / Alison M Schram / Kelley Shortsleeves / Sweta Swaminathan / Shahein Tajmir / Gege Tan / Yong Tang / Roberto Valverde / Bryan Wehrenberg / Jeremy Wilbur / Bret R Williams / Hongtao Zeng / Hanmo Zhang / W Patrick Walters / Beni B Wolf / David E Shaw / Donald A Bergstrom / James Watters / James S Fraser / Pascal D Fortin / D Randal Kipp /   要旨: PIK3CA (PI3Kα) is a lipid kinase commonly mutated in cancer, including ∼40% of hormone receptor-positive breast cancer. The most frequently observed mutants occur in the kinase and helical domains. ...PIK3CA (PI3Kα) is a lipid kinase commonly mutated in cancer, including ∼40% of hormone receptor-positive breast cancer. The most frequently observed mutants occur in the kinase and helical domains. Orthosteric PI3Kα inhibitors suffer from poor selectivity leading to undesirable side effects, most prominently hyperglycemia due to inhibition of wild-type (WT) PI3Kα. Here, we used molecular dynamics simulations and cryo-electron microscopy to identify an allosteric network that provides an explanation for how mutations favor PI3Kα activation. A DNA-encoded library screen leveraging electron microscopy-optimized constructs, differential enrichment, and an orthosteric-blocking compound led to the identification of RLY-2608, a first-in-class allosteric mutant-selective inhibitor of PI3Kα. RLY-2608 inhibited tumor growth in PIK3CA-mutant xenograft models with minimal impact on insulin, a marker of dysregulated glucose homeostasis. RLY-2608 elicited objective tumor responses in two patients diagnosed with advanced hormone receptor-positive breast cancer with kinase or helical domain PIK3CA mutations, with no observed WT PI3Kα-related toxicities. SIGNIFICANCE: Treatments for PIK3CA-mutant cancers are limited by toxicities associated with the inhibition of WT PI3Kα. Molecular dynamics, cryo-electron microscopy, and DNA-encoded libraries were ...SIGNIFICANCE: Treatments for PIK3CA-mutant cancers are limited by toxicities associated with the inhibition of WT PI3Kα. Molecular dynamics, cryo-electron microscopy, and DNA-encoded libraries were used to develop RLY-2608, a first-in-class inhibitor that demonstrates mutant selectivity in patients. This marks the advance of clinical mutant-selective inhibition that overcomes limitations of orthosteric PI3Kα inhibitors. See related commentary by Gong and Vanhaesebroeck, p. 204 . See related article by Varkaris et al., p. 227 . This article is featured in Selected Articles from This Issue, p. 201. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_41617.map.gz emd_41617.map.gz | 3.6 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-41617-v30.xml emd-41617-v30.xml emd-41617.xml emd-41617.xml | 25.6 KB 25.6 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_41617_fsc.xml emd_41617_fsc.xml | 9.5 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_41617.png emd_41617.png | 69.8 KB | ||
| Filedesc metadata |  emd-41617.cif.gz emd-41617.cif.gz | 7.7 KB | ||
| その他 |  emd_41617_additional_1.map.gz emd_41617_additional_1.map.gz emd_41617_half_map_1.map.gz emd_41617_half_map_1.map.gz emd_41617_half_map_2.map.gz emd_41617_half_map_2.map.gz | 81.7 MB 84.5 MB 84.5 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-41617 http://ftp.pdbj.org/pub/emdb/structures/EMD-41617 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-41617 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-41617 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8tu6MC  8ts7C  8ts8C  8ts9C  8tsaC  8tsbC  8tscC  8tsdC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_41617.map.gz / 形式: CCP4 / 大きさ: 91.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_41617.map.gz / 形式: CCP4 / 大きさ: 91.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 0.819 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-追加マップ: #1
| ファイル | emd_41617_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_41617_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_41617_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : PI3Kalpha
| 全体 | 名称: PI3Kalpha |
|---|---|
| 要素 |
|
-超分子 #1: PI3Kalpha
| 超分子 | 名称: PI3Kalpha / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 850 KDa |
-超分子 #2: p110
| 超分子 | 名称: p110 / タイプ: complex / ID: 2 / 親要素: 1 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
-超分子 #3: p85
| 超分子 | 名称: p85 / タイプ: complex / ID: 3 / 親要素: 1 / 含まれる分子: #2 |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
-分子 #1: Phosphatidylinositol 4,5-bisphosphate 3-kinase catalytic subunit ...
| 分子 | 名称: Phosphatidylinositol 4,5-bisphosphate 3-kinase catalytic subunit alpha isoform タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 126.301992 KDa |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: MHHHHHHGSL EVLFQGPPPR PSSGELWGIH LMPPRILVEC LLPNGMIVTL ECLREATLIT IKHELFKEAR KYPLHQLLQD ESSYIFVSV TQEAEREEFF DETRRLCDLR LFQPFLKVIE PVGNREEKIL NREIGFAIGM PVCEFDMVKD PEVQDFRRNI L NVCKEAVD ...文字列: MHHHHHHGSL EVLFQGPPPR PSSGELWGIH LMPPRILVEC LLPNGMIVTL ECLREATLIT IKHELFKEAR KYPLHQLLQD ESSYIFVSV TQEAEREEFF DETRRLCDLR LFQPFLKVIE PVGNREEKIL NREIGFAIGM PVCEFDMVKD PEVQDFRRNI L NVCKEAVD LRDLNSPHSR AMYVYPPNVE SSPELPKHIY NKLDKGQIIV VIWVIVSPNN DKQKYTLKIN HDCVPEQVIA EA IRKKTRS MLLSSEQLKL CVLEYQGKYI LKVCGCDEYF LEKYPLSQYK YIRSCIMLGR MPNLMLMAKE SLYSQLPMDC FTM PSYSRR ISTATPYMNG ETSTKSLWVI NSALRIKILC ATYVNVNIRD IDKIYVRTGI YHGGEPLCDN VNTQRVPCSN PRWN EWLNY DIYIPDLPRA ARLCLSICSV KGRKGAKEEH CPLAWGNINL FDYTDTLVSG KMALNLWPVP HGLEDLLNPI GVTGS NPNK ETPCLELEFD WFSSVVKFPD MSVIEEHANW SVSREAGFSY SHAGLSNRLA RDNELRENDK EQLKAISTRD PLSEIT EQE KDFLWSHRHY CVTIPEILPK LLLSVKWNSR DEVAQMYCLV KDWPPIKPEQ AMELLDCNYP DPMVRGFAVR CLEKYLT DD KLSQYLIQLV QVLKYEQYLD NLLVRFLLKK ALTNQRIGHF FFWHLKSEMH NKTVSQRFGL LLESYCRACG MYLKHLNR Q VEAMEKLINL TDILKQEKKD ETQKVQMKFL VEQMRRPDFM DALQGFLSPL NPAHQLGNLR LEECRIMSSA KRPLWLNWE NPDIMSELLF QNNEIIFKNG DDLRQDMLTL QIIRIMENIW QNQGLDLRML PYGCLSIGDC VGLIEVVRNS HTIMQIQCKG GLKGALQFN SHTLHQWLKD KNKGEIYDAA IDLFTRSCAG YCVATFILGI GDRHNSNIMV KDDGQLFHID FGHFLDHKKK K FGYKRERV PFVLTQDFLI VISKGAQECT KTREFERFQE MCYKAYLAIR QHANLFINLF SMMLGSGMPE LQSFDDIAYI RK TLALDKT EQEALEYFMK QMNDAHHGGW TTKMDWIFHT IKQHALN UniProtKB: Phosphatidylinositol 4,5-bisphosphate 3-kinase catalytic subunit alpha isoform |
-分子 #2: Phosphatidylinositol 3-kinase regulatory subunit alpha
| 分子 | 名称: Phosphatidylinositol 3-kinase regulatory subunit alpha タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 83.710281 KDa |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: MSAEGYQYRA LYDYKKEREE DIDLHLGDIL TVNKGSLVAL GFSDGQEARP EEIGWLNGYN ETTGERGDFP GTYVEYIGRK KISPPTPKP RPPRPLPVAP GSSKTEADVE QQALTLPDLA EQFAPPDIAP PLLIKLVEAI EKKGLECSTL YRTQSSSNLA E LRQLLDCD ...文字列: MSAEGYQYRA LYDYKKEREE DIDLHLGDIL TVNKGSLVAL GFSDGQEARP EEIGWLNGYN ETTGERGDFP GTYVEYIGRK KISPPTPKP RPPRPLPVAP GSSKTEADVE QQALTLPDLA EQFAPPDIAP PLLIKLVEAI EKKGLECSTL YRTQSSSNLA E LRQLLDCD TPSVDLEMID VHVLADAFKR YLLDLPNPVI PAAVYSEMIS LAPEVQSSEE YIQLLKKLIR SPSIPHQYWL TL QYLLKHF FKLSQTSSKN LLNARVLSEI FSPMLFRFSA ASSDNTENLI KVIEILISTE WNERQPAPAL PPKPPKPTTV ANN GMNNNM SLQDAEWYWG DISREEVNEK LRDTADGTFL VRDASTKMHG DYTLTLRKGG NNKLIKIFHR DGKYGFSDPL TFSS VVELI NHYRNESLAQ YNPKLDVKLL YPVSKYQQDQ VVKEDNIEAV GKKLHEYNTQ FQEKSREYDR LYEEYTRTSQ EIQMK RTAI EAFNETIKIF EEQCQTQERY SKEYIEKFKR EGNEKEIQRI MHNYDKLKSR ISEIIDSRRR LEEDLKKQAA EYREID KRM NSIKPDLIQL RKTRDQYLMW LTQKGVRQKK LNEWLGNENT EDQYSLVEDD EDLPHHDEKT WNVGSSNRNK AENLLRG KR DGTFLVRESS KQGCYACSVV VDGEVKHCVI NKTATGYGFA EPYNLYSSLK ELVLHYQHTS LVQHNDSLNV TLAYPVYA Q QRR UniProtKB: Phosphatidylinositol 3-kinase regulatory subunit alpha |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.35 mg/mL |
|---|---|
| 緩衝液 | pH: 7.5 |
| グリッド | モデル: UltrAuFoil R1.2/1.3 / 材質: GOLD / メッシュ: 300 / 支持フィルム - 材質: GOLD / 支持フィルム - トポロジー: HOLEY / 支持フィルム - Film thickness: 50 / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 90 sec. |
| 凍結 | 凍結剤: ETHANE |
| 詳細 | The sample was purified as a heterodimer and was monodisperse. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 100.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.0 µm / 最小 デフォーカス(公称値): 1.0 µm / 倍率(公称値): 105000 Bright-field microscopy / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.0 µm / 最小 デフォーカス(公称値): 1.0 µm / 倍率(公称値): 105000 |
| 特殊光学系 | エネルギーフィルター - 名称: GIF Bioquantum / エネルギーフィルター - スリット幅: 20 eV |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 撮影 | #0 - Image recording ID: 1 #0 - フィルム・検出器のモデル: GATAN K3 (6k x 4k) #0 - 検出モード: COUNTING / #0 - 撮影したグリッド数: 3 / #0 - 実像数: 6866 / #0 - 平均露光時間: 2.68 sec. / #0 - 平均電子線量: 60.0 e/Å2 #0 - 詳細: Grids were prepared with 0.02% CTAB. Images were collected in movie mode at 23 frames per second. #1 - Image recording ID: 2 #1 - フィルム・検出器のモデル: GATAN K3 (6k x 4k) #1 - 撮影したグリッド数: 1 / #1 - 実像数: 2058 / #1 - 平均露光時間: 2.68 sec. / #1 - 平均電子線量: 60.0 e/Å2 #1 - 詳細: Images were collected in movie mode at 23 frames per second. |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー






















 Z
Z Y
Y X
X