+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-2660 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of the Plasmodium falciparum 80S ribosome bound to the anti-protozoan drug emetine | |||||||||
 マップデータ マップデータ | Cryo-EM structure of the Plasmodium falciparum 80S ribosome bound to the anti-protozoan drug emetine | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード |  Plasmodium falciparum / Plasmodium falciparum /  80S ribosome / 80S ribosome /  Cryo-EM (低温電子顕微鏡法) / Cryo-EM (低温電子顕微鏡法) /  emetine (エメチン) emetine (エメチン) | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報RMTs methylate histone arginines /  Protein methylation / Translesion synthesis by REV1 / Translesion Synthesis by POLH / : / Translesion synthesis by POLK / Translesion synthesis by POLI / Josephin domain DUBs / : / Metalloprotease DUBs ...RMTs methylate histone arginines / Protein methylation / Translesion synthesis by REV1 / Translesion Synthesis by POLH / : / Translesion synthesis by POLK / Translesion synthesis by POLI / Josephin domain DUBs / : / Metalloprotease DUBs ...RMTs methylate histone arginines /  Protein methylation / Translesion synthesis by REV1 / Translesion Synthesis by POLH / : / Translesion synthesis by POLK / Translesion synthesis by POLI / Josephin domain DUBs / : / Metalloprotease DUBs / PTK6 Regulates RTKs and Their Effectors AKT1 and DOK1 / ER Quality Control Compartment (ERQC) / Iron uptake and transport / L13a-mediated translational silencing of Ceruloplasmin expression / SRP-dependent cotranslational protein targeting to membrane / Major pathway of rRNA processing in the nucleolus and cytosol / Formation of a pool of free 40S subunits / Formation of the ternary complex, and subsequently, the 43S complex / Ribosomal scanning and start codon recognition / GTP hydrolysis and joining of the 60S ribosomal subunit / Nonsense Mediated Decay (NMD) independent of the Exon Junction Complex (EJC) / Nonsense Mediated Decay (NMD) enhanced by the Exon Junction Complex (EJC) / Aggrephagy / Synthesis of active ubiquitin: roles of E1 and E2 enzymes / : / Orc1 removal from chromatin / CDK-mediated phosphorylation and removal of Cdc6 / KEAP1-NFE2L2 pathway / UCH proteinases / Ub-specific processing proteases / Protein methylation / Translesion synthesis by REV1 / Translesion Synthesis by POLH / : / Translesion synthesis by POLK / Translesion synthesis by POLI / Josephin domain DUBs / : / Metalloprotease DUBs / PTK6 Regulates RTKs and Their Effectors AKT1 and DOK1 / ER Quality Control Compartment (ERQC) / Iron uptake and transport / L13a-mediated translational silencing of Ceruloplasmin expression / SRP-dependent cotranslational protein targeting to membrane / Major pathway of rRNA processing in the nucleolus and cytosol / Formation of a pool of free 40S subunits / Formation of the ternary complex, and subsequently, the 43S complex / Ribosomal scanning and start codon recognition / GTP hydrolysis and joining of the 60S ribosomal subunit / Nonsense Mediated Decay (NMD) independent of the Exon Junction Complex (EJC) / Nonsense Mediated Decay (NMD) enhanced by the Exon Junction Complex (EJC) / Aggrephagy / Synthesis of active ubiquitin: roles of E1 and E2 enzymes / : / Orc1 removal from chromatin / CDK-mediated phosphorylation and removal of Cdc6 / KEAP1-NFE2L2 pathway / UCH proteinases / Ub-specific processing proteases /  Neddylation / Antigen processing: Ubiquitination & Proteasome degradation / endonucleolytic cleavage to generate mature 3'-end of SSU-rRNA from (SSU-rRNA, 5.8S rRNA, LSU-rRNA) / protein-RNA complex assembly / endonucleolytic cleavage in ITS1 to separate SSU-rRNA from 5.8S rRNA and LSU-rRNA from tricistronic rRNA transcript (SSU-rRNA, 5.8S rRNA, LSU-rRNA) / maturation of SSU-rRNA / maturation of SSU-rRNA from tricistronic rRNA transcript (SSU-rRNA, 5.8S rRNA, LSU-rRNA) / maturation of LSU-rRNA from tricistronic rRNA transcript (SSU-rRNA, 5.8S rRNA, LSU-rRNA) / maturation of LSU-rRNA / Neddylation / Antigen processing: Ubiquitination & Proteasome degradation / endonucleolytic cleavage to generate mature 3'-end of SSU-rRNA from (SSU-rRNA, 5.8S rRNA, LSU-rRNA) / protein-RNA complex assembly / endonucleolytic cleavage in ITS1 to separate SSU-rRNA from 5.8S rRNA and LSU-rRNA from tricistronic rRNA transcript (SSU-rRNA, 5.8S rRNA, LSU-rRNA) / maturation of SSU-rRNA / maturation of SSU-rRNA from tricistronic rRNA transcript (SSU-rRNA, 5.8S rRNA, LSU-rRNA) / maturation of LSU-rRNA from tricistronic rRNA transcript (SSU-rRNA, 5.8S rRNA, LSU-rRNA) / maturation of LSU-rRNA /  ribosomal large subunit biogenesis / small-subunit processome / modification-dependent protein catabolic process / mRNA 5'-UTR binding / ribosomal large subunit biogenesis / small-subunit processome / modification-dependent protein catabolic process / mRNA 5'-UTR binding /  ribosomal small subunit biogenesis / ribosomal small subunit biogenesis /  ribosomal large subunit assembly / small ribosomal subunit rRNA binding / ribosomal large subunit assembly / small ribosomal subunit rRNA binding /  protein tag activity / protein tag activity /  ribosomal small subunit assembly / rRNA processing / cytosolic small ribosomal subunit / large ribosomal subunit rRNA binding / large ribosomal subunit / ribosomal small subunit assembly / rRNA processing / cytosolic small ribosomal subunit / large ribosomal subunit rRNA binding / large ribosomal subunit /  リボソーム生合成 / cytoplasmic translation / small ribosomal subunit / リボソーム生合成 / cytoplasmic translation / small ribosomal subunit /  5S rRNA binding / cytosolic large ribosomal subunit / ubiquitin-dependent protein catabolic process / negative regulation of translation / 5S rRNA binding / cytosolic large ribosomal subunit / ubiquitin-dependent protein catabolic process / negative regulation of translation /  rRNA binding / protein ubiquitination / rRNA binding / protein ubiquitination /  リボソーム / structural constituent of ribosome / リボソーム / structural constituent of ribosome /  ribonucleoprotein complex / ribonucleoprotein complex /  翻訳 (生物学) / 翻訳 (生物学) /  mRNA binding / mRNA binding /  ubiquitin protein ligase binding / ubiquitin protein ligase binding /  核小体 / 核小体 /  ミトコンドリア / ミトコンドリア /  RNA binding / zinc ion binding / RNA binding / zinc ion binding /  metal ion binding / metal ion binding /  細胞核 / 細胞核 /  細胞質基質 / 細胞質基質 /  細胞質 細胞質類似検索 - 分子機能 | |||||||||
| 生物種 |   Plasmodium falciparum (マラリア病原虫) / synthetic construct (人工物) Plasmodium falciparum (マラリア病原虫) / synthetic construct (人工物) | |||||||||
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / クライオ電子顕微鏡法 /  ネガティブ染色法 / 解像度: 3.2 Å ネガティブ染色法 / 解像度: 3.2 Å | |||||||||
 データ登録者 データ登録者 | Wong W / Bai XC / Brown A / Fernandez IS / Hanssen E / Condron M / Tan YH / Baum J / Scheres SHW | |||||||||
 引用 引用 |  ジャーナル: Elife / 年: 2014 ジャーナル: Elife / 年: 2014タイトル: Cryo-EM structure of the Plasmodium falciparum 80S ribosome bound to the anti-protozoan drug emetine. 著者: Wilson Wong / Xiao-chen Bai / Alan Brown / Israel S Fernandez / Eric Hanssen / Melanie Condron / Yan Hong Tan / Jake Baum / Sjors H W Scheres /   要旨: Malaria inflicts an enormous burden on global human health. The emergence of parasite resistance to front-line drugs has prompted a renewed focus on the repositioning of clinically approved drugs as ...Malaria inflicts an enormous burden on global human health. The emergence of parasite resistance to front-line drugs has prompted a renewed focus on the repositioning of clinically approved drugs as potential anti-malarial therapies. Antibiotics that inhibit protein translation are promising candidates for repositioning. We have solved the cryo-EM structure of the cytoplasmic ribosome from the human malaria parasite, Plasmodium falciparum, in complex with emetine at 3.2 Å resolution. Emetine is an anti-protozoan drug used in the treatment of ameobiasis that also displays potent anti-malarial activity. Emetine interacts with the E-site of the ribosomal small subunit and shares a similar binding site with the antibiotic pactamycin, thereby delivering its therapeutic effect by blocking mRNA/tRNA translocation. As the first cryo-EM structure that visualizes an antibiotic bound to any ribosome at atomic resolution, this establishes cryo-EM as a powerful tool for screening and guiding the design of drugs that target parasite translation machinery. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_2660.map.gz emd_2660.map.gz | 166.7 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-2660-v30.xml emd-2660-v30.xml emd-2660.xml emd-2660.xml | 10.8 KB 10.8 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  cover_image_EMD2660.png cover_image_EMD2660.png | 344.1 KB | ||
| その他 |  run1_half1_class001_unfil.map run1_half1_class001_unfil.map run1_half2_class001_unfil.map run1_half2_class001_unfil.map | 178 MB 178 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-2660 http://ftp.pdbj.org/pub/emdb/structures/EMD-2660 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-2660 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-2660 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  3j79MC  3j7aMC  6okkMC  2661C M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | |
| 電子顕微鏡画像生データ |  EMPIAR-10028 (タイトル: Cryo-EM structure of the Plasmodium falciparum 80S ribosome bound to the anti-protozoan drug emetine EMPIAR-10028 (タイトル: Cryo-EM structure of the Plasmodium falciparum 80S ribosome bound to the anti-protozoan drug emetineData size: 1.2 TB Data #1: Unaligned multi-frame micrographs [micrographs - multiframe] Data #2: Frame averaged micrographs [micrographs - single frame] Data #3: Processed shiny particles [picked particles - multiframe - processed]) |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_2660.map.gz / 形式: CCP4 / 大きさ: 173.8 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_2660.map.gz / 形式: CCP4 / 大きさ: 173.8 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Cryo-EM structure of the Plasmodium falciparum 80S ribosome bound to the anti-protozoan drug emetine | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.34 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-添付マップデータ: run1 half1 class001 unfil.map
| ファイル | run1_half1_class001_unfil.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
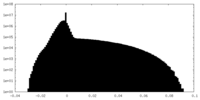
| 投影像・断面図 |
| ||||||||||||
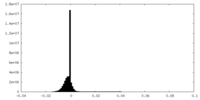
| 密度ヒストグラム |
-添付マップデータ: run1 half2 class001 unfil.map
| ファイル | run1_half2_class001_unfil.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
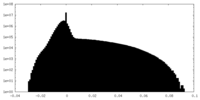
| 投影像・断面図 |
| ||||||||||||
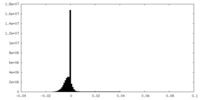
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Plasmodium falciparum 80S ribosome bound to the anti-protozoan dr...
| 全体 | 名称: Plasmodium falciparum 80S ribosome bound to the anti-protozoan drug emetine |
|---|---|
| 要素 |
|
-超分子 #1000: Plasmodium falciparum 80S ribosome bound to the anti-protozoan dr...
| 超分子 | 名称: Plasmodium falciparum 80S ribosome bound to the anti-protozoan drug emetine タイプ: sample / ID: 1000 / Number unique components: 2 |
|---|---|
| 分子量 | 実験値: 4.2 MDa / 理論値: 4.2 MDa |
-超分子 #1: Plasmodium falciparum 80S ribosome bound to the anti- protozoan d...
| 超分子 | 名称: Plasmodium falciparum 80S ribosome bound to the anti- protozoan drug emetine タイプ: complex / ID: 1 詳細: the anti-protozoan drug emetine was bound to the Plasmodium falciparum 80S ribosome 組換発現: No / Ribosome-details: ribosome-eukaryote: ALL |
|---|---|
| 由来(天然) | 生物種:   Plasmodium falciparum (マラリア病原虫) Plasmodium falciparum (マラリア病原虫) |
| 分子量 | 実験値: 4.2 MDa / 理論値: 4.2 MDa |
-分子 #1: emetine
| 分子 | 名称: emetine / タイプ: ligand / ID: 1 / 組換発現: No |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| Chemical component information |  ChemComp-34G: |
-実験情報
-構造解析
| 手法 |  ネガティブ染色法, ネガティブ染色法,  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.6 mg/mL |
|---|---|
| 緩衝液 | pH: 7.4 詳細: 20 mM Hepes pH7.4, 40 mM KCH3COO, 10 mM NH4CH3COO, 10 mM Mg(CH3COO)2 and 5 mM 2-mecaptoethanol |
| 染色 | タイプ: NEGATIVE / 詳細: cryo-EM |
| グリッド | 詳細: 30 s on glow-discharged holey carbon grids (Quantifoil R2/2), onto which a home-made continuous carbon film |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 90 K / 装置: FEI VITROBOT MARK IV / 手法: Blot 2.5 seconds before plunging |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI POLARA 300 |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 倍率(補正後): 104748 / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / Cs: 2 mm / 最大 デフォーカス(公称値): 3.8 µm / 最小 デフォーカス(公称値): 0.8 µm / 倍率(公称値): 78000 Bright-field microscopy / Cs: 2 mm / 最大 デフォーカス(公称値): 3.8 µm / 最小 デフォーカス(公称値): 0.8 µm / 倍率(公称値): 78000 |
| 試料ステージ | 試料ホルダーモデル: GATAN LIQUID NITROGEN |
| 温度 | 最低: 80 K / 最高: 90 K / 平均: 85 K |
| アライメント法 | Legacy - 非点収差: Objective lens astigmatism was corrected at 78,000 times magnification |
| 日付 | 2014年1月19日 |
| 撮影 | カテゴリ: CCD フィルム・検出器のモデル: FEI FALCON II (4k x 4k) デジタル化 - サンプリング間隔: 14 µm / 実像数: 1083 / 平均電子線量: 20 e/Å2 詳細: Use a newly developed statistical movie processing approach to compensate for beam-induced movement. |
| 実験機器 |  モデル: Tecnai Polara / 画像提供: FEI Company |
- 画像解析
画像解析
| CTF補正 | 詳細: Each particle |
|---|---|
| 最終 再構成 | 想定した対称性 - 点群: C1 (非対称) / 解像度のタイプ: BY AUTHOR / 解像度: 3.2 Å / 解像度の算出法: OTHER / ソフトウェア - 名称: CTFFIND3, RELION 詳細: Use a newly developed statistical movie processing approach to compensate for beam-induced movement. 使用した粒子像数: 105247 |
| 詳細 | Use a newly developed statistical movie processing approach to compensate for beam-induced movement. |
 ムービー
ムービー コントローラー
コントローラー


















 Z
Z Y
Y X
X