+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-20589 | ||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | CryoEM reconstruction of membrane-bound ESCRT-III filament composed of CHMP1B+IST1 (left-handed) | ||||||||||||||||||
 マップデータ マップデータ | RELION postprocessed map with helical symmetry applied to the entire map | ||||||||||||||||||
 試料 試料 |
| ||||||||||||||||||
 キーワード キーワード | membrane remodeling /  membrane-bound protein filament (生体膜) / membrane-bound protein filament (生体膜) /  ESCRT-III (ESCRT) / LIPID BINDING PROTEIN ESCRT-III (ESCRT) / LIPID BINDING PROTEIN | ||||||||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報viral capsid secondary envelopment / MIT domain binding /  abscission / amphisome membrane / multivesicular body-lysosome fusion / vesicle fusion with vacuole / ESCRT III complex disassembly / late endosome to lysosome transport / abscission / amphisome membrane / multivesicular body-lysosome fusion / vesicle fusion with vacuole / ESCRT III complex disassembly / late endosome to lysosome transport /  ESCRT III complex / kinetochore microtubule ...viral capsid secondary envelopment / MIT domain binding / ESCRT III complex / kinetochore microtubule ...viral capsid secondary envelopment / MIT domain binding /  abscission / amphisome membrane / multivesicular body-lysosome fusion / vesicle fusion with vacuole / ESCRT III complex disassembly / late endosome to lysosome transport / abscission / amphisome membrane / multivesicular body-lysosome fusion / vesicle fusion with vacuole / ESCRT III complex disassembly / late endosome to lysosome transport /  ESCRT III complex / kinetochore microtubule / cytoskeleton-dependent cytokinesis / endosome transport via multivesicular body sorting pathway / collateral sprouting / regulation of centrosome duplication / nuclear membrane reassembly / Sealing of the nuclear envelope (NE) by ESCRT-III / positive regulation of collateral sprouting / midbody abscission / multivesicular body sorting pathway / membrane fission / plasma membrane repair / membrane coat / late endosome to vacuole transport / multivesicular body membrane / ubiquitin-dependent protein catabolic process via the multivesicular body sorting pathway / ESCRT III complex / kinetochore microtubule / cytoskeleton-dependent cytokinesis / endosome transport via multivesicular body sorting pathway / collateral sprouting / regulation of centrosome duplication / nuclear membrane reassembly / Sealing of the nuclear envelope (NE) by ESCRT-III / positive regulation of collateral sprouting / midbody abscission / multivesicular body sorting pathway / membrane fission / plasma membrane repair / membrane coat / late endosome to vacuole transport / multivesicular body membrane / ubiquitin-dependent protein catabolic process via the multivesicular body sorting pathway /  multivesicular body assembly / multivesicular body assembly /  regulation of mitotic spindle assembly / Flemming body / regulation of mitotic spindle assembly / Flemming body /  nucleus organization / mitotic metaphase chromosome alignment / viral budding via host ESCRT complex / autophagosome maturation / autophagosome membrane / positive regulation of proteolysis / nucleus organization / mitotic metaphase chromosome alignment / viral budding via host ESCRT complex / autophagosome maturation / autophagosome membrane / positive regulation of proteolysis /  endoplasmic reticulum-Golgi intermediate compartment / viral release from host cell / endoplasmic reticulum-Golgi intermediate compartment / viral release from host cell /  核膜孔 / 核膜孔 /  エンドソーム / エンドソーム /  viral budding from plasma membrane / establishment of protein localization / viral budding from plasma membrane / establishment of protein localization /  protein localization / protein localization /  動原体 / 動原体 /  オートファジー / azurophil granule lumen / オートファジー / azurophil granule lumen /  protein transport / protein transport /  核膜 / midbody / endosome membrane / 核膜 / midbody / endosome membrane /  cadherin binding / lysosomal membrane / cadherin binding / lysosomal membrane /  細胞分裂 / protein domain specific binding / intracellular membrane-bounded organelle / 細胞分裂 / protein domain specific binding / intracellular membrane-bounded organelle /  中心体 / 中心体 /  クロマチン / Neutrophil degranulation / protein-containing complex binding / extracellular exosome / extracellular region / クロマチン / Neutrophil degranulation / protein-containing complex binding / extracellular exosome / extracellular region /  核質 / identical protein binding / 核質 / identical protein binding /  細胞膜 / 細胞膜 /  細胞質基質 細胞質基質類似検索 - 分子機能 | ||||||||||||||||||
| 生物種 |   Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||||||||||||||
| 手法 | らせん対称体再構成法 /  クライオ電子顕微鏡法 / 解像度: 3.1 Å クライオ電子顕微鏡法 / 解像度: 3.1 Å | ||||||||||||||||||
 データ登録者 データ登録者 | Nguyen HC / Frost A | ||||||||||||||||||
| 資金援助 |  米国, 5件 米国, 5件
| ||||||||||||||||||
 引用 引用 |  ジャーナル: Nat Struct Mol Biol / 年: 2020 ジャーナル: Nat Struct Mol Biol / 年: 2020タイトル: Membrane constriction and thinning by sequential ESCRT-III polymerization. 著者: Henry C Nguyen / Nathaniel Talledge / John McCullough / Abhimanyu Sharma / Frank R Moss / Janet H Iwasa / Michael D Vershinin / Wesley I Sundquist / Adam Frost /  要旨: The endosomal sorting complexes required for transport (ESCRTs) mediate diverse membrane remodeling events. These typically require ESCRT-III proteins to stabilize negatively curved membranes; ...The endosomal sorting complexes required for transport (ESCRTs) mediate diverse membrane remodeling events. These typically require ESCRT-III proteins to stabilize negatively curved membranes; however, recent work has indicated that certain ESCRT-IIIs also participate in positive-curvature membrane-shaping reactions. ESCRT-IIIs polymerize into membrane-binding filaments, but the structural basis for negative versus positive membrane remodeling by these proteins remains poorly understood. To learn how certain ESCRT-IIIs shape positively curved membranes, we determined structures of human membrane-bound CHMP1B-only, membrane-bound CHMP1B + IST1, and IST1-only filaments by cryo-EM. Our structures show how CHMP1B first polymerizes into a single-stranded helical filament, shaping membranes into moderate-curvature tubules. Subsequently, IST1 assembles a second strand on CHMP1B, further constricting the membrane tube and reducing its diameter nearly to the fission point. Each step of constriction thins the underlying bilayer, lowering the barrier to membrane fission. Our structures reveal how a two-component, sequential polymerization mechanism drives membrane tubulation, constriction and bilayer thinning. | ||||||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_20589.map.gz emd_20589.map.gz | 40.2 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-20589-v30.xml emd-20589-v30.xml emd-20589.xml emd-20589.xml | 26.4 KB 26.4 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_20589_fsc.xml emd_20589_fsc.xml | 12.5 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_20589.png emd_20589.png | 57.5 KB | ||
| マスクデータ |  emd_20589_msk_1.map emd_20589_msk_1.map | 166.4 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-20589.cif.gz emd-20589.cif.gz | 6.2 KB | ||
| その他 |  emd_20589_additional_1.map.gz emd_20589_additional_1.map.gz emd_20589_additional_2.map.gz emd_20589_additional_2.map.gz emd_20589_additional_3.map.gz emd_20589_additional_3.map.gz emd_20589_additional_4.map.gz emd_20589_additional_4.map.gz emd_20589_half_map_1.map.gz emd_20589_half_map_1.map.gz emd_20589_half_map_2.map.gz emd_20589_half_map_2.map.gz | 131.8 MB 131.6 MB 131.7 MB 131.6 MB 131.6 MB 131.7 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-20589 http://ftp.pdbj.org/pub/emdb/structures/EMD-20589 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-20589 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-20589 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  6tz5MC  6tz4C  6tz9C  6tzaC C: 同じ文献を引用 ( M: このマップから作成された原子モデル |
|---|---|
| 類似構造データ | |
| 電子顕微鏡画像生データ |  EMPIAR-10395 (タイトル: Helical Reconstruction of a left-handed and membrnae-bound ESCRT-III copolymer comprised of human CHMP1B and IST1 EMPIAR-10395 (タイトル: Helical Reconstruction of a left-handed and membrnae-bound ESCRT-III copolymer comprised of human CHMP1B and IST1Data size: 26.8 Data #1: copolymer_LH_job1415.mrcs [picked particles - multiframe - processed]) |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_20589.map.gz / 形式: CCP4 / 大きさ: 166.4 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_20589.map.gz / 形式: CCP4 / 大きさ: 166.4 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | RELION postprocessed map with helical symmetry applied to the entire map | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.22 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
| ファイル |  emd_20589_msk_1.map emd_20589_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
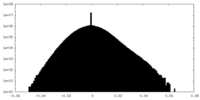
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: RELION Refine3D filtered map with no symmetry applied (C1 map)
| ファイル | emd_20589_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | RELION Refine3D filtered map with no symmetry applied (C1 map) | ||||||||||||
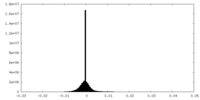
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: RELION Refine3D filtered map with no symmetry applied (C1 map)
| ファイル | emd_20589_additional_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | RELION Refine3D filtered map with no symmetry applied (C1 map) | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: RELION Refine3D unfiltered half map1 with no symmetry...
| ファイル | emd_20589_additional_3.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | RELION Refine3D unfiltered half map1 with no symmetry applied (C1 half1 map) | ||||||||||||
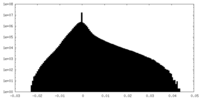
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: RELION Refine3D unfiltered half map2 with no symmetry...
| ファイル | emd_20589_additional_4.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | RELION Refine3D unfiltered half map2 with no symmetry applied (C1 half2 map) | ||||||||||||
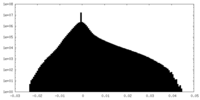
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: RELION Refine3D unfiltered half map1 with helical symmetry...
| ファイル | emd_20589_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | RELION Refine3D unfiltered half map1 with helical symmetry imposed on the central 40% | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: RELION Refine3D unfiltered half map2 with helical symmetry...
| ファイル | emd_20589_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | RELION Refine3D unfiltered half map2 with helical symmetry imposed on the central 40% | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : membrane-bound ESCRT-III copolymer filament composed of CHMP1B an...
| 全体 | 名称: membrane-bound ESCRT-III copolymer filament composed of CHMP1B and IST1 |
|---|---|
| 要素 |
|
-超分子 #1: membrane-bound ESCRT-III copolymer filament composed of CHMP1B an...
| 超分子 | 名称: membrane-bound ESCRT-III copolymer filament composed of CHMP1B and IST1 タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
-分子 #1: Charged multivesicular body protein 1b
| 分子 | 名称: Charged multivesicular body protein 1b / タイプ: protein_or_peptide / ID: 1 / コピー数: 34 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 22.140354 KDa |
| 組換発現 | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 配列 | 文字列: MSNMEKHLFN LKFAAKELSR SAKKCDKEEK AEKAKIEKAI QKGNMEVARI HAENAIRQKN QAVNFLRMSA RVDAVAARVQ TAVTMGKVT KSMAGVVKSM DATLKTMNLE KISALMDKFE HQFETLDVQT QQMEDTMSST TTLTTPQNQV DMLLQEMADE A GLDLNMEL ...文字列: MSNMEKHLFN LKFAAKELSR SAKKCDKEEK AEKAKIEKAI QKGNMEVARI HAENAIRQKN QAVNFLRMSA RVDAVAARVQ TAVTMGKVT KSMAGVVKSM DATLKTMNLE KISALMDKFE HQFETLDVQT QQMEDTMSST TTLTTPQNQV DMLLQEMADE A GLDLNMEL PQGQTGSVGT SVASAEQDEL SQRLARLRDQ V UniProtKB: Charged multivesicular body protein 1b |
-分子 #2: IST1 homolog
| 分子 | 名称: IST1 homolog / タイプ: protein_or_peptide / ID: 2 / コピー数: 34 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 21.574281 KDa |
| 組換発現 | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 配列 | 文字列: MLGSGFKAER LRVNLRLVIN RLKLLEKKKT ELAQKARKEI ADYLAAGKDE RARIRVEHII REDYLVEAME ILELYCDLLL ARFGLIQSM KELDSGLAES VSTLIWAAPR LQSEVAELKI VADQLCAKYS KEYGKLCRTN QIGTVNDRLM HKLSVEAPPK I LVERYLIE ...文字列: MLGSGFKAER LRVNLRLVIN RLKLLEKKKT ELAQKARKEI ADYLAAGKDE RARIRVEHII REDYLVEAME ILELYCDLLL ARFGLIQSM KELDSGLAES VSTLIWAAPR LQSEVAELKI VADQLCAKYS KEYGKLCRTN QIGTVNDRLM HKLSVEAPPK I LVERYLIE IAKNYNVPYE PDSVVMAEAP P UniProtKB: IST1 homolog |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | らせん対称体再構成法 |
| 試料の集合状態 | helical array |
- 試料調製
試料調製
| 緩衝液 | pH: 7.4 |
|---|---|
| グリッド | 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 30 sec. / 詳細: unspecified |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 292 K / 装置: FEI VITROBOT MARK III 詳細: Grids were blotted with Whatman No. 1 filter paper for 4-8 seconds with a 0 mm offset at 19C and 100 percent humidity before plunging into liquid ethane. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI POLARA 300 |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy Bright-field microscopy |
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: SUPER-RESOLUTION / 平均電子線量: 44.0 e/Å2 |
| 実験機器 |  モデル: Tecnai Polara / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー











 Z
Z Y
Y X
X