+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-1893 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
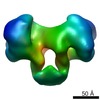
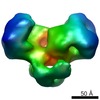
| タイトル | EcoKI Type I DNA restriction-modification enzyme complex in closed state with bound 75bp cognate DNA fragment. 3D reconstruction by single particle analysis from negative stain EM. | |||||||||
 マップデータ マップデータ | 3D reconstruction of EcoKI Type I restriction-modification enzyme with DNA fragment, from negative stain EM data. | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | EcoKI /  endonuclease (エンドヌクレアーゼ) / endonuclease (エンドヌクレアーゼ) /  methyltransferase (メチルトランスフェラーゼ) / type I restriction / methyltransferase (メチルトランスフェラーゼ) / type I restriction /  DNA (デオキシリボ核酸) / DNA (デオキシリボ核酸) /  HsdS (倚天屠龍記) / HsdM / HsdR / HsdS (倚天屠龍記) / HsdM / HsdR /  electron microscopy (電子顕微鏡) / electron microscopy (電子顕微鏡) /  negative stain / negative stain /  translocase (輸送酵素) / DEAD-box / translocase (輸送酵素) / DEAD-box /  ATPase (ATPアーゼ) ATPase (ATPアーゼ) | |||||||||
| 機能・相同性 | Type I restriction modification DNA specificity domain /  Restriction endonuclease, type I, HsdR / Restriction endonuclease, type I, HsdR /  protein binding / DNA methylase, adenine-specific / DNA restriction-modification system protein binding / DNA methylase, adenine-specific / DNA restriction-modification system 機能・相同性情報 機能・相同性情報 | |||||||||
| 生物種 |   Escherichia coli (大腸菌) / synthetic construct (人工物) Escherichia coli (大腸菌) / synthetic construct (人工物) | |||||||||
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  ネガティブ染色法 / 解像度: 20.0 Å ネガティブ染色法 / 解像度: 20.0 Å | |||||||||
 データ登録者 データ登録者 | Kennaway CK / Taylor JE / Song CF / Potrzebowski W / White JH / Swiderska A / Obarska-Kosinska A / Callow P / Cooper LP / Roberts GA ...Kennaway CK / Taylor JE / Song CF / Potrzebowski W / White JH / Swiderska A / Obarska-Kosinska A / Callow P / Cooper LP / Roberts GA / Bujnicki JM / Trinick J / Kneale GG / Dryden DTF | |||||||||
 引用 引用 |  ジャーナル: Genes Dev / 年: 2012 ジャーナル: Genes Dev / 年: 2012タイトル: Structure and operation of the DNA-translocating type I DNA restriction enzymes. 著者: Christopher K Kennaway / James E N Taylor / Chun Feng Song / Wojciech Potrzebowski / William Nicholson / John H White / Anna Swiderska / Agnieszka Obarska-Kosinska / Philip Callow / Laurie P ...著者: Christopher K Kennaway / James E N Taylor / Chun Feng Song / Wojciech Potrzebowski / William Nicholson / John H White / Anna Swiderska / Agnieszka Obarska-Kosinska / Philip Callow / Laurie P Cooper / Gareth A Roberts / Jean-Baptiste Artero / Janusz M Bujnicki / John Trinick / G Geoff Kneale / David T F Dryden /    要旨: Type I DNA restriction/modification (RM) enzymes are molecular machines found in the majority of bacterial species. Their early discovery paved the way for the development of genetic engineering. ...Type I DNA restriction/modification (RM) enzymes are molecular machines found in the majority of bacterial species. Their early discovery paved the way for the development of genetic engineering. They control (restrict) the influx of foreign DNA via horizontal gene transfer into the bacterium while maintaining sequence-specific methylation (modification) of host DNA. The endonuclease reaction of these enzymes on unmethylated DNA is preceded by bidirectional translocation of thousands of base pairs of DNA toward the enzyme. We present the structures of two type I RM enzymes, EcoKI and EcoR124I, derived using electron microscopy (EM), small-angle scattering (neutron and X-ray), and detailed molecular modeling. DNA binding triggers a large contraction of the open form of the enzyme to a compact form. The path followed by DNA through the complexes is revealed by using a DNA mimic anti-restriction protein. The structures reveal an evolutionary link between type I RM enzymes and type II RM enzymes. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_1893.map.gz emd_1893.map.gz | 80.6 KB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-1893-v30.xml emd-1893-v30.xml emd-1893.xml emd-1893.xml | 14.4 KB 14.4 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  1893.png 1893.png | 154.9 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-1893 http://ftp.pdbj.org/pub/emdb/structures/EMD-1893 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-1893 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-1893 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_1893.map.gz / 形式: CCP4 / 大きさ: 422.9 KB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_1893.map.gz / 形式: CCP4 / 大きさ: 422.9 KB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | 3D reconstruction of EcoKI Type I restriction-modification enzyme with DNA fragment, from negative stain EM data. | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 5.27 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : EcoKI R2 M2 S1 complex with 75 bp cognate dsDNA fragment
| 全体 | 名称: EcoKI R2 M2 S1 complex with 75 bp cognate dsDNA fragment |
|---|---|
| 要素 |
|
-超分子 #1000: EcoKI R2 M2 S1 complex with 75 bp cognate dsDNA fragment
| 超分子 | 名称: EcoKI R2 M2 S1 complex with 75 bp cognate dsDNA fragment タイプ: sample / ID: 1000 / 詳細: Stained with uranyl acetate / 集合状態: 1x HsdS, 2x HsdM, 2x HsdR, 1x dsDNA / Number unique components: 4 |
|---|---|
| 分子量 | 実験値: 420 KDa / 理論値: 440 KDa / 手法: Small angle X-ray scattering (SAXS) |
-分子 #1: EcoKI HsdS specificity subunit
| 分子 | 名称: EcoKI HsdS specificity subunit / タイプ: protein_or_peptide / ID: 1 / Name.synonym: HsdS / コピー数: 1 / 集合状態: Monomer / 組換発現: No |
|---|---|
| 由来(天然) | 生物種:   Escherichia coli (大腸菌) / 株: R / 細胞中の位置: Cytoplasm Escherichia coli (大腸菌) / 株: R / 細胞中の位置: Cytoplasm |
| 分子量 | 理論値: 50 KDa |
| 配列 | GO:  protein binding protein bindingInterPro: Type I restriction modification DNA specificity domain |
-分子 #2: EcoKI HsdM methyltransferase subunit
| 分子 | 名称: EcoKI HsdM methyltransferase subunit / タイプ: protein_or_peptide / ID: 2 / Name.synonym: HsdM / コピー数: 2 / 集合状態: Dimer / 組換発現: No |
|---|---|
| 由来(天然) | 生物種:   Escherichia coli (大腸菌) / 株: R / 細胞中の位置: cytoplasm Escherichia coli (大腸菌) / 株: R / 細胞中の位置: cytoplasm |
| 分子量 | 理論値: 59 KDa |
| 配列 | GO:  protein binding / InterPro: DNA methylase, adenine-specific protein binding / InterPro: DNA methylase, adenine-specific |
-分子 #3: EcoKI HsdR endonuclease subunit
| 分子 | 名称: EcoKI HsdR endonuclease subunit / タイプ: protein_or_peptide / ID: 3 / Name.synonym: HsdR / コピー数: 2 / 集合状態: Monomer / 組換発現: No |
|---|---|
| 由来(天然) | 生物種:   Escherichia coli (大腸菌) / 株: R Escherichia coli (大腸菌) / 株: R |
| 分子量 | 理論値: 120 KDa |
| 配列 | GO: DNA restriction-modification system / InterPro:  Restriction endonuclease, type I, HsdR Restriction endonuclease, type I, HsdR |
-分子 #4: Deoxyribonucleic acid
| 分子 | 名称: Deoxyribonucleic acid / タイプ: dna / ID: 4 / Name.synonym: DNA / 分類: DNA / Structure: DOUBLE HELIX / Synthetic?: Yes |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 15 KDa |
| 配列 | 文字列: AACNNNNNNG TGC |
-実験情報
-構造解析
| 手法 |  ネガティブ染色法 ネガティブ染色法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.050 mg/mL |
|---|---|
| 緩衝液 | pH: 4.7 / 詳細: 20mM Tris-Cl, 100 mM NaCl |
| 染色 | タイプ: NEGATIVE 詳細: Protein was adsorbed onto UV treated carbon for 1 minute, blotted, then 1% uranyl acetate solution was applied for 1 min then blotted, three times. |
| グリッド | 詳細: 400 mesh copper with continuous carbon |
| 凍結 | 凍結剤: NONE / 装置: OTHER / 詳細: Negative stain |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | JEOL 1200EXII |
|---|---|
| 電子線 | 加速電圧: 80 kV / 電子線源: TUNGSTEN HAIRPIN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / Cs: 2.0 mm / 最大 デフォーカス(公称値): 0.9 µm / 最小 デフォーカス(公称値): 0.4 µm / 倍率(公称値): 40000 Bright-field microscopy / Cs: 2.0 mm / 最大 デフォーカス(公称値): 0.9 µm / 最小 デフォーカス(公称値): 0.4 µm / 倍率(公称値): 40000 |
| 試料ステージ | 試料ホルダー: Side entry / 試料ホルダーモデル: JEOL |
| 温度 | 平均: 294 K |
| アライメント法 | Legacy - 非点収差: Corrected at 80,000x |
| 詳細 | Customised JEOL 1200 EX microscope, low dose mode. |
| 日付 | 2004年7月1日 |
| 撮影 | カテゴリ: FILM / フィルム・検出器のモデル: KODAK SO-163 FILM / デジタル化 - スキャナー: OTHER / デジタル化 - サンプリング間隔: 20 µm / 実像数: 50 / 平均電子線量: 40 e/Å2 / 詳細: Scanned on Imacon scanner / ビット/ピクセル: 8 |
- 画像解析
画像解析
| CTF補正 | 詳細: Filtered at 1st zero |
|---|---|
| 最終 2次元分類 | クラス数: 100 |
| 最終 角度割当 | 詳細: full range, C2 symmetry |
| 最終 再構成 | 想定した対称性 - 点群: C2 (2回回転対称 ) / アルゴリズム: OTHER / 解像度のタイプ: BY AUTHOR / 解像度: 20.0 Å / 解像度の算出法: FSC 0.5 CUT-OFF / ソフトウェア - 名称: EMAN, IMAGIC, Spider, XMIPP ) / アルゴリズム: OTHER / 解像度のタイプ: BY AUTHOR / 解像度: 20.0 Å / 解像度の算出法: FSC 0.5 CUT-OFF / ソフトウェア - 名称: EMAN, IMAGIC, Spider, XMIPP詳細: Final rounds of refinement done in EMAN using selected input classes. 使用した粒子像数: 5786 |
| 詳細 | The particles were manually selected using boxer. |
-原子モデル構築 1
| 初期モデル | PDB ID: Chain - Chain ID: A |
|---|---|
| ソフトウェア | 名称:  Chimera Chimera |
| 詳細 | PDBEntryID_givenInChain. Protocol: rigid body. Homology model based on HsdR from EcoR124 (2W00) was fitted into the density after the core methylase (HsdS and 2x HsdM) was fitted. |
| 精密化 | 空間: RECIPROCAL / プロトコル: RIGID BODY FIT / 当てはまり具合の基準: cross-correlation |
 ムービー
ムービー コントローラー
コントローラー