+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
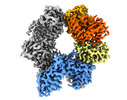
| タイトル | Human SLFN11 dimer bound to ssDNA | |||||||||
 マップデータ マップデータ | sharpened map | |||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報replication fork arrest /  加水分解酵素; 酸無水物に作用 / negative regulation of G1/S transition of mitotic cell cycle / 加水分解酵素; 酸無水物に作用 / negative regulation of G1/S transition of mitotic cell cycle /  immune system process / negative regulation of DNA replication / site of DNA damage / immune system process / negative regulation of DNA replication / site of DNA damage /  helicase activity / defense response to virus / helicase activity / defense response to virus /  tRNA binding / tRNA binding /  クロマチンリモデリング ...replication fork arrest / クロマチンリモデリング ...replication fork arrest /  加水分解酵素; 酸無水物に作用 / negative regulation of G1/S transition of mitotic cell cycle / 加水分解酵素; 酸無水物に作用 / negative regulation of G1/S transition of mitotic cell cycle /  immune system process / negative regulation of DNA replication / site of DNA damage / immune system process / negative regulation of DNA replication / site of DNA damage /  helicase activity / defense response to virus / helicase activity / defense response to virus /  tRNA binding / tRNA binding /  クロマチンリモデリング / DNA damage response / クロマチンリモデリング / DNA damage response /  ATP hydrolysis activity / ATP hydrolysis activity /  核質 / 核質 /  ATP binding / ATP binding /  細胞核 / 細胞核 /  細胞質基質 細胞質基質類似検索 - 分子機能 | |||||||||
| 生物種 |   Homo sapiens (ヒト) / synthetic construct (人工物) Homo sapiens (ヒト) / synthetic construct (人工物) | |||||||||
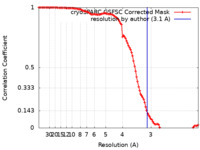
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 3.1 Å クライオ電子顕微鏡法 / 解像度: 3.1 Å | |||||||||
 データ登録者 データ登録者 | Metzner FJ / Kugler M / Wenzl SJ / Lammens K | |||||||||
| 資金援助 |  ドイツ, European Union, 2件 ドイツ, European Union, 2件
| |||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2022 ジャーナル: Nat Commun / 年: 2022タイトル: Mechanistic understanding of human SLFN11. 著者: Felix J Metzner / Simon J Wenzl / Michael Kugler / Stefan Krebs / Karl-Peter Hopfner / Katja Lammens /  要旨: Schlafen 11 (SLFN11) is an interferon-inducible antiviral restriction factor with tRNA endoribonuclease and DNA binding functions. It is recruited to stalled replication forks in response to ...Schlafen 11 (SLFN11) is an interferon-inducible antiviral restriction factor with tRNA endoribonuclease and DNA binding functions. It is recruited to stalled replication forks in response to replication stress and inhibits replication of certain viruses such as the human immunodeficiency virus 1 (HIV-1) by modulating the tRNA pool. SLFN11 has been identified as a predictive biomarker in cancer, as its expression correlates with a beneficial response to DNA damage inducing anticancer drugs. However, the mechanism and interdependence of these two functions are largely unknown. Here, we present cryo-electron microscopy (cryo-EM) structures of human SLFN11 in its dimeric apoenzyme state, bound to tRNA and in complex with single-strand DNA. Full-length SLFN11 neither hydrolyses nor binds ATP and the helicase domain appears in an autoinhibited state. Together with biochemical and structure guided mutagenesis studies, our data give detailed insights into the mechanism of endoribonuclease activity as well as suggestions on how SLFN11 may block stressed replication forks. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_14692.map.gz emd_14692.map.gz | 117.8 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-14692-v30.xml emd-14692-v30.xml emd-14692.xml emd-14692.xml | 17.3 KB 17.3 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_14692_fsc.xml emd_14692_fsc.xml | 10.6 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_14692.png emd_14692.png | 115.5 KB | ||
| マスクデータ |  emd_14692_msk_1.map emd_14692_msk_1.map | 125 MB |  マスクマップ マスクマップ | |
| その他 |  emd_14692_half_map_1.map.gz emd_14692_half_map_1.map.gz emd_14692_half_map_2.map.gz emd_14692_half_map_2.map.gz | 115.9 MB 115.9 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-14692 http://ftp.pdbj.org/pub/emdb/structures/EMD-14692 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-14692 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-14692 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  7zesMC  7zelC  7zepC C: 同じ文献を引用 ( M: このマップから作成された原子モデル |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_14692.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_14692.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | sharpened map | ||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.046 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_14692_msk_1.map emd_14692_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: half map A
| ファイル | emd_14692_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | half map A | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: half map B
| ファイル | emd_14692_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | half map B | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : SLFN11 dimer bound to ssDNA
| 全体 | 名称: SLFN11 dimer bound to ssDNA |
|---|---|
| 要素 |
|
-超分子 #1: SLFN11 dimer bound to ssDNA
| 超分子 | 名称: SLFN11 dimer bound to ssDNA / タイプ: organelle_or_cellular_component / ID: 1 / 親要素: 0 / 含まれる分子: #1-#2 |
|---|
-超分子 #2: Schlafen family member 11
| 超分子 | 名称: Schlafen family member 11 / タイプ: complex / ID: 2 / 親要素: 1 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 組換発現 | 生物種:   Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
-超分子 #3: DNA (5'-D(P*CP*GP*CP*GP*T)-3')
| 超分子 | 名称: DNA (5'-D(P*CP*GP*CP*GP*T)-3') / タイプ: complex / ID: 3 / 親要素: 1 / 含まれる分子: #2 |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
-分子 #1: Schlafen family member 11
| 分子 | 名称: Schlafen family member 11 / タイプ: protein_or_peptide / ID: 1 / コピー数: 2 / 光学異性体: LEVO / EC番号:  加水分解酵素; 酸無水物に作用 加水分解酵素; 酸無水物に作用 |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 106.207914 KDa |
| 組換発現 | 生物種:   Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: MADYKDDDDK GTDYKDDDDK LEVLFQGPME ANQCPLVVEP SYPDLVINVG EVTLGEENRK KLQKIQRDQE KERVMRAACA LLNSGGGVI RMAKKVEHPV EMGLDLEQSL RELIQSSDLQ AFFETKQQGR CFYIFVKSWS SGPFPEDRSV KPRLCSLSSS L YRRSETSV ...文字列: MADYKDDDDK GTDYKDDDDK LEVLFQGPME ANQCPLVVEP SYPDLVINVG EVTLGEENRK KLQKIQRDQE KERVMRAACA LLNSGGGVI RMAKKVEHPV EMGLDLEQSL RELIQSSDLQ AFFETKQQGR CFYIFVKSWS SGPFPEDRSV KPRLCSLSSS L YRRSETSV RSMDSREAFC FLKTKRKPKI LEEGPFHKIH KGVYQELPNS DPADPNSDPA DLIFQKDYLE YGEILPFPES QL VEFKQFS TKHFQEYVKR TIPEYVPAFA NTGGGYLFIG VDDKSREVLG CAKENVDPDS LRRKIEQAIY KLPCVHFCQP QRP ITFTLK IVNVLKRGEL YGYACMIRVN PFCCAVFSEA PNSWIVEDKY VCSLTTEKWV GMMTDTDPDL LQLSEDFECQ LSLS SGPPL SRPVYSKKGL EHKKELQQLL FSVPPGYLRY TPESLWRDLI SEHRGLEELI NKQMQPFFRG ILIFSRSWAV DLNLQ EKPG VICDALLIAQ NSTPILYTIL REQDAEGQDY CTRTAFTLKQ KLVNMGGYTG KVCVRAKVLC LSPESSAEAL EAAVSP MDY PASYSLAGTQ HMEALLQSLV IVLLGFRSLL SDQLGCEVLN LLTAQQYEIF SRSLRKNREL FVHGLPGSGK TIMAMKI ME KIRNVFHCEA HRILYVCENQ PLRNFISDRN ICRAETRKTF LRENFEHIQH IVIDEAQNFR TEDGDWYGKA KSITRRAK G GPGILWIFLD YFQTSHLDCS GLPPLSDQYP REELTRIVRN ADPIAKYLQK EMQVIRSNPS FNIPTGCLEV FPEAEWSQG VQGTLRIKKY LTVEQIMTCV ADTCRRFFDR GYSPKDVAVL VSTAKEVEHY KYELLKAMRK KRVVQLSDAC DMLGDHIVLD SVRRFSGLE RSIVFGIHPR TADPAILPNV LICLASRAKQ HLYIFPWGGH |
-分子 #2: DNA (5'-D(P*CP*GP*CP*GP*T)-3')
| 分子 | 名称: DNA (5'-D(P*CP*GP*CP*GP*T)-3') / タイプ: dna / ID: 2 / コピー数: 2 / 分類: DNA |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 1.496011 KDa |
| 配列 | 文字列: (DC)(DG)(DC)(DG)(DT) |
-分子 #3: ZINC ION
| 分子 | 名称: ZINC ION / タイプ: ligand / ID: 3 / コピー数: 2 / 式: ZN |
|---|---|
| 分子量 | 理論値: 65.409 Da |
-分子 #4: MAGNESIUM ION
| 分子 | 名称: MAGNESIUM ION / タイプ: ligand / ID: 4 / コピー数: 2 / 式: MG |
|---|---|
| 分子量 | 理論値: 24.305 Da |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 9 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / 最大 デフォーカス(公称値): 2.9 µm / 最小 デフォーカス(公称値): 1.1 µm Bright-field microscopy / 最大 デフォーカス(公称値): 2.9 µm / 最小 デフォーカス(公称値): 1.1 µm |
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 平均電子線量: 43.33 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー







 Z
Z Y
Y X
X