+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 7fdj | ||||||
|---|---|---|---|---|---|---|---|
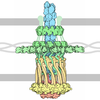
| タイトル | Engineered Hepatitis B virus core antigen with short linker T=4 | ||||||
 要素 要素 | Capsid protein,Immunoglobulin G-binding protein A カプシド カプシド | ||||||
 キーワード キーワード |  VIRUS LIKE PARTICLE (ウイルス様粒子) / VIRUS LIKE PARTICLE (ウイルス様粒子) /  cancer therapy (悪性腫瘍) / cancer therapy (悪性腫瘍) /  epidermal growth factor receptor 1 (上皮成長因子受容体) / epidermal growth factor receptor 1 (上皮成長因子受容体) /  affibody affibody | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報microtubule-dependent intracellular transport of viral material towards nucleus / T=4 icosahedral viral capsid / IgG binding / viral penetration into host nucleus / host cell cytoplasm / symbiont entry into host cell / structural molecule activity /  DNA binding / DNA binding /  RNA binding / extracellular region RNA binding / extracellular region類似検索 - 分子機能 | ||||||
| 生物種 | Hepatitis B virus genotype C subtype adr  Staphylococcus aureus (黄色ブドウ球菌) Staphylococcus aureus (黄色ブドウ球菌) | ||||||
| 手法 |  電子顕微鏡法 / 電子顕微鏡法 /  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 4.4 Å クライオ電子顕微鏡法 / 解像度: 4.4 Å | ||||||
 データ登録者 データ登録者 | Jeong, H. / Heo, Y. / Yoo, Y. / Ryu, B. / Yun, J. / Cho, H. / Lee, W. | ||||||
| 資金援助 |  韓国, 1件 韓国, 1件
| ||||||
 引用 引用 |  ジャーナル: Int J Mol Sci / 年: 2021 ジャーナル: Int J Mol Sci / 年: 2021タイトル: Structural and Functional Characterizations of Cancer Targeting Nanoparticles Based on Hepatitis B Virus Capsid. 著者: Yunseok Heo / Hyeongseop Jeong / Youngki Yoo / Ji-Hye Yun / Bumhan Ryu / Young-Je Cha / Bo-Ram Lee / Ye-Eun Jeon / Jongmin Kim / Sojin Jeong / Eunji Jo / Jae-Sung Woo / Jeewon Lee / Hyun-Soo Cho / Weontae Lee /  要旨: Cancer targeting nanoparticles have been extensively studied, but stable and applicable agents have yet to be developed. Here, we report stable nanoparticles based on hepatitis B core antigen (HBcAg) ...Cancer targeting nanoparticles have been extensively studied, but stable and applicable agents have yet to be developed. Here, we report stable nanoparticles based on hepatitis B core antigen (HBcAg) for cancer therapy. HBcAg monomers assemble into spherical capsids of 180 or 240 subunits. HBcAg was engineered to present an affibody for binding to human epidermal growth factor receptor 1 (EGFR) and to present histidine and tyrosine tags for binding to gold ions. The HBcAg engineered to present affibody and tags (HAF) bound specifically to EGFR and exterminated the EGFR-overexpressing adenocarcinomas under alternating magnetic field (AMF) after binding with gold ions. Using cryogenic electron microscopy (cryo-EM), we obtained the molecular structures of recombinant HAF and found that the overall structure of HAF was the same as that of HBcAg, except with the affibody on the spike. Therefore, HAF is viable for cancer therapy with the advantage of maintaining a stable capsid form. If the affibody in HAF is replaced with a specific sequence to bind to another targetable disease protein, the nanoparticles can be used for drug development over a wide spectrum. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  7fdj.cif.gz 7fdj.cif.gz | 120.3 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb7fdj.ent.gz pdb7fdj.ent.gz | 88.5 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  7fdj.json.gz 7fdj.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/fd/7fdj https://data.pdbj.org/pub/pdb/validation_reports/fd/7fdj ftp://data.pdbj.org/pub/pdb/validation_reports/fd/7fdj ftp://data.pdbj.org/pub/pdb/validation_reports/fd/7fdj | HTTPS FTP |
|---|
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 | x 60
|
| 2 |
|
| 3 | x 5
|
| 4 | x 6
|
| 5 | 
|
| 対称性 | 点対称性: (シェーンフリース記号 : I (正20面体型対称 : I (正20面体型対称 )) )) |
- 要素
要素
| #1: 抗体 |  カプシド / Core antigen / Core protein / HBcAg / p21.5 / IgG-binding protein A / Staphylococcal protein A / SpA カプシド / Core antigen / Core protein / HBcAg / p21.5 / IgG-binding protein A / Staphylococcal protein A / SpA分子量: 35615.000 Da / 分子数: 4 / 由来タイプ: 組換発現 詳細: MHHHHHHMASSLRQILDSQKMEWRSNAGGSGGGSGGGTGGGGGGYYYYYY (expression tag) DIDPYKEFGASVELLSFLPSDFFPSIRDLLDTASALYREALESPEHCSPHHTALRQAILCWGELMNLATWVGSNLED (P69706, residues 2-78) LE (linker) ...詳細: MHHHHHHMASSLRQILDSQKMEWRSNAGGSGGGSGGGTGGGGGGYYYYYY (expression tag) DIDPYKEFGASVELLSFLPSDFFPSIRDLLDTASALYREALESPEHCSPHHTALRQAILCWGELMNLATWVGSNLED (P69706, residues 2-78) LE (linker) VDNKFNKEMWAAWEEIRNLPNLNGWQMTAFIASLVDDPSQSANLLAEAKKLNDAQAPK (P38507, residues 212-269 => modified) EF (linker) VDNKFNKEMWAAWEEIRNLPNLNGWQMTAFIASLVDDPSQSANLLAEAKKLNDAQAPK (P38507, residues 212-269 => modified) GS (linker) SRELVVSYVNVNMGLKIRQLLWFHISCLTFGRETVLEYLVSFGVWIRTPPAYRPPNAPILSTLPETTVV (P69706, residues 81-149) 由来: (組換発現)   Hepatitis B virus genotype C subtype adr (strain Japan/adr4/1983) (B型肝炎ウイルス), (組換発現) Hepatitis B virus genotype C subtype adr (strain Japan/adr4/1983) (B型肝炎ウイルス), (組換発現)   Staphylococcus aureus (黄色ブドウ球菌) Staphylococcus aureus (黄色ブドウ球菌)遺伝子: spa / 発現宿主:   Escherichia coli (大腸菌) / 参照: UniProt: P69706, UniProt: P38507 Escherichia coli (大腸菌) / 参照: UniProt: P69706, UniProt: P38507 |
|---|
-実験情報
-実験
| 実験 | 手法:  電子顕微鏡法 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法:  単粒子再構成法 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: Staphylococcus aureus 黄色ブドウ球菌 / タイプ: VIRUS / 詳細: virus core antigen with short linker / Entity ID: all / 由来: RECOMBINANT 黄色ブドウ球菌 / タイプ: VIRUS / 詳細: virus core antigen with short linker / Entity ID: all / 由来: RECOMBINANT | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 由来(天然) |
| ||||||||||||
| 由来(組換発現) | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) | ||||||||||||
| ウイルスについての詳細 | 中空か: YES / エンベロープを持つか: NO / 単離: OTHER / タイプ: VIRUS-LIKE PARTICLE | ||||||||||||
| 緩衝液 | pH: 7.5 | ||||||||||||
| 試料 | 包埋: NO / シャドウイング: NO / 染色 : NO / 凍結 : NO / 凍結 : YES : YES | ||||||||||||
急速凍結 | 凍結剤: ETHANE |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源 : :  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD Bright-field microscopy Bright-field microscopy |
| 撮影 | 電子線照射量: 45 e/Å2 フィルム・検出器のモデル: FEI FALCON III (4k x 4k) |
- 解析
解析
| ソフトウェア | 名称: PHENIX / バージョン: 1.19.2_4158: / 分類: 精密化 | ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||
3次元再構成 | 解像度: 4.4 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 46346 / 対称性のタイプ: POINT | ||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー


















 PDBj
PDBj