+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 7aaq | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Title | sugar/H+ symporter STP10 in outward occluded conformation | ||||||||||||
 Components Components | Sugar transport protein 10 | ||||||||||||
 Keywords Keywords |  MEMBRANE PROTEIN / MEMBRANE PROTEIN /  ALPHA-HELICAL PROTEIN / SUGAR TRANSPORT / PROTOIN/SUGAR SYMPORTER / MAJOR FACILITATOR ALPHA-HELICAL PROTEIN / SUGAR TRANSPORT / PROTOIN/SUGAR SYMPORTER / MAJOR FACILITATOR | ||||||||||||
| Function / homology |  Function and homology information Function and homology informationhexose:proton symporter activity / mannose transmembrane transporter activity / D-glucose:proton symporter activity / galactose transmembrane transporter activity / hexose transmembrane transport / cellular response to glucose stimulus /  plasma membrane plasma membraneSimilarity search - Function | ||||||||||||
| Biological species |   Arabidopsis thaliana (thale cress) Arabidopsis thaliana (thale cress) | ||||||||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  MOLECULAR REPLACEMENT / MOLECULAR REPLACEMENT /  molecular replacement / Resolution: 1.81 Å molecular replacement / Resolution: 1.81 Å | ||||||||||||
 Authors Authors | Bavnhoej, L. / Paulsen, P.A. / Pedersen, B.P. | ||||||||||||
| Funding support |  Denmark, 3items Denmark, 3items
| ||||||||||||
 Citation Citation |  Journal: Nat.Plants / Year: 2021 Journal: Nat.Plants / Year: 2021Title: Molecular mechanism of sugar transport in plants unveiled by structures of glucose/H + symporter STP10. Authors: Bavnhoj, L. / Paulsen, P.A. / Flores-Canales, J.C. / Schiott, B. / Pedersen, B.P. | ||||||||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  7aaq.cif.gz 7aaq.cif.gz | 208.3 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb7aaq.ent.gz pdb7aaq.ent.gz | 165.4 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  7aaq.json.gz 7aaq.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/aa/7aaq https://data.pdbj.org/pub/pdb/validation_reports/aa/7aaq ftp://data.pdbj.org/pub/pdb/validation_reports/aa/7aaq ftp://data.pdbj.org/pub/pdb/validation_reports/aa/7aaq | HTTPS FTP |
|---|
-Related structure data
| Related structure data |  7aarC  6h7dS S: Starting model for refinement C: citing same article ( |
|---|---|
| Similar structure data |
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| Unit cell |
|
- Components
Components
-Protein / Sugars , 2 types, 2 molecules A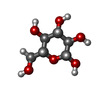

| #1: Protein | Mass: 56244.781 Da / Num. of mol.: 1 Source method: isolated from a genetically manipulated source Source: (gene. exp.)   Arabidopsis thaliana (thale cress) / Gene: STP10, At3g19940, MPN9.19 / Plasmid: p423_GAL1 / Production host: Arabidopsis thaliana (thale cress) / Gene: STP10, At3g19940, MPN9.19 / Plasmid: p423_GAL1 / Production host:   Saccharomyces cerevisiae (brewer's yeast) / Strain (production host): DSY5 / References: UniProt: Q9LT15 Saccharomyces cerevisiae (brewer's yeast) / Strain (production host): DSY5 / References: UniProt: Q9LT15 |
|---|---|
| #2: Sugar | ChemComp-BGC /  Glucose Glucose |
-Non-polymers , 4 types, 164 molecules 






| #3: Chemical | ChemComp-OLC / ( #4: Chemical | ChemComp-XPE / |  Polyethylene glycol Polyethylene glycol#5: Chemical |  Acetate Acetate#6: Water | ChemComp-HOH / |  Water Water |
|---|
-Details
| Has ligand of interest | Y |
|---|
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 2.94 Å3/Da / Density % sol: 58.1 % |
|---|---|
Crystal grow | Temperature: 292.15 K / Method: lipidic cubic phase / pH: 4 Details: 0.1-0.15M Ammonium Acetate, 0.1M Sodium Citrate and 36-40% PEG400 |
-Data collection
| Diffraction | Mean temperature: 100 K / Serial crystal experiment: N | ||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  Diamond Diamond  / Beamline: I04 / Wavelength: 0.97942 Å / Beamline: I04 / Wavelength: 0.97942 Å | ||||||||||||||||||||||||||||||
| Detector | Type: DECTRIS PILATUS 6M-F / Detector: PIXEL / Date: Jun 20, 2019 | ||||||||||||||||||||||||||||||
| Radiation | Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray | ||||||||||||||||||||||||||||||
| Radiation wavelength | Wavelength : 0.97942 Å / Relative weight: 1 : 0.97942 Å / Relative weight: 1 | ||||||||||||||||||||||||||||||
| Reflection | Resolution: 1.81→59.9 Å / Num. obs: 61268 / % possible obs: 100 % / Redundancy: 11 % / CC1/2: 0.998 / Rmerge(I) obs: 0.168 / Rpim(I) all: 0.053 / Rrim(I) all: 0.176 / Net I/σ(I): 7.7 / Num. measured all: 665695 / Scaling rejects: 1006 | ||||||||||||||||||||||||||||||
| Reflection shell | Diffraction-ID: 1
|
-Phasing
Phasing | Method:  molecular replacement molecular replacement |
|---|
- Processing
Processing
| Software |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure : :  MOLECULAR REPLACEMENT MOLECULAR REPLACEMENTStarting model: 6H7D Resolution: 1.81→46.39 Å / SU ML: 0.19 / Cross valid method: THROUGHOUT / σ(F): 1.33 / Phase error: 24.88 / Stereochemistry target values: ML
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Solvent computation | Shrinkage radii: 0.9 Å / VDW probe radii: 1.11 Å / Solvent model: FLAT BULK SOLVENT MODEL | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | Biso max: 120.64 Å2 / Biso mean: 37.451 Å2 / Biso min: 19.99 Å2 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: final / Resolution: 1.81→46.39 Å
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell | Refine-ID: X-RAY DIFFRACTION / Rfactor Rfree error: 0 / Total num. of bins used: 22
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS params. | Method: refined / Refine-ID: X-RAY DIFFRACTION
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS group |
|
 Movie
Movie Controller
Controller













 PDBj
PDBj













