[English] 日本語
 Yorodumi
Yorodumi- PDB-5ob2: Crystal structure of the c-Src-SH3 domain E97T mutant in complex ... -
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 5ob2 | ||||||
|---|---|---|---|---|---|---|---|
| Title | Crystal structure of the c-Src-SH3 domain E97T mutant in complex with the high affinity peptide APP12 | ||||||
 Components Components |
| ||||||
 Keywords Keywords |  TRANSFERASE / beta shandwich TRANSFERASE / beta shandwich | ||||||
| Function / homology |  Function and homology information Function and homology informationSignaling by ERBB2 / Nuclear signaling by ERBB4 / PIP3 activates AKT signaling / Signaling by SCF-KIT / Regulation of KIT signaling / Signaling by EGFR / GAB1 signalosome /  Regulation of gap junction activity / FCGR activation / PECAM1 interactions ...Signaling by ERBB2 / Nuclear signaling by ERBB4 / PIP3 activates AKT signaling / Signaling by SCF-KIT / Regulation of KIT signaling / Signaling by EGFR / GAB1 signalosome / Regulation of gap junction activity / FCGR activation / PECAM1 interactions ...Signaling by ERBB2 / Nuclear signaling by ERBB4 / PIP3 activates AKT signaling / Signaling by SCF-KIT / Regulation of KIT signaling / Signaling by EGFR / GAB1 signalosome /  Regulation of gap junction activity / FCGR activation / PECAM1 interactions / CD28 co-stimulation / CTLA4 inhibitory signaling / EPHA-mediated growth cone collapse / Ephrin signaling / G alpha (i) signalling events / GP1b-IX-V activation signalling / Recycling pathway of L1 / Thrombin signalling through proteinase activated receptors (PARs) / VEGFR2 mediated cell proliferation / RAF activation / PI5P, PP2A and IER3 Regulate PI3K/AKT Signaling / RET signaling / Receptor Mediated Mitophagy / ADP signalling through P2Y purinoceptor 1 / Downregulation of ERBB4 signaling / EPH-ephrin mediated repulsion of cells / Cyclin D associated events in G1 / Regulation of RUNX3 expression and activity / Activated NTRK3 signals through PI3K / Downstream signal transduction / MAP2K and MAPK activation / Integrin signaling / GRB2:SOS provides linkage to MAPK signaling for Integrins / MET activates PTK2 signaling / Extra-nuclear estrogen signaling / EPHB-mediated forward signaling / p130Cas linkage to MAPK signaling for integrins / VEGFA-VEGFR2 Pathway / Regulation of gap junction activity / FCGR activation / PECAM1 interactions / CD28 co-stimulation / CTLA4 inhibitory signaling / EPHA-mediated growth cone collapse / Ephrin signaling / G alpha (i) signalling events / GP1b-IX-V activation signalling / Recycling pathway of L1 / Thrombin signalling through proteinase activated receptors (PARs) / VEGFR2 mediated cell proliferation / RAF activation / PI5P, PP2A and IER3 Regulate PI3K/AKT Signaling / RET signaling / Receptor Mediated Mitophagy / ADP signalling through P2Y purinoceptor 1 / Downregulation of ERBB4 signaling / EPH-ephrin mediated repulsion of cells / Cyclin D associated events in G1 / Regulation of RUNX3 expression and activity / Activated NTRK3 signals through PI3K / Downstream signal transduction / MAP2K and MAPK activation / Integrin signaling / GRB2:SOS provides linkage to MAPK signaling for Integrins / MET activates PTK2 signaling / Extra-nuclear estrogen signaling / EPHB-mediated forward signaling / p130Cas linkage to MAPK signaling for integrins / VEGFA-VEGFR2 Pathway /  connexin binding / osteoclast development / progesterone receptor signaling pathway / negative regulation of intrinsic apoptotic signaling pathway / connexin binding / osteoclast development / progesterone receptor signaling pathway / negative regulation of intrinsic apoptotic signaling pathway /  bone resorption / bone resorption /  extrinsic component of cytoplasmic side of plasma membrane / negative regulation of extrinsic apoptotic signaling pathway / extrinsic component of cytoplasmic side of plasma membrane / negative regulation of extrinsic apoptotic signaling pathway /  non-specific protein-tyrosine kinase / non-membrane spanning protein tyrosine kinase activity / epidermal growth factor receptor signaling pathway / non-specific protein-tyrosine kinase / non-membrane spanning protein tyrosine kinase activity / epidermal growth factor receptor signaling pathway /  cell junction / cell junction /  protein phosphatase binding / protein phosphatase binding /  protein tyrosine kinase activity / protein tyrosine kinase activity /  mitochondrial inner membrane / mitochondrial inner membrane /  cell differentiation / cell differentiation /  cytoskeleton / endosome membrane / cytoskeleton / endosome membrane /  regulation of cell cycle / regulation of cell cycle /  cell adhesion / cell adhesion /  cell cycle / cell cycle /  phosphorylation / phosphorylation /  signaling receptor binding / signaling receptor binding /  focal adhesion / focal adhesion /  innate immune response / innate immune response /  heme binding / perinuclear region of cytoplasm / protein-containing complex / heme binding / perinuclear region of cytoplasm / protein-containing complex /  ATP binding / ATP binding /  membrane / membrane /  nucleus / nucleus /  plasma membrane / plasma membrane /  cytosol cytosolSimilarity search - Function | ||||||
| Biological species |   Gallus gallus (chicken) Gallus gallus (chicken)synthetic construct (others) | ||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  MOLECULAR REPLACEMENT / MOLECULAR REPLACEMENT /  molecular replacement / Resolution: 1.8 Å molecular replacement / Resolution: 1.8 Å | ||||||
 Authors Authors | Camara-Artigas, A. | ||||||
| Funding support |  Spain, 1items Spain, 1items
| ||||||
 Citation Citation |  Journal: to be published Journal: to be publishedTitle: Crystal structure of the c-Src-SH3 domain E97T mutant in complex with the high affinity peptide APP12 Authors: Camara-Artigas, A. | ||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  5ob2.cif.gz 5ob2.cif.gz | 85.7 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb5ob2.ent.gz pdb5ob2.ent.gz | 65.2 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  5ob2.json.gz 5ob2.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/ob/5ob2 https://data.pdbj.org/pub/pdb/validation_reports/ob/5ob2 ftp://data.pdbj.org/pub/pdb/validation_reports/ob/5ob2 ftp://data.pdbj.org/pub/pdb/validation_reports/ob/5ob2 | HTTPS FTP |
|---|
-Related structure data
| Related structure data |  4jz4S S: Starting model for refinement |
|---|---|
| Similar structure data |
- Links
Links
- Assembly
Assembly
| Deposited unit | 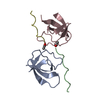
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| Unit cell |
|
- Components
Components
| #1: Protein |  / Proto-oncogene c-Src / pp60c-src / p60-Src / Proto-oncogene c-Src / pp60c-src / p60-SrcMass: 6906.553 Da / Num. of mol.: 2 / Fragment: SH3 DOMAIN Source method: isolated from a genetically manipulated source Source: (gene. exp.)   Gallus gallus (chicken) / Gene: SRC / Plasmid: pET15b / Production host: Gallus gallus (chicken) / Gene: SRC / Plasmid: pET15b / Production host:   Escherichia coli BL21(DE3) (bacteria) Escherichia coli BL21(DE3) (bacteria)References: UniProt: P00523,  non-specific protein-tyrosine kinase non-specific protein-tyrosine kinase#2: Protein/peptide | Mass: 1412.705 Da / Num. of mol.: 2 / Source method: obtained synthetically / Source: (synth.) synthetic construct (others) #3: Water | ChemComp-HOH / |  Water Water |
|---|
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 2.09 Å3/Da / Density % sol: 41.14 % / Mosaicity: 0.31 ° |
|---|---|
Crystal grow | Temperature: 298 K / Method: vapor diffusion, hanging drop / pH: 4 Details: 1.9 M Ammonium sulphate, 0.1 M sodium acetate and 10% PEG 400 |
-Data collection
| Diffraction | Mean temperature: 100 K | |||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  ESRF ESRF  / Beamline: MASSIF-1 / Wavelength: 0.965 Å / Beamline: MASSIF-1 / Wavelength: 0.965 Å | |||||||||||||||||||||
| Detector | Type: DECTRIS PILATUS 2M / Detector: PIXEL / Date: Feb 25, 2015 | |||||||||||||||||||||
| Radiation | Monochromator: Diamond / Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray | |||||||||||||||||||||
| Radiation wavelength | Wavelength : 0.965 Å / Relative weight: 1 : 0.965 Å / Relative weight: 1 | |||||||||||||||||||||
| Reflection | Resolution: 1.8→19.29 Å / Num. obs: 21432 / % possible obs: 93.1 % / Redundancy: 2.3 % / Biso Wilson estimate: 12.93 Å2 / CC1/2: 0.994 / Rmerge(I) obs: 0.059 / Rpim(I) all: 0.047 / Rrim(I) all: 0.076 / Net I/σ(I): 9.8 | |||||||||||||||||||||
| Reflection shell | Diffraction-ID: 1
|
-Phasing
Phasing | Method:  molecular replacement molecular replacement |
|---|
- Processing
Processing
| Software |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure : :  MOLECULAR REPLACEMENT MOLECULAR REPLACEMENTStarting model: 4JZ4 Resolution: 1.8→19.288 Å / SU ML: 0.21 / Cross valid method: THROUGHOUT / σ(F): 0.53 / Phase error: 23.06
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Solvent computation | Shrinkage radii: 0.9 Å / VDW probe radii: 1.11 Å | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | Biso max: 59.4 Å2 / Biso mean: 19.1468 Å2 / Biso min: 4.86 Å2 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: final / Resolution: 1.8→19.288 Å
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell | Refine-ID: X-RAY DIFFRACTION / Rfactor Rfree error: 0 / Total num. of bins used: 8
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS params. | Method: refined / Refine-ID: X-RAY DIFFRACTION
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS group |
|
 Movie
Movie Controller
Controller












 PDBj
PDBj
