+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 5ix0 | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | HDAC2 WITH LIGAND BRD7232 | ||||||
 要素 要素 | Histone deacetylase 2 | ||||||
 キーワード キーワード |  HYDROLASE (加水分解酵素) / HDAC HISTONE DEACETYLASE HYDROLASE (加水分解酵素) / HDAC HISTONE DEACETYLASE | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報protein de-2-hydroxyisobutyrylase activity / positive regulation of male mating behavior / negative regulation of peptidyl-lysine acetylation / p75NTR negatively regulates cell cycle via SC1 / epidermal cell differentiation / negative regulation of dendritic spine development / histone decrotonylase activity / fungiform papilla formation / negative regulation of MHC class II biosynthetic process / behavioral response to ethanol ...protein de-2-hydroxyisobutyrylase activity / positive regulation of male mating behavior / negative regulation of peptidyl-lysine acetylation / p75NTR negatively regulates cell cycle via SC1 / epidermal cell differentiation / negative regulation of dendritic spine development / histone decrotonylase activity / fungiform papilla formation / negative regulation of MHC class II biosynthetic process / behavioral response to ethanol / NuRD complex / positive regulation of interleukin-1 production / regulation of cell fate specification / negative regulation of stem cell population maintenance / EGR2 and SOX10-mediated initiation of Schwann cell myelination / negative regulation of transcription by competitive promoter binding / ESC/E(Z) complex /  regulation of stem cell differentiation / STAT3 nuclear events downstream of ALK signaling / cellular response to dopamine / regulation of stem cell differentiation / STAT3 nuclear events downstream of ALK signaling / cellular response to dopamine /  ヒストン脱アセチル化酵素 / cardiac muscle hypertrophy / protein lysine deacetylase activity / positive regulation of signaling receptor activity / response to caffeine / ヒストン脱アセチル化酵素 / cardiac muscle hypertrophy / protein lysine deacetylase activity / positive regulation of signaling receptor activity / response to caffeine /  加水分解酵素; ペプチド以外のCN結合加水分解酵素; 鎖状アミドに作用 / 加水分解酵素; ペプチド以外のCN結合加水分解酵素; 鎖状アミドに作用 /  histone deacetylase activity / embryonic digit morphogenesis / positive regulation of oligodendrocyte differentiation / positive regulation of stem cell population maintenance / Sin3-type complex / Notch-HLH transcription pathway / eyelid development in camera-type eye / dendrite development / odontogenesis of dentin-containing tooth / positive regulation of proteolysis / RNA Polymerase I Transcription Initiation / response to amyloid-beta / histone deacetylase activity / embryonic digit morphogenesis / positive regulation of oligodendrocyte differentiation / positive regulation of stem cell population maintenance / Sin3-type complex / Notch-HLH transcription pathway / eyelid development in camera-type eye / dendrite development / odontogenesis of dentin-containing tooth / positive regulation of proteolysis / RNA Polymerase I Transcription Initiation / response to amyloid-beta /  histone deacetylase complex / hair follicle placode formation / Regulation of MECP2 expression and activity / histone deacetylase complex / hair follicle placode formation / Regulation of MECP2 expression and activity /  NF-kappaB binding / positive regulation of collagen biosynthetic process / response to hyperoxia / positive regulation of epithelial to mesenchymal transition / FOXO-mediated transcription of oxidative stress, metabolic and neuronal genes / heterochromatin formation / MECP2 regulates neuronal receptors and channels / cellular response to retinoic acid / positive regulation of tyrosine phosphorylation of STAT protein / Regulation of TP53 Activity through Acetylation / cellular response to transforming growth factor beta stimulus / response to amphetamine / NF-kappaB binding / positive regulation of collagen biosynthetic process / response to hyperoxia / positive regulation of epithelial to mesenchymal transition / FOXO-mediated transcription of oxidative stress, metabolic and neuronal genes / heterochromatin formation / MECP2 regulates neuronal receptors and channels / cellular response to retinoic acid / positive regulation of tyrosine phosphorylation of STAT protein / Regulation of TP53 Activity through Acetylation / cellular response to transforming growth factor beta stimulus / response to amphetamine /  heat shock protein binding / SUMOylation of chromatin organization proteins / negative regulation of cell migration / ERCC6 (CSB) and EHMT2 (G9a) positively regulate rRNA expression / response to nicotine / response to cocaine / Regulation of PTEN gene transcription / promoter-specific chromatin binding / HDACs deacetylate histones / negative regulation of transforming growth factor beta receptor signaling pathway / circadian regulation of gene expression / protein modification process / NoRC negatively regulates rRNA expression / negative regulation of DNA-binding transcription factor activity / NOTCH1 Intracellular Domain Regulates Transcription / cellular response to hydrogen peroxide / Constitutive Signaling by NOTCH1 PEST Domain Mutants / Constitutive Signaling by NOTCH1 HD+PEST Domain Mutants / heat shock protein binding / SUMOylation of chromatin organization proteins / negative regulation of cell migration / ERCC6 (CSB) and EHMT2 (G9a) positively regulate rRNA expression / response to nicotine / response to cocaine / Regulation of PTEN gene transcription / promoter-specific chromatin binding / HDACs deacetylate histones / negative regulation of transforming growth factor beta receptor signaling pathway / circadian regulation of gene expression / protein modification process / NoRC negatively regulates rRNA expression / negative regulation of DNA-binding transcription factor activity / NOTCH1 Intracellular Domain Regulates Transcription / cellular response to hydrogen peroxide / Constitutive Signaling by NOTCH1 PEST Domain Mutants / Constitutive Signaling by NOTCH1 HD+PEST Domain Mutants /  histone deacetylase binding / positive regulation of tumor necrosis factor production / negative regulation of neuron projection development / cellular response to heat / Factors involved in megakaryocyte development and platelet production / histone deacetylase binding / positive regulation of tumor necrosis factor production / negative regulation of neuron projection development / cellular response to heat / Factors involved in megakaryocyte development and platelet production /  histone binding / RNA polymerase II-specific DNA-binding transcription factor binding / Potential therapeutics for SARS / response to lipopolysaccharide / histone binding / RNA polymerase II-specific DNA-binding transcription factor binding / Potential therapeutics for SARS / response to lipopolysaccharide /  chromosome, telomeric region / chromosome, telomeric region /  クロマチンリモデリング / response to xenobiotic stimulus / negative regulation of DNA-templated transcription / クロマチンリモデリング / response to xenobiotic stimulus / negative regulation of DNA-templated transcription /  chromatin binding / positive regulation of cell population proliferation / chromatin binding / positive regulation of cell population proliferation /  クロマチン / negative regulation of apoptotic process / positive regulation of DNA-templated transcription / negative regulation of transcription by RNA polymerase II / クロマチン / negative regulation of apoptotic process / positive regulation of DNA-templated transcription / negative regulation of transcription by RNA polymerase II /  enzyme binding / positive regulation of transcription by RNA polymerase II / protein-containing complex / enzyme binding / positive regulation of transcription by RNA polymerase II / protein-containing complex /  RNA binding / RNA binding /  核質 / 核質 /  細胞核 / 細胞核 /  細胞質 細胞質類似検索 - 分子機能 | ||||||
| 生物種 |   Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 1.72 Å 分子置換 / 解像度: 1.72 Å | ||||||
 データ登録者 データ登録者 | Steinbacher, S. | ||||||
 引用 引用 |  ジャーナル: Bioorg.Med.Chem. / 年: 2016 ジャーナル: Bioorg.Med.Chem. / 年: 2016タイトル: Kinetic and structural insights into the binding of histone deacetylase 1 and 2 (HDAC1, 2) inhibitors. 著者: Wagner, F.F. / Weiwer, M. / Steinbacher, S. / Schomburg, A. / Reinemer, P. / Gale, J.P. / Campbell, A.J. / Fisher, S.L. / Zhao, W.N. / Reis, S.A. / Hennig, K.M. / Thomas, M. / Muller, P. / ...著者: Wagner, F.F. / Weiwer, M. / Steinbacher, S. / Schomburg, A. / Reinemer, P. / Gale, J.P. / Campbell, A.J. / Fisher, S.L. / Zhao, W.N. / Reis, S.A. / Hennig, K.M. / Thomas, M. / Muller, P. / Jefson, M.R. / Fass, D.M. / Haggarty, S.J. / Zhang, Y.L. / Holson, E.B. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  5ix0.cif.gz 5ix0.cif.gz | 473.2 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb5ix0.ent.gz pdb5ix0.ent.gz | 387.8 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  5ix0.json.gz 5ix0.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/ix/5ix0 https://data.pdbj.org/pub/pdb/validation_reports/ix/5ix0 ftp://data.pdbj.org/pub/pdb/validation_reports/ix/5ix0 ftp://data.pdbj.org/pub/pdb/validation_reports/ix/5ix0 | HTTPS FTP |
|---|
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 | 
| ||||||||
| 2 |
| ||||||||
| 3 | 
| ||||||||
| 4 | 
| ||||||||
| 単位格子 |
|
- 要素
要素
-タンパク質 , 1種, 3分子 ABC
| #1: タンパク質 |  / HD2 / HD2分子量: 42286.141 Da / 分子数: 3 / 断片: UNP residues 7-375 / 由来タイプ: 組換発現 / 由来: (組換発現)   Homo sapiens (ヒト) / 遺伝子: HDAC2 / 発現宿主: Homo sapiens (ヒト) / 遺伝子: HDAC2 / 発現宿主:   Escherichia coli (大腸菌) Escherichia coli (大腸菌)参照: UniProt: Q92769,  ヒストン脱アセチル化酵素 ヒストン脱アセチル化酵素 |
|---|
-非ポリマー , 9種, 872分子 

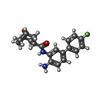













| #2: 化合物 | | #3: 化合物 | ChemComp-CA / #4: 化合物 | #5: 化合物 | ChemComp-PEG /  ジエチレングリコール ジエチレングリコール#6: 化合物 |  ポリエチレングリコール ポリエチレングリコール#7: 化合物 |  トリグリム トリグリム#8: 化合物 | ChemComp-PGE /  ポリエチレングリコール ポリエチレングリコール#9: 化合物 |  エチレングリコール エチレングリコール#10: 水 | ChemComp-HOH / |  水 水 |
|---|
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.51 Å3/Da / 溶媒含有率: 51.07 % |
|---|---|
結晶化 | 温度: 293 K / 手法: 蒸気拡散法, シッティングドロップ法 / pH: 5.5 / 詳細: PEG 400, potassium phosphate |
-データ収集
| 回折 | 平均測定温度: 100 K |
|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  SLS SLS  / ビームライン: X06SA / 波長: 1 Å / ビームライン: X06SA / 波長: 1 Å |
| 検出器 | タイプ: DECTRIS PILATUS3 6M / 検出器: PIXEL / 日付: 2013年11月18日 / 詳細: Dynamically bendable mirror |
| 放射 | モノクロメーター: LN2 cooled fixed-exit Si(111) monochromator プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長 : 1 Å / 相対比: 1 : 1 Å / 相対比: 1 |
| 反射 | 解像度: 1.72→79.85 Å / Num. obs: 133389 / % possible obs: 100 % / Observed criterion σ(I): 0 / 冗長度: 8.2 % / Rmerge(I) obs: 0.08 / Net I/σ(I): 2.81 |
| 反射 シェル | 解像度: 1.72→1.76 Å / 冗長度: 8.4 % / Rmerge(I) obs: 0.934 / % possible all: 100 |
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法 : :  分子置換 / 解像度: 1.72→48.736 Å / Cor.coef. Fo:Fc: 0.962 / Cor.coef. Fo:Fc free: 0.949 / SU B: 4.784 / SU ML: 0.076 / 交差検証法: THROUGHOUT / ESU R: 0.102 / ESU R Free: 0.095 / 詳細: HYDROGENS HAVE BEEN ADDED IN THE RIDING POSITIONS 分子置換 / 解像度: 1.72→48.736 Å / Cor.coef. Fo:Fc: 0.962 / Cor.coef. Fo:Fc free: 0.949 / SU B: 4.784 / SU ML: 0.076 / 交差検証法: THROUGHOUT / ESU R: 0.102 / ESU R Free: 0.095 / 詳細: HYDROGENS HAVE BEEN ADDED IN THE RIDING POSITIONS
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | イオンプローブ半径: 0.8 Å / 減衰半径: 0.8 Å / VDWプローブ半径: 1.2 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 27.193 Å2
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 1.72→48.736 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー














 PDBj
PDBj
































