| 登録情報 | データベース: PDB / ID: 4yk5
|
|---|
| タイトル | Crystal Structures of mPGES-1 Inhibitor Complexes |
|---|
 要素 要素 | Prostaglandin E synthase |
|---|
 キーワード キーワード | ISOMERASE/ISOMERASE INHIBITOR /  Inflammation (炎症) / ISOMERASE-ISOMERASE INHIBITOR complex Inflammation (炎症) / ISOMERASE-ISOMERASE INHIBITOR complex |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報 |
|---|
| 生物種 |   Homo sapiens (ヒト) Homo sapiens (ヒト) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / 解像度: 1.42 Å シンクロトロン / 解像度: 1.42 Å |
|---|
 データ登録者 データ登録者 | Luz, J.G. / Antonysamy, S. / Kuklish, S.L. / Fisher, M.J. |
|---|
 引用 引用 |  ジャーナル: J.Med.Chem. / 年: 2015 ジャーナル: J.Med.Chem. / 年: 2015
タイトル: Crystal Structures of mPGES-1 Inhibitor Complexes Form a Basis for the Rational Design of Potent Analgesic and Anti-Inflammatory Therapeutics.
著者: Luz, J.G. / Antonysamy, S. / Kuklish, S.L. / Condon, B. / Lee, M.R. / Allison, D. / Yu, X.P. / Chandrasekhar, S. / Backer, R. / Zhang, A. / Russell, M. / Chang, S.S. / Harvey, A. / Sloan, A.V. / Fisher, M.J. |
|---|
| 履歴 | | 登録 | 2015年3月4日 | 登録サイト: RCSB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2015年7月15日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2017年11月22日 | Group: Database references / Derived calculations ...Database references / Derived calculations / Other / Refinement description / Source and taxonomy / Structure summary
カテゴリ: citation / entity_src_gen ...citation / entity_src_gen / pdbx_database_status / pdbx_struct_oper_list / software / struct_keywords
Item: _citation.journal_id_CSD / _entity_src_gen.pdbx_alt_source_flag ..._citation.journal_id_CSD / _entity_src_gen.pdbx_alt_source_flag / _pdbx_database_status.pdb_format_compatible / _pdbx_struct_oper_list.symmetry_operation / _struct_keywords.text |
|---|
| 改定 1.2 | 2020年7月29日 | Group: Data collection / Derived calculations / Structure summary
カテゴリ: chem_comp / entity ...chem_comp / entity / pdbx_chem_comp_identifier / pdbx_entity_nonpoly / struct_site / struct_site_gen
Item: _chem_comp.mon_nstd_flag / _chem_comp.name ..._chem_comp.mon_nstd_flag / _chem_comp.name / _chem_comp.type / _entity.pdbx_description / _pdbx_entity_nonpoly.name
解説: Carbohydrate remediation / Provider: repository / タイプ: Remediation |
|---|
| 改定 1.3 | 2024年2月28日 | Group: Data collection / Database references / Structure summary
カテゴリ: chem_comp / chem_comp_atom ...chem_comp / chem_comp_atom / chem_comp_bond / database_2
Item: _chem_comp.pdbx_synonyms / _database_2.pdbx_DOI / _database_2.pdbx_database_accession |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素
 キーワード
キーワード Inflammation (炎症) / ISOMERASE-ISOMERASE INHIBITOR complex
Inflammation (炎症) / ISOMERASE-ISOMERASE INHIBITOR complex 機能・相同性情報
機能・相同性情報 prostaglandin-E synthase /
prostaglandin-E synthase /  prostaglandin-E synthase activity /
prostaglandin-E synthase activity /  prostaglandin-D synthase activity / positive regulation of prostaglandin secretion /
prostaglandin-D synthase activity / positive regulation of prostaglandin secretion /  glutathione binding / Synthesis of Prostaglandins (PG) and Thromboxanes (TX) /
glutathione binding / Synthesis of Prostaglandins (PG) and Thromboxanes (TX) /  glutathione peroxidase activity / prostaglandin biosynthetic process / prostaglandin metabolic process ...regulation of fever generation /
glutathione peroxidase activity / prostaglandin biosynthetic process / prostaglandin metabolic process ...regulation of fever generation /  prostaglandin-E synthase /
prostaglandin-E synthase /  prostaglandin-E synthase activity /
prostaglandin-E synthase activity /  prostaglandin-D synthase activity / positive regulation of prostaglandin secretion /
prostaglandin-D synthase activity / positive regulation of prostaglandin secretion /  glutathione binding / Synthesis of Prostaglandins (PG) and Thromboxanes (TX) /
glutathione binding / Synthesis of Prostaglandins (PG) and Thromboxanes (TX) /  glutathione peroxidase activity / prostaglandin biosynthetic process / prostaglandin metabolic process / nuclear envelope lumen /
glutathione peroxidase activity / prostaglandin biosynthetic process / prostaglandin metabolic process / nuclear envelope lumen /  グルタチオン-S-トランスフェラーゼ /
グルタチオン-S-トランスフェラーゼ /  glutathione transferase activity /
glutathione transferase activity /  酸化還元酵素; 過酸化物を電子受容体にする; ペルオキシダーゼ / sensory perception of pain /
酸化還元酵素; 過酸化物を電子受容体にする; ペルオキシダーゼ / sensory perception of pain /  regulation of inflammatory response / cell population proliferation / negative regulation of cell population proliferation / endoplasmic reticulum membrane / perinuclear region of cytoplasm /
regulation of inflammatory response / cell population proliferation / negative regulation of cell population proliferation / endoplasmic reticulum membrane / perinuclear region of cytoplasm /  シグナル伝達 /
シグナル伝達 /  生体膜
生体膜
 Homo sapiens (ヒト)
Homo sapiens (ヒト) X線回折 /
X線回折 /  シンクロトロン / 解像度: 1.42 Å
シンクロトロン / 解像度: 1.42 Å  データ登録者
データ登録者 引用
引用 ジャーナル: J.Med.Chem. / 年: 2015
ジャーナル: J.Med.Chem. / 年: 2015 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 4yk5.cif.gz
4yk5.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb4yk5.ent.gz
pdb4yk5.ent.gz PDB形式
PDB形式 4yk5.json.gz
4yk5.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/yk/4yk5
https://data.pdbj.org/pub/pdb/validation_reports/yk/4yk5 ftp://data.pdbj.org/pub/pdb/validation_reports/yk/4yk5
ftp://data.pdbj.org/pub/pdb/validation_reports/yk/4yk5 リンク
リンク 集合体
集合体

 要素
要素 / Microsomal glutathione S-transferase 1-like 1 / MGST1-L1 / Microsomal prostaglandin E synthase 1 / ...Microsomal glutathione S-transferase 1-like 1 / MGST1-L1 / Microsomal prostaglandin E synthase 1 / MPGES-1 / p53-induced gene 12 protein
/ Microsomal glutathione S-transferase 1-like 1 / MGST1-L1 / Microsomal prostaglandin E synthase 1 / ...Microsomal glutathione S-transferase 1-like 1 / MGST1-L1 / Microsomal prostaglandin E synthase 1 / MPGES-1 / p53-induced gene 12 protein
 Homo sapiens (ヒト) / 遺伝子: PTGES, MGST1L1, MPGES1, PGES, PIG12
Homo sapiens (ヒト) / 遺伝子: PTGES, MGST1L1, MPGES1, PGES, PIG12
 Spodoptera frugiperda (ツマジロクサヨトウ)
Spodoptera frugiperda (ツマジロクサヨトウ) prostaglandin-E synthase
prostaglandin-E synthase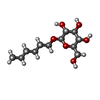
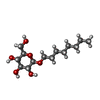

 Octyl glucoside
Octyl glucoside
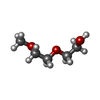
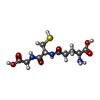






 ジエチレングリコールモノメチルエーテル
ジエチレングリコールモノメチルエーテル グルタチオン
グルタチオン ポリエチレングリコール
ポリエチレングリコール 水
水 X線回折
X線回折 試料調製
試料調製
 シンクロトロン / サイト:
シンクロトロン / サイト:  APS
APS  / ビームライン: 31-ID / 波長: 0.97929 Å
/ ビームライン: 31-ID / 波長: 0.97929 Å : 0.97929 Å / 相対比: 1
: 0.97929 Å / 相対比: 1  解析
解析 ムービー
ムービー コントローラー
コントローラー
















 PDBj
PDBj







