[English] 日本語
 Yorodumi
Yorodumi- PDB-4hkl: Crystal Structures of Mutant Endo-beta-1,4-xylanase II Complexed ... -
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 4hkl | ||||||
|---|---|---|---|---|---|---|---|
| Title | Crystal Structures of Mutant Endo-beta-1,4-xylanase II Complexed with substrate (1.15 A) and Products (1.6 A) | ||||||
 Components Components | Endo-1,4-beta-xylanase 2 Xylanase Xylanase | ||||||
 Keywords Keywords |  HYDROLASE / HYDROLASE /  xylanase II / xylohexaose / xylotriose / induced fit mechanism / xylanase II / xylohexaose / xylotriose / induced fit mechanism /  oxocarbenium ion oxocarbenium ion | ||||||
| Function / homology |  Function and homology information Function and homology information endo-1,4-beta-xylanase activity / endo-1,4-beta-xylanase activity /  endo-1,4-beta-xylanase / xylan catabolic process / extracellular region endo-1,4-beta-xylanase / xylan catabolic process / extracellular regionSimilarity search - Function | ||||||
| Biological species |   Trichoderma reesei (fungus) Trichoderma reesei (fungus) | ||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  MOLECULAR REPLACEMENT / MOLECULAR REPLACEMENT /  molecular replacement / Resolution: 1.1 Å molecular replacement / Resolution: 1.1 Å | ||||||
 Authors Authors | Langan, P. / Wan, Q. / Coates, L. / Kovalevsky, A. | ||||||
 Citation Citation |  Journal: Acta Crystallogr.,Sect.D / Year: 2014 Journal: Acta Crystallogr.,Sect.D / Year: 2014Title: X-ray crystallographic studies of family 11 xylanase Michaelis and product complexes: implications for the catalytic mechanism. Authors: Wan, Q. / Zhang, Q. / Hamilton-Brehm, S. / Weiss, K. / Mustyakimov, M. / Coates, L. / Langan, P. / Graham, D. / Kovalevsky, A. | ||||||
| History |
|
- Structure visualization
Structure visualization
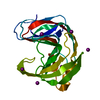
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  4hkl.cif.gz 4hkl.cif.gz | 129 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb4hkl.ent.gz pdb4hkl.ent.gz | 101.8 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  4hkl.json.gz 4hkl.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/hk/4hkl https://data.pdbj.org/pub/pdb/validation_reports/hk/4hkl ftp://data.pdbj.org/pub/pdb/validation_reports/hk/4hkl ftp://data.pdbj.org/pub/pdb/validation_reports/hk/4hkl | HTTPS FTP |
|---|
-Related structure data
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| Unit cell |
| ||||||||
| Details | biological unit is the same as asym. |
- Components
Components
| #1: Protein |  Xylanase / Xylanase 2 / 1 / 4-beta-D-xylan xylanohydrolase 2 Xylanase / Xylanase 2 / 1 / 4-beta-D-xylan xylanohydrolase 2Mass: 20751.381 Da / Num. of mol.: 1 / Mutation: N76H Source method: isolated from a genetically manipulated source Source: (gene. exp.)   Trichoderma reesei (fungus) / Gene: xyn2 / Plasmid: pJexpress401 / Production host: Trichoderma reesei (fungus) / Gene: xyn2 / Plasmid: pJexpress401 / Production host:   Escherichia coli (E. coli) / Strain (production host): BL21(DE3) / References: UniProt: P36217, Escherichia coli (E. coli) / Strain (production host): BL21(DE3) / References: UniProt: P36217,  endo-1,4-beta-xylanase endo-1,4-beta-xylanase | ||
|---|---|---|---|
| #2: Chemical | ChemComp-IOD /  Iodide Iodide#3: Water | ChemComp-HOH / |  Water Water |
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 2.4 Å3/Da / Density % sol: 48.65 % |
|---|---|
Crystal grow | Temperature: 298 K / Method: vapor diffusion / pH: 7 Details: 15-20 % PEG 8,000, 0.2 M NaI, 0.1 M MES, pH6.0 , pH 7.0, VAPOR DIFFUSION, temperature 298K |
-Data collection
| Diffraction | Mean temperature: 100 K | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  APS APS  / Beamline: 19-ID / Wavelength: 0.9793 Å / Beamline: 19-ID / Wavelength: 0.9793 Å | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Detector | Type: ADSC QUANTUM 315 / Detector: CCD / Date: Jun 28, 2012 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Radiation | Protocol: SINGLE WAVELENGTH / Scattering type: x-ray | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Radiation wavelength | Wavelength : 0.9793 Å / Relative weight: 1 : 0.9793 Å / Relative weight: 1 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Reflection | Resolution: 1.1→15 Å / Num. obs: 81313 / % possible obs: 99.8 % / Redundancy: 4.3 % / Rmerge(I) obs: 0.051 / Χ2: 1.02 / Net I/σ(I): 9.4 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Reflection shell |
|
-Phasing
Phasing | Method:  molecular replacement molecular replacement |
|---|
- Processing
Processing
| Software |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure : :  MOLECULAR REPLACEMENT / Resolution: 1.1→15 Å / Occupancy max: 1 / Occupancy min: 0.14 / FOM work R set: 0.9465 / SU ML: 0.08 / σ(F): 1.34 / Phase error: 10.43 / Stereochemistry target values: ML MOLECULAR REPLACEMENT / Resolution: 1.1→15 Å / Occupancy max: 1 / Occupancy min: 0.14 / FOM work R set: 0.9465 / SU ML: 0.08 / σ(F): 1.34 / Phase error: 10.43 / Stereochemistry target values: ML
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Solvent computation | Shrinkage radii: 0.9 Å / VDW probe radii: 1.11 Å / Solvent model: FLAT BULK SOLVENT MODEL | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | Biso max: 36.07 Å2 / Biso mean: 12.8405 Å2 / Biso min: 6.31 Å2 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: LAST / Resolution: 1.1→15 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell | Refine-ID: X-RAY DIFFRACTION / Total num. of bins used: 29
|
 Movie
Movie Controller
Controller



















 PDBj
PDBj



