[English] 日本語
 Yorodumi
Yorodumi- PDB-3vwb: Crystal structure of VirB core domain (Se-Met derivative) complex... -
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 3vwb | ||||||
|---|---|---|---|---|---|---|---|
| Title | Crystal structure of VirB core domain (Se-Met derivative) complexed with the cis-acting site (5-BRU modifications) upstream icsb promoter | ||||||
 Components Components |
| ||||||
 Keywords Keywords | TRANSCRIPTION/DNA / HTH DNA binding motif / dsDNA / Palindromic DNA sequence / ParB like / HTH DNA-binding motif / transcriptional activator / sequence specific dsDNA binding / TRANSCRIPTION-DNA complex | ||||||
| Function / homology |  Function and homology information Function and homology information | ||||||
| Biological species |  Shigella flexneri 2a (bacteria) Shigella flexneri 2a (bacteria) | ||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  SAD / Resolution: 2.416 Å SAD / Resolution: 2.416 Å | ||||||
 Authors Authors | Gao, X.P. / Waltersperger, S. / Wang, M.T. / Cui, S. | ||||||
 Citation Citation |  Journal: Nucleic Acids Res. / Year: 2013 Journal: Nucleic Acids Res. / Year: 2013Title: Structural insights into VirB-DNA complexes reveal mechanism of transcriptional activation of virulence genes Authors: Gao, X.P. / Zou, T.T. / Mu, Z.X. / Qin, B. / Yang, J. / Waltersperger, S. / Wang, M.T. / Cui, S. / Jin, Q. | ||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  3vwb.cif.gz 3vwb.cif.gz | 153.7 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb3vwb.ent.gz pdb3vwb.ent.gz | 121.7 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  3vwb.json.gz 3vwb.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Summary document |  3vwb_validation.pdf.gz 3vwb_validation.pdf.gz | 447.8 KB | Display |  wwPDB validaton report wwPDB validaton report |
|---|---|---|---|---|
| Full document |  3vwb_full_validation.pdf.gz 3vwb_full_validation.pdf.gz | 453.8 KB | Display | |
| Data in XML |  3vwb_validation.xml.gz 3vwb_validation.xml.gz | 10.4 KB | Display | |
| Data in CIF |  3vwb_validation.cif.gz 3vwb_validation.cif.gz | 13.2 KB | Display | |
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/vw/3vwb https://data.pdbj.org/pub/pdb/validation_reports/vw/3vwb ftp://data.pdbj.org/pub/pdb/validation_reports/vw/3vwb ftp://data.pdbj.org/pub/pdb/validation_reports/vw/3vwb | HTTPS FTP |
-Related structure data
- Links
Links
- Assembly
Assembly
| Deposited unit | 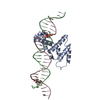
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| Unit cell |
|
- Components
Components
| #1: Protein | Mass: 16254.703 Da / Num. of mol.: 1 / Fragment: UNP residues 129-250 Source method: isolated from a genetically manipulated source Source: (gene. exp.)  Shigella flexneri 2a (bacteria) / Strain: 301 / Gene: virB / Plasmid: pET-28a / Production host: Shigella flexneri 2a (bacteria) / Strain: 301 / Gene: virB / Plasmid: pET-28a / Production host:  |
|---|---|
| #2: DNA chain | Mass: 8004.859 Da / Num. of mol.: 1 / Source method: obtained synthetically / Details: synthetic DNA with two internal Br-dU labels |
| #3: DNA chain | Mass: 8097.236 Da / Num. of mol.: 1 / Source method: obtained synthetically / Details: synthetic DNA |
| #4: Water | ChemComp-HOH / |
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 2.86 Å3/Da / Density % sol: 56.95 % Description: THE ENTRY CONTAINS FRIEDEL PAIRS IN F_PLUS/MINUS COLUMNS. |
|---|---|
| Crystal grow | Temperature: 295 K / Method: vapor diffusion, hanging drop / pH: 4.5 Details: 0.1M MgCl2, 0.1M Sodium Acetate, 22% PEG400, 3%(v/v) dimethyl sulfoxide, pH 4.5, VAPOR DIFFUSION, HANGING DROP, temperature 295K |
-Data collection
| Diffraction | Mean temperature: 100 K |
|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  SLS SLS  / Beamline: X06DA / Wavelength: 0.9792 Å / Beamline: X06DA / Wavelength: 0.9792 Å |
| Detector | Type: RAYONIX MX-225 / Detector: CCD / Date: Aug 5, 2011 |
| Radiation | Monochromator: Bartels Monochromator Crystal Type Si (111) / Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray |
| Radiation wavelength | Wavelength: 0.9792 Å / Relative weight: 1 |
| Reflection | Resolution: 2.416→46.891 Å / Num. all: 27467 / Num. obs: 27467 / % possible obs: 99.8 % / Observed criterion σ(F): -3 / Observed criterion σ(I): -3 / Redundancy: 7.77 % / Biso Wilson estimate: 46.5 Å2 / Rmerge(I) obs: 0.067 / Net I/σ(I): 21.56 |
| Reflection shell | Resolution: 2.42→2.56 Å / Redundancy: 7.54 % / Rmerge(I) obs: 0.768 / Mean I/σ(I) obs: 2.43 / Num. unique all: 4363 / % possible all: 98.8 |
- Processing
Processing
| Software |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure:  SAD / Resolution: 2.416→46.891 Å / Occupancy max: 1 / Occupancy min: 1 / FOM work R set: 0.7987 / SU ML: 0.41 / Cross valid method: THROUGHOUT / σ(F): 1.99 / Phase error: 26.83 / Stereochemistry target values: ML SAD / Resolution: 2.416→46.891 Å / Occupancy max: 1 / Occupancy min: 1 / FOM work R set: 0.7987 / SU ML: 0.41 / Cross valid method: THROUGHOUT / σ(F): 1.99 / Phase error: 26.83 / Stereochemistry target values: MLDetails: THE ENTRY CONTAINS FRIEDEL PAIRS IN F_PLUS/MINUS COLUMNS.
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Solvent computation | Shrinkage radii: 0.98 Å / VDW probe radii: 1.2 Å / Solvent model: FLAT BULK SOLVENT MODEL. / Bsol: 31.73 Å2 / ksol: 0.301 e/Å3 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | Biso max: 190.73 Å2 / Biso mean: 68.9097 Å2 / Biso min: 13.81 Å2
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: LAST / Resolution: 2.416→46.891 Å
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell | Refine-ID: X-RAY DIFFRACTION / Total num. of bins used: 10
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS params. | Method: refined / Refine-ID: X-RAY DIFFRACTION
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS group |
|
 Movie
Movie Controller
Controller















 PDBj
PDBj







































