+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 3ldb | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | Structure of JMJD6 complexd with ALPHA-KETOGLUTARATE and Fab Fragment. | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード |  IMMUNE SYSTEM (免疫系) / JMJ6D / IMMUNE SYSTEM (免疫系) / JMJ6D /  ALPHA-KETOGLUTARATE (Α-ケトグルタル酸) / Fab Fragments ALPHA-KETOGLUTARATE (Α-ケトグルタル酸) / Fab Fragments | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報peptidyl-lysine hydroxylation to 5-hydroxy-L-lysine / histone H3R2 demethylase activity / peptidyl-lysine 5-dioxygenase activity / histone H4R3 demethylase activity / protein demethylase activity / recognition of apoptotic cell / negative regulation of protein homooligomerization / oxidative RNA demethylation / oxidative RNA demethylase activity /  酸化還元酵素; 電子対供与作用を持つ; 分子酸素を取り込むないしは分子酸素を還元する; 2-オキソグルタル酸類を片方の電子供与体とする; 酸素分をそれぞれの電子供与体に取り込む ...peptidyl-lysine hydroxylation to 5-hydroxy-L-lysine / histone H3R2 demethylase activity / peptidyl-lysine 5-dioxygenase activity / histone H4R3 demethylase activity / protein demethylase activity / recognition of apoptotic cell / negative regulation of protein homooligomerization / oxidative RNA demethylation / oxidative RNA demethylase activity / 酸化還元酵素; 電子対供与作用を持つ; 分子酸素を取り込むないしは分子酸素を還元する; 2-オキソグルタル酸類を片方の電子供与体とする; 酸素分をそれぞれの電子供与体に取り込む ...peptidyl-lysine hydroxylation to 5-hydroxy-L-lysine / histone H3R2 demethylase activity / peptidyl-lysine 5-dioxygenase activity / histone H4R3 demethylase activity / protein demethylase activity / recognition of apoptotic cell / negative regulation of protein homooligomerization / oxidative RNA demethylation / oxidative RNA demethylase activity /  酸化還元酵素; 電子対供与作用を持つ; 分子酸素を取り込むないしは分子酸素を還元する; 2-オキソグルタル酸類を片方の電子供与体とする; 酸素分をそれぞれの電子供与体に取り込む / 酸化還元酵素; 電子対供与作用を持つ; 分子酸素を取り込むないしは分子酸素を還元する; 2-オキソグルタル酸類を片方の電子供与体とする; 酸素分をそれぞれの電子供与体に取り込む /  マクロファージ / non-membrane-bounded organelle assembly / transcription regulator activator activity / マクロファージ / non-membrane-bounded organelle assembly / transcription regulator activator activity /  regulation of mRNA splicing, via spliceosome / regulation of mRNA splicing, via spliceosome /  血管新生 / 血管新生 /  ヒドロキシル化 / erythrocyte development / P-TEFb complex binding / histone demethylase activity / ヒドロキシル化 / erythrocyte development / P-TEFb complex binding / histone demethylase activity /  食作用 / 食作用 /  RNA splicing / RNA splicing /  kidney development / lung development / protein homooligomerization / HDMs demethylate histones / kidney development / lung development / protein homooligomerization / HDMs demethylate histones /  転写後修飾 / retina development in camera-type eye / 転写後修飾 / retina development in camera-type eye /  signaling receptor activity / signaling receptor activity /  heart development / T cell differentiation in thymus / heart development / T cell differentiation in thymus /  single-stranded RNA binding / cell surface receptor signaling pathway / single-stranded RNA binding / cell surface receptor signaling pathway /  クロマチンリモデリング / クロマチンリモデリング /  ribonucleoprotein complex / iron ion binding / ribonucleoprotein complex / iron ion binding /  核小体 / positive regulation of DNA-templated transcription / positive regulation of transcription by RNA polymerase II / 核小体 / positive regulation of DNA-templated transcription / positive regulation of transcription by RNA polymerase II /  RNA binding / RNA binding /  核質 / identical protein binding / 核質 / identical protein binding /  細胞核 / 細胞核 /  細胞膜 / 細胞膜 /  細胞質基質 / 細胞質基質 /  細胞質 細胞質類似検索 - 分子機能 | ||||||
| 生物種 |   Homo sapiens (ヒト) Homo sapiens (ヒト) Cricetulus migratorius (ネズミ) Cricetulus migratorius (ネズミ) | ||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 2.7 Å 分子置換 / 解像度: 2.7 Å | ||||||
 データ登録者 データ登録者 | Hong, X. / Zang, J. / White, J. / Kappler, J.W. / Wang, C. / Zhang, G. | ||||||
 引用 引用 |  ジャーナル: Proc.Natl.Acad.Sci.USA / 年: 2010 ジャーナル: Proc.Natl.Acad.Sci.USA / 年: 2010タイトル: Interaction of JMJD6 with single-stranded RNA. 著者: Hong, X. / Zang, J. / White, J. / Wang, C. / Pan, C.H. / Zhao, R. / Murphy, R.C. / Dai, S. / Henson, P. / Kappler, J.W. / Hagman, J. / Zhang, G. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  3ldb.cif.gz 3ldb.cif.gz | 169.4 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb3ldb.ent.gz pdb3ldb.ent.gz | 132.8 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  3ldb.json.gz 3ldb.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/ld/3ldb https://data.pdbj.org/pub/pdb/validation_reports/ld/3ldb ftp://data.pdbj.org/pub/pdb/validation_reports/ld/3ldb ftp://data.pdbj.org/pub/pdb/validation_reports/ld/3ldb | HTTPS FTP |
|---|
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| 単位格子 |
|
- 要素
要素
-タンパク質 , 1種, 1分子 A
| #1: タンパク質 | 分子量: 39437.746 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)   Homo sapiens (ヒト) / 遺伝子: JMJD6, JMJD6 (1-403), KIAA0585, PTDSR / プラスミド: pET23b / 発現宿主: Homo sapiens (ヒト) / 遺伝子: JMJD6, JMJD6 (1-403), KIAA0585, PTDSR / プラスミド: pET23b / 発現宿主:   Escherichia coli (大腸菌) / 株 (発現宿主): BL21 Escherichia coli (大腸菌) / 株 (発現宿主): BL21参照: UniProt: Q6NYC1, 酸化還元酵素; 電子対供与作用を持つ; 分子酸素を取り込むないしは分子酸素を還元する; 2- ...参照: UniProt: Q6NYC1,  酸化還元酵素; 電子対供与作用を持つ; 分子酸素を取り込むないしは分子酸素を還元する; 2-オキソグルタル酸類を片方の電子供与体とする; 酸素分をそれぞれの電子供与体に取り込む 酸化還元酵素; 電子対供与作用を持つ; 分子酸素を取り込むないしは分子酸素を還元する; 2-オキソグルタル酸類を片方の電子供与体とする; 酸素分をそれぞれの電子供与体に取り込む |
|---|
-抗体 , 2種, 2分子 BC
| #2: 抗体 | 分子量: 24100.004 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)  Cricetulus migratorius (ネズミ) / Cell: hybridoma / 発現宿主: Cricetulus migratorius (ネズミ) / Cell: hybridoma / 発現宿主:  Cricetulus migratorius (ネズミ) Cricetulus migratorius (ネズミ) |
|---|---|
| #3: 抗体 | 分子量: 24007.662 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)  Cricetulus migratorius (ネズミ) / Cell: hybridoma / 発現宿主: Cricetulus migratorius (ネズミ) / Cell: hybridoma / 発現宿主:  Cricetulus migratorius (ネズミ) Cricetulus migratorius (ネズミ) |
-非ポリマー , 5種, 28分子 

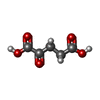






| #4: 化合物 | ChemComp-GOL /  グリセリン グリセリン#5: 化合物 | ChemComp-SO4 /  硫酸塩 硫酸塩#6: 化合物 | ChemComp-AKG / |  Α-ケトグルタル酸 Α-ケトグルタル酸#7: 化合物 | ChemComp-FE / |  鉄 鉄#8: 化合物 |  水銀 水銀 |
|---|
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 3 X線回折 / 使用した結晶の数: 3 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 5.02 Å3/Da / 溶媒含有率: 75.5 % |
|---|---|
結晶化 | 温度: 277 K / 手法: 蒸気拡散法, ハンギングドロップ法 / pH: 5.6 詳細: 0.1 M Bis(2-hydroxyethyl)-amino-tris(hydroxymethyl)-methane, 2.1 M Ammonium Sulphate, pH 5.6, VAPOR DIFFUSION, HANGING DROP, temperature 277K |
-データ収集
| 回折 |
| |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 放射光源 |
| |||||||||||||||
| 検出器 |
| |||||||||||||||
| 放射 |
| |||||||||||||||
| 放射波長 | 波長 : 1 Å / 相対比: 1 : 1 Å / 相対比: 1 | |||||||||||||||
| 反射 | 解像度: 2.61→99 Å / Num. all: 54702 / Num. obs: 48696 / % possible obs: 89 % / Biso Wilson estimate: 66.1 Å2 |
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法 : :  分子置換 分子置換開始モデル: PDB entries 3LD8, JMJD6, and Fab Fragment 解像度: 2.7→47.28 Å / Rfactor Rfree error: 0.006 / Data cutoff high absF: 3487182.74 / Data cutoff low absF: 0 / Isotropic thermal model: RESTRAINED / 交差検証法: THROUGHOUT / σ(F): 0 / 詳細: BULK SOLVENT MODEL USED
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | 溶媒モデル: FLAT MODEL / Bsol: 58.7914 Å2 / ksol: 0.35 e/Å3 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 83.5 Å2
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine analyze |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 2.7→47.28 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints NCS | NCS model details: NONE | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS精密化 シェル | 解像度: 2.7→2.87 Å / Rfactor Rfree error: 0.039 / Total num. of bins used: 6
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Xplor file |
|
 ムービー
ムービー コントローラー
コントローラー














 PDBj
PDBj























