+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 2rfm | ||||||
|---|---|---|---|---|---|---|---|
| Title | Structure of a Thermophilic Ankyrin Repeat Protein | ||||||
 Components Components | Putative ankyrin repeat protein TV1425 | ||||||
 Keywords Keywords |  PROTEIN BINDING / PROTEIN BINDING /  Ankyrin Repeat / ANK repeat Ankyrin Repeat / ANK repeat | ||||||
| Function / homology |  Function and homology information Function and homology informationAnkyrin repeats (many copies) / Domain of unknown function DUF3447 / Ankyrin repeat-containing domain / Ankyrin repeats (3 copies) / Ankyrin repeat profile. / Ankyrin repeat region circular profile. / ankyrin repeats /  Ankyrin repeat / Ankyrin repeat-containing domain superfamily / Serine Threonine Protein Phosphatase 5, Tetratricopeptide repeat ...Ankyrin repeats (many copies) / Domain of unknown function DUF3447 / Ankyrin repeat-containing domain / Ankyrin repeats (3 copies) / Ankyrin repeat profile. / Ankyrin repeat region circular profile. / ankyrin repeats / Ankyrin repeat / Ankyrin repeat-containing domain superfamily / Serine Threonine Protein Phosphatase 5, Tetratricopeptide repeat ...Ankyrin repeats (many copies) / Domain of unknown function DUF3447 / Ankyrin repeat-containing domain / Ankyrin repeats (3 copies) / Ankyrin repeat profile. / Ankyrin repeat region circular profile. / ankyrin repeats /  Ankyrin repeat / Ankyrin repeat-containing domain superfamily / Serine Threonine Protein Phosphatase 5, Tetratricopeptide repeat / Ankyrin repeat / Ankyrin repeat-containing domain superfamily / Serine Threonine Protein Phosphatase 5, Tetratricopeptide repeat /  Alpha Horseshoe / Mainly Alpha Alpha Horseshoe / Mainly AlphaSimilarity search - Domain/homology | ||||||
| Biological species |    Thermoplasma volcanium (archaea) Thermoplasma volcanium (archaea) | ||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  SAD / Resolution: 1.65 Å SAD / Resolution: 1.65 Å | ||||||
 Authors Authors | Loew, C. / Weininger, U. / Neumann, P. / Stubbs, M.T. / Balbach, J. | ||||||
 Citation Citation |  Journal: Proc.Natl.Acad.Sci.Usa / Year: 2008 Journal: Proc.Natl.Acad.Sci.Usa / Year: 2008Title: Structural insights into an equilibrium folding intermediate of an archaeal ankyrin repeat protein Authors: Loew, C. / Weininger, U. / Neumann, P. / Klepsch, M. / Lilie, H. / Stubbs, M.T. / Balbach, J. | ||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  2rfm.cif.gz 2rfm.cif.gz | 177.6 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb2rfm.ent.gz pdb2rfm.ent.gz | 142.9 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  2rfm.json.gz 2rfm.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/rf/2rfm https://data.pdbj.org/pub/pdb/validation_reports/rf/2rfm ftp://data.pdbj.org/pub/pdb/validation_reports/rf/2rfm ftp://data.pdbj.org/pub/pdb/validation_reports/rf/2rfm | HTTPS FTP |
|---|
-Related structure data
| Similar structure data |
|---|
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 1 | 
| |||||||||
| 2 | 
| |||||||||
| 3 | 
| |||||||||
| 4 | 
| |||||||||
| Unit cell |
| |||||||||
| Components on special symmetry positions |
|
- Components
Components
-Protein , 1 types, 2 molecules AB
| #1: Protein |  Mass: 21622.680 Da / Num. of mol.: 2 Source method: isolated from a genetically manipulated source Source: (gene. exp.)    Thermoplasma volcanium (archaea) / Gene: TVG1472127 / Plasmid: pet28c / Species (production host): Escherichia coli / Production host: Thermoplasma volcanium (archaea) / Gene: TVG1472127 / Plasmid: pet28c / Species (production host): Escherichia coli / Production host:   Escherichia coli BL21 (bacteria) / Strain (production host): BL21 / References: UniProt: Q978J0 Escherichia coli BL21 (bacteria) / Strain (production host): BL21 / References: UniProt: Q978J0 |
|---|
-Non-polymers , 6 types, 501 molecules 
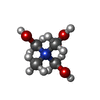
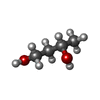








| #2: Chemical | ChemComp-SO4 /  Sulfate Sulfate#3: Chemical | ChemComp-144 / | #4: Chemical | ChemComp-BU2 /  1,3-Butanediol 1,3-Butanediol#5: Chemical | ChemComp-GOL /  Glycerol Glycerol#6: Chemical |  Chloride Chloride#7: Water | ChemComp-HOH / |  Water Water |
|---|
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 2 X-RAY DIFFRACTION / Number of used crystals: 2 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 2.97 Å3/Da / Density % sol: 58.59 % |
|---|---|
Crystal grow | Temperature: 286 K / Method: vapor diffusion, hanging drop / pH: 7.4 Details: 20% Glycerol, 2M Ammoniumsulfate, 1% 1,3-butanediole, 20mM HEPES, pH 7.4, VAPOR DIFFUSION, HANGING DROP, temperature 286K |
-Data collection
| Diffraction |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Diffraction source |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Detector |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Radiation |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Radiation wavelength |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Reflection | Redundancy: 15.4 % / Av σ(I) over netI: 5.4 / Number: 715122 / Rmerge(I) obs: 0.089 / Rsym value: 0.089 / D res high: 1.83 Å / D res low: 174.483 Å / Num. obs: 46388 / % possible obs: 98.5 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Diffraction reflection shell |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Reflection | Resolution: 1.65→48.472 Å / Num. obs: 58965 / % possible obs: 93 % / Observed criterion σ(F): 3 / Observed criterion σ(I): 3 / Redundancy: 9.9 % / Biso Wilson estimate: 19.96 Å2 / Rmerge(I) obs: 0.055 / Rsym value: 0.055 / Net I/σ(I): 7.2 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Reflection shell | Diffraction-ID: 1,2
|
-Phasing
Phasing | Method:  SAD SAD |
|---|
- Processing
Processing
| Software |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure : :  SAD / Resolution: 1.65→20 Å / Cor.coef. Fo:Fc: 0.967 / Cor.coef. Fo:Fc free: 0.96 / SU B: 2.349 / SU ML: 0.043 / Isotropic thermal model: Isotropic / Cross valid method: THROUGHOUT / σ(F): 0 / σ(I): 0 / ESU R: 0.081 / ESU R Free: 0.079 / Stereochemistry target values: MAXIMUM LIKELIHOOD / Details: TLS refinement - 1 group for every molecule. SAD / Resolution: 1.65→20 Å / Cor.coef. Fo:Fc: 0.967 / Cor.coef. Fo:Fc free: 0.96 / SU B: 2.349 / SU ML: 0.043 / Isotropic thermal model: Isotropic / Cross valid method: THROUGHOUT / σ(F): 0 / σ(I): 0 / ESU R: 0.081 / ESU R Free: 0.079 / Stereochemistry target values: MAXIMUM LIKELIHOOD / Details: TLS refinement - 1 group for every molecule.
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Solvent computation | Ion probe radii: 0.8 Å / Shrinkage radii: 0.8 Å / VDW probe radii: 1.2 Å / Solvent model: BABINET MODEL WITH MASK | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | Biso mean: 45.827 Å2
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine analyze |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: LAST / Resolution: 1.65→20 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell | Resolution: 1.65→1.693 Å / Total num. of bins used: 20
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS params. | Method: refined / Refine-ID: X-RAY DIFFRACTION
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS group |
|
 Movie
Movie Controller
Controller













 PDBj
PDBj





