+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 1n72 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
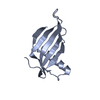
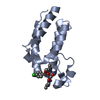
| タイトル | Structure and Ligand of a Histone Acetyltransferase Bromodomain | |||||||||
 要素 要素 | HISTONE ACETYLTRANSFERASE ヒストンアセチルトランスフェラーゼ ヒストンアセチルトランスフェラーゼ | |||||||||
 キーワード キーワード |  TRANSFERASE (転移酵素) / Histone acetyltransferase bromodomain / 4-helical bundle TRANSFERASE (転移酵素) / Histone acetyltransferase bromodomain / 4-helical bundle | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報regulation of protein ADP-ribosylation / negative regulation of rRNA processing / histone H3K9 acetyltransferase activity /  diamine N-acetyltransferase / diamine N-acetyltransferase /  diamine N-acetyltransferase activity / positive regulation of transcription from RNA polymerase II promoter by glucose / negative regulation of centriole replication / Physiological factors / positive regulation of attachment of mitotic spindle microtubules to kinetochore / peptidyl-lysine acetylation ...regulation of protein ADP-ribosylation / negative regulation of rRNA processing / histone H3K9 acetyltransferase activity / diamine N-acetyltransferase activity / positive regulation of transcription from RNA polymerase II promoter by glucose / negative regulation of centriole replication / Physiological factors / positive regulation of attachment of mitotic spindle microtubules to kinetochore / peptidyl-lysine acetylation ...regulation of protein ADP-ribosylation / negative regulation of rRNA processing / histone H3K9 acetyltransferase activity /  diamine N-acetyltransferase / diamine N-acetyltransferase /  diamine N-acetyltransferase activity / positive regulation of transcription from RNA polymerase II promoter by glucose / negative regulation of centriole replication / Physiological factors / positive regulation of attachment of mitotic spindle microtubules to kinetochore / peptidyl-lysine acetylation / lysine N-acetyltransferase activity, acting on acetyl phosphate as donor / YAP1- and WWTR1 (TAZ)-stimulated gene expression / positive regulation of fatty acid biosynthetic process / diamine N-acetyltransferase activity / positive regulation of transcription from RNA polymerase II promoter by glucose / negative regulation of centriole replication / Physiological factors / positive regulation of attachment of mitotic spindle microtubules to kinetochore / peptidyl-lysine acetylation / lysine N-acetyltransferase activity, acting on acetyl phosphate as donor / YAP1- and WWTR1 (TAZ)-stimulated gene expression / positive regulation of fatty acid biosynthetic process /  ミオフィラメント / histone H3 acetyltransferase activity / internal peptidyl-lysine acetylation / cyclin-dependent protein serine/threonine kinase inhibitor activity / N-terminal peptidyl-lysine acetylation / ミオフィラメント / histone H3 acetyltransferase activity / internal peptidyl-lysine acetylation / cyclin-dependent protein serine/threonine kinase inhibitor activity / N-terminal peptidyl-lysine acetylation /  ATAC complex / I band / cellular response to parathyroid hormone stimulus / ATAC complex / I band / cellular response to parathyroid hormone stimulus /  Regulation of gene expression in late stage (branching morphogenesis) pancreatic bud precursor cells / SAGA complex / RUNX3 regulates NOTCH signaling / Regulation of gene expression in late stage (branching morphogenesis) pancreatic bud precursor cells / SAGA complex / RUNX3 regulates NOTCH signaling /  limb development / A band / NOTCH4 Intracellular Domain Regulates Transcription / Regulation of FOXO transcriptional activity by acetylation / NOTCH3 Intracellular Domain Regulates Transcription / regulation of tubulin deacetylation / peptide-lysine-N-acetyltransferase activity / limb development / A band / NOTCH4 Intracellular Domain Regulates Transcription / Regulation of FOXO transcriptional activity by acetylation / NOTCH3 Intracellular Domain Regulates Transcription / regulation of tubulin deacetylation / peptide-lysine-N-acetyltransferase activity /  histone acetyltransferase binding / histone acetyltransferase binding /  protein acetylation / Notch-HLH transcription pathway / Formation of WDR5-containing histone-modifying complexes / protein acetylation / Notch-HLH transcription pathway / Formation of WDR5-containing histone-modifying complexes /  regulation of cell division / Formation of paraxial mesoderm / regulation of cell division / Formation of paraxial mesoderm /  acetyltransferase activity / RNA Polymerase I Transcription Initiation / acetyltransferase activity / RNA Polymerase I Transcription Initiation /  regulation of RNA splicing / regulation of RNA splicing /  regulation of embryonic development / regulation of embryonic development /  regulation of DNA repair / regulation of DNA repair /  histone acetyltransferase activity / positive regulation of gluconeogenesis / histone acetyltransferase activity / positive regulation of gluconeogenesis /  ヒストンアセチルトランスフェラーゼ / transcription initiation-coupled chromatin remodeling / positive regulation of glycolytic process / ヒストンアセチルトランスフェラーゼ / transcription initiation-coupled chromatin remodeling / positive regulation of glycolytic process /  糖新生 / 糖新生 /  transcription coregulator activity / RNA polymerase II transcription regulatory region sequence-specific DNA binding / RUNX1 regulates genes involved in megakaryocyte differentiation and platelet function / B-WICH complex positively regulates rRNA expression / transcription coregulator activity / RNA polymerase II transcription regulatory region sequence-specific DNA binding / RUNX1 regulates genes involved in megakaryocyte differentiation and platelet function / B-WICH complex positively regulates rRNA expression /  紡錘体 / NOTCH1 Intracellular Domain Regulates Transcription / Metalloprotease DUBs / 紡錘体 / NOTCH1 Intracellular Domain Regulates Transcription / Metalloprotease DUBs /  動原体 / 動原体 /  記憶 / Pre-NOTCH Transcription and Translation / Constitutive Signaling by NOTCH1 PEST Domain Mutants / Constitutive Signaling by NOTCH1 HD+PEST Domain Mutants / positive regulation of neuron projection development / 記憶 / Pre-NOTCH Transcription and Translation / Constitutive Signaling by NOTCH1 PEST Domain Mutants / Constitutive Signaling by NOTCH1 HD+PEST Domain Mutants / positive regulation of neuron projection development /  histone deacetylase binding / cellular response to insulin stimulus / histone deacetylase binding / cellular response to insulin stimulus /  vasodilation / rhythmic process / cellular response to oxidative stress / vasodilation / rhythmic process / cellular response to oxidative stress /  heart development / HATs acetylate histones / DNA-binding transcription factor binding / Estrogen-dependent gene expression / heart development / HATs acetylate histones / DNA-binding transcription factor binding / Estrogen-dependent gene expression /  transcription coactivator activity / transcription coactivator activity /  regulation of cell cycle / regulation of cell cycle /  クロマチンリモデリング / クロマチンリモデリング /  細胞周期 / negative regulation of cell population proliferation / 細胞周期 / negative regulation of cell population proliferation /  中心体 / 中心体 /  chromatin binding / regulation of DNA-templated transcription / regulation of transcription by RNA polymerase II / chromatin binding / regulation of DNA-templated transcription / regulation of transcription by RNA polymerase II /  protein kinase binding / positive regulation of DNA-templated transcription / negative regulation of transcription by RNA polymerase II / positive regulation of transcription by RNA polymerase II / protein-containing complex / protein kinase binding / positive regulation of DNA-templated transcription / negative regulation of transcription by RNA polymerase II / positive regulation of transcription by RNA polymerase II / protein-containing complex /  核質 / 核質 /  細胞核 / 細胞核 /  細胞質基質 細胞質基質類似検索 - 分子機能 | |||||||||
| 生物種 |   Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 |  溶液NMR / distance geometry simulated annealing, molecular dynamics matrix relaxation torsion angle dynamics 溶液NMR / distance geometry simulated annealing, molecular dynamics matrix relaxation torsion angle dynamics | |||||||||
 データ登録者 データ登録者 | Dhalluin, C. / Carlson, J.E. / Zeng, L. / He, C. / Aggarwal, A.K. / Zhou, M.-M. | |||||||||
 引用 引用 |  ジャーナル: Nature / 年: 1999 ジャーナル: Nature / 年: 1999タイトル: Structure and Ligand of a Histone Acetyltransferase Bromodomain 著者: Dhalluin, C. / Carlson, J.E. / Zeng, L. / He, C. / Aggarwal, A.K. / Zhou, M.-M. | |||||||||
| 履歴 |
| |||||||||
| Remark 999 | SEQUENCE The authors believe PRO is at both positions 804 and 805 in the wild protein sequence. |
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  1n72.cif.gz 1n72.cif.gz | 48.8 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb1n72.ent.gz pdb1n72.ent.gz | 34.7 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  1n72.json.gz 1n72.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/n7/1n72 https://data.pdbj.org/pub/pdb/validation_reports/n7/1n72 ftp://data.pdbj.org/pub/pdb/validation_reports/n7/1n72 ftp://data.pdbj.org/pub/pdb/validation_reports/n7/1n72 | HTTPS FTP |
|---|
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 1 |
| |||||||||
| NMR アンサンブル |
|
- 要素
要素
| #1: タンパク質 |  ヒストンアセチルトランスフェラーゼ / P300/CBP-associated factor / P/CAF / Histone acetylase PCAF ヒストンアセチルトランスフェラーゼ / P300/CBP-associated factor / P/CAF / Histone acetylase PCAF分子量: 14052.226 Da / 分子数: 1 / 断片: Bromodomain / 由来タイプ: 組換発現 / 由来: (組換発現)   Homo sapiens (ヒト) / 遺伝子: PCAF / プラスミド: pET14b / 生物種 (発現宿主): Escherichia coli / 発現宿主: Homo sapiens (ヒト) / 遺伝子: PCAF / プラスミド: pET14b / 生物種 (発現宿主): Escherichia coli / 発現宿主:   Escherichia coli BL21(DE3) (大腸菌) / 株 (発現宿主): BL21(DE3) Escherichia coli BL21(DE3) (大腸菌) / 株 (発現宿主): BL21(DE3)参照: UniProt: Q92831,  ヒストンアセチルトランスフェラーゼ ヒストンアセチルトランスフェラーゼ |
|---|
-実験情報
-実験
| 実験 | 手法:  溶液NMR 溶液NMR | ||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| NMR実験 |
|
- 試料調製
試料調製
| 詳細 | 内容: 1mM Bromodomain, 100mM Sodium phosphate, 5mM DTT-d10, 0.5mM EDTA, pH 6.5 溶媒系: 90% H2O/10% D2O |
|---|---|
| 試料状態 | イオン強度: 200 / pH: 6.5 / 圧: 1 atm / 温度: 303 K |
結晶化 | *PLUS 手法: その他 / 詳細: NMR |
-NMR測定
| 放射 | プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M | |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 放射波長 | 相対比: 1 | |||||||||||||||
| NMRスペクトロメーター |
|
- 解析
解析
| NMR software |
| |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 手法: distance geometry simulated annealing, molecular dynamics matrix relaxation torsion angle dynamics ソフトェア番号: 1 | |||||||||||||||
| NMRアンサンブル | 計算したコンフォーマーの数: 200 / 登録したコンフォーマーの数: 1 |
 ムービー
ムービー コントローラー
コントローラー











 PDBj
PDBj





