+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 1k5i | ||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
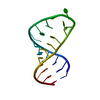
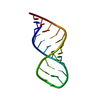
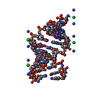
| タイトル | NMR Structure of a Ribosomal RNA Hairpin Containing a Conserved CUCAA Pentaloop | ||||||||||||||||||
 要素 要素 | 5'-R(P* キーワード キーワード RNA (リボ核酸) / CUCAA pentaloop / RNA hairpin / non standard base-base interaction RNA (リボ核酸) / CUCAA pentaloop / RNA hairpin / non standard base-base interaction機能・相同性 |  リボ核酸 / RNA (> 10) リボ核酸 / RNA (> 10) 機能・相同性情報 機能・相同性情報手法 |  溶液NMR / Distance Geometry, 溶液NMR / Distance Geometry,  Simulated Annealing, Restrained Molecular Dynamics Simulated Annealing, Restrained Molecular Dynamics  データ登録者 データ登録者Nagaswamy, U. / Gao, X. / Martinis, S.A. / Fox, G.E. |  引用 引用 ジャーナル: Nucleic Acids Res. / 年: 2001 ジャーナル: Nucleic Acids Res. / 年: 2001タイトル: NMR structure of a ribosomal RNA hairpin containing a conserved CUCAA pentaloop. 著者: Nagaswamy, U. / Gao, X. / Martinis, S.A. / Fox, G.E. 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  1k5i.cif.gz 1k5i.cif.gz | 145.8 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb1k5i.ent.gz pdb1k5i.ent.gz | 121.7 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  1k5i.json.gz 1k5i.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/k5/1k5i https://data.pdbj.org/pub/pdb/validation_reports/k5/1k5i ftp://data.pdbj.org/pub/pdb/validation_reports/k5/1k5i ftp://data.pdbj.org/pub/pdb/validation_reports/k5/1k5i | HTTPS FTP |
|---|
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 1 |
| |||||||||
| NMR アンサンブル |
|
- 要素
要素
| #1: RNA鎖 | 分子量: 7369.440 Da / 分子数: 1 / 断片: 16S ribosomal RNA fragment (612-628) / 由来タイプ: 合成 詳細: The oligonucleotide was synthesized by T7 run-off transcription. |
|---|
-実験情報
-実験
| 実験 | 手法:  溶液NMR 溶液NMR | ||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| NMR実験 |
|
- 試料調製
試料調製
| 詳細 |
| |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 試料状態 | イオン強度: 10 mM Sodium Phosphate / pH: 6.5 / 圧: ambient / 温度: 298 K | |||||||||
結晶化 | *PLUS 手法: その他 / 詳細: NMR |
-NMR測定
| 放射 | プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M |
|---|---|
| 放射波長 | 相対比: 1 |
| NMRスペクトロメーター | タイプ: Bruker AMX / 製造業者: Bruker / モデル : AMX / 磁場強度: 600 MHz : AMX / 磁場強度: 600 MHz |
- 解析
解析
| NMR software | 名称:  X-PLOR / バージョン: 3.1 / 開発者: Brunger / 分類: 精密化 X-PLOR / バージョン: 3.1 / 開発者: Brunger / 分類: 精密化 |
|---|---|
| 精密化 | 手法: Distance Geometry,  Simulated Annealing, Restrained Molecular Dynamics Simulated Annealing, Restrained Molecular Dynamicsソフトェア番号: 1 詳細: A total of 300 structures were calculated using distance geometry utilizing 123 experimentally derived distance restraints for the loop and 918 (258-experimental distances, 660-A form ...詳細: A total of 300 structures were calculated using distance geometry utilizing 123 experimentally derived distance restraints for the loop and 918 (258-experimental distances, 660-A form distances) distance restraints for the stem region and 143 dihedral angle restraints. Additionally, 50 distance restraints were used to maintain the Watson-Crick geometry of the base pairs in the stem region. Final refinement resulted in 10 lowest energy structures. |
| NMRアンサンブル | コンフォーマー選択の基準: structures with the lowest energy 計算したコンフォーマーの数: 33 / 登録したコンフォーマーの数: 10 |
 ムービー
ムービー コントローラー
コントローラー




 PDBj
PDBj





























