+ データを開く
データを開く
- 基本情報
基本情報
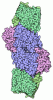
| 登録情報 | データベース: PDB / ID: 1g20 | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | MGATP-BOUND AND NUCLEOTIDE-FREE STRUCTURES OF A NITROGENASE PROTEIN COMPLEX BETWEEN LEU127DEL-FE PROTEIN AND THE MOFE PROTEIN | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード |  OXIDOREDUCTASE (酸化還元酵素) / nitrogen-fixation / Fe protein / MoFe protein / P-cluster and FeMo cofactor OXIDOREDUCTASE (酸化還元酵素) / nitrogen-fixation / Fe protein / MoFe protein / P-cluster and FeMo cofactor | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報molybdenum-iron nitrogenase complex /  ニトロゲナーゼ / carbonyl sulfide nitrogenase activity / ニトロゲナーゼ / carbonyl sulfide nitrogenase activity /  nitrogenase activity / nitrogenase activity /  窒素固定 / 窒素固定 /  iron-sulfur cluster binding / 4 iron, 4 sulfur cluster binding / iron-sulfur cluster binding / 4 iron, 4 sulfur cluster binding /  ATP binding / ATP binding /  metal ion binding metal ion binding類似検索 - 分子機能 | ||||||
| 生物種 |   Azotobacter vinelandii (窒素固定) Azotobacter vinelandii (窒素固定) | ||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 2.2 Å 分子置換 / 解像度: 2.2 Å | ||||||
 データ登録者 データ登録者 | Chiu, H.-J. / Peters, J.W. / Lanzilotta, W.N. / Ryle, M.J. / Seefeldt, L.C. / Howard, J.B. / Rees, D.C. | ||||||
 引用 引用 |  ジャーナル: Biochemistry / 年: 2001 ジャーナル: Biochemistry / 年: 2001タイトル: MgATP-Bound and nucleotide-free structures of a nitrogenase protein complex between the Leu 127 Delta-Fe-protein and the MoFe-protein. 著者: Chiu, H. / Peters, J.W. / Lanzilotta, W.N. / Ryle, M.J. / Seefeldt, L.C. / Howard, J.B. / Rees, D.C. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  1g20.cif.gz 1g20.cif.gz | 615.7 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb1g20.ent.gz pdb1g20.ent.gz | 499.3 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  1g20.json.gz 1g20.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/g2/1g20 https://data.pdbj.org/pub/pdb/validation_reports/g2/1g20 ftp://data.pdbj.org/pub/pdb/validation_reports/g2/1g20 ftp://data.pdbj.org/pub/pdb/validation_reports/g2/1g20 | HTTPS FTP |
|---|
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||||
| 単位格子 |
| ||||||||||
| 詳細 | The biological assembly is a dimer, and each subunit contains one MoeFe protein and two Fe protein monomers |
- 要素
要素
-NITROGENASE MOLYBDENUM-IRON PROTEIN ... , 2種, 4分子 ACBD
| #1: タンパク質 | 分子量: 55363.043 Da / 分子数: 2 / 由来タイプ: 天然 / 由来: (天然)   Azotobacter vinelandii (窒素固定) / 参照: UniProt: P07328, Azotobacter vinelandii (窒素固定) / 参照: UniProt: P07328,  ニトロゲナーゼ ニトロゲナーゼ#2: タンパク質 | 分子量: 59535.879 Da / 分子数: 2 / 由来タイプ: 天然 / 由来: (天然)   Azotobacter vinelandii (窒素固定) / 参照: UniProt: P07329, Azotobacter vinelandii (窒素固定) / 参照: UniProt: P07329,  ニトロゲナーゼ ニトロゲナーゼ |
|---|
-タンパク質 , 1種, 4分子 EFGH
| #3: タンパク質 | 分子量: 31435.084 Da / 分子数: 4 / 由来タイプ: 天然 / 由来: (天然)   Azotobacter vinelandii (窒素固定) / 参照: UniProt: P00459, Azotobacter vinelandii (窒素固定) / 参照: UniProt: P00459,  ニトロゲナーゼ ニトロゲナーゼ |
|---|
-非ポリマー , 6種, 1076分子 
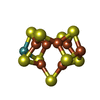

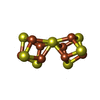





| #4: 化合物 | | #5: 化合物 | #6: 化合物 | #7: 化合物 | #8: 化合物 |  鉄・硫黄クラスター 鉄・硫黄クラスター#9: 水 | ChemComp-HOH / |  水 水 |
|---|
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.5 Å3/Da / 溶媒含有率: 50 % | ||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
結晶化 | 温度: 298 K / 手法: microcapillary batch diffusion / pH: 8.5 詳細: PEG 4000, sodium acetate, Tris-HCl. Ph 8.8, pH 8.5, microcapillary batch diffusion, temperature 298K | ||||||||||||||||||||||||||||||
| 結晶化 | *PLUS 手法: batch method | ||||||||||||||||||||||||||||||
| 溶液の組成 | *PLUS
|
-データ収集
| 回折 | 平均測定温度: 100 K |
|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  SSRL SSRL  / ビームライン: BL7-1 / 波長: 1.08 / ビームライン: BL7-1 / 波長: 1.08 |
| 検出器 | タイプ: MARRESEARCH / 検出器: IMAGE PLATE / 日付: 1998年4月20日 |
| 放射 | プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長 : 1.08 Å / 相対比: 1 : 1.08 Å / 相対比: 1 |
| 反射 | 解像度: 2.2→20 Å / Num. all: 167675 / Num. obs: 157699 / % possible obs: 89.1 % / Observed criterion σ(F): 1 / Observed criterion σ(I): 0.5 / 冗長度: 6.5 % / Rmerge(I) obs: 0.112 / Net I/σ(I): 15 |
| 反射 シェル | 解像度: 2.2→2.24 Å / 冗長度: 3.5 % / Rmerge(I) obs: 0.296 / % possible all: 83.2 |
| 反射 | *PLUS 最低解像度: 20 Å / % possible obs: 94.7 % / Num. measured all: 1092580 |
| 反射 シェル | *PLUS % possible obs: 83.2 % |
- 解析
解析
| ソフトウェア |
| |||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法 : :  分子置換 分子置換開始モデル: 2MIN 解像度: 2.2→20 Å / 交差検証法: THROUGHOUT / σ(F): 1 / σ(I): 0.5 / 立体化学のターゲット値: Engh & Huber
| |||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 2.2→20 Å
| |||||||||||||||||||||||||
| 拘束条件 |
| |||||||||||||||||||||||||
| ソフトウェア | *PLUS 名称: CNS / 分類: refinement | |||||||||||||||||||||||||
| 精密化 | *PLUS 最低解像度: 20 Å / σ(F): 1 / % reflection Rfree: 5 % / Rfactor obs: 0.219 | |||||||||||||||||||||||||
| 溶媒の処理 | *PLUS | |||||||||||||||||||||||||
| 原子変位パラメータ | *PLUS |
 ムービー
ムービー コントローラー
コントローラー
















 PDBj
PDBj