+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 7z8r | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
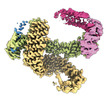
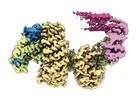
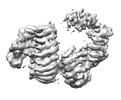
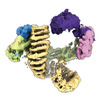
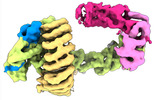
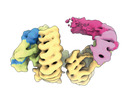
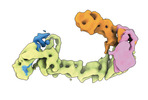
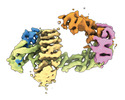
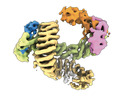
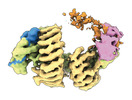
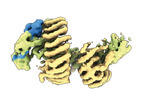
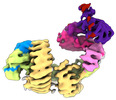
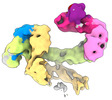
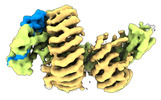
| タイトル | CAND1-CUL1-RBX1 | |||||||||
 要素 要素 |
| |||||||||
 キーワード キーワード |  LIGASE (リガーゼ) / cullin-RING E3 ubiquitin ligase / Assembly factor / CAND1 LIGASE (リガーゼ) / cullin-RING E3 ubiquitin ligase / Assembly factor / CAND1 | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報 SCF complex assembly / Parkin-FBXW7-Cul1 ubiquitin ligase complex / negative regulation of catalytic activity / cullin-RING-type E3 NEDD8 transferase / cellular response to chemical stress / NEDD8 transferase activity / cullin-RING ubiquitin ligase complex / Cul7-RING ubiquitin ligase complex / ubiquitin-dependent protein catabolic process via the C-end degron rule pathway / Loss of Function of FBXW7 in Cancer and NOTCH1 Signaling ... SCF complex assembly / Parkin-FBXW7-Cul1 ubiquitin ligase complex / negative regulation of catalytic activity / cullin-RING-type E3 NEDD8 transferase / cellular response to chemical stress / NEDD8 transferase activity / cullin-RING ubiquitin ligase complex / Cul7-RING ubiquitin ligase complex / ubiquitin-dependent protein catabolic process via the C-end degron rule pathway / Loss of Function of FBXW7 in Cancer and NOTCH1 Signaling ... SCF complex assembly / Parkin-FBXW7-Cul1 ubiquitin ligase complex / negative regulation of catalytic activity / cullin-RING-type E3 NEDD8 transferase / cellular response to chemical stress / NEDD8 transferase activity / cullin-RING ubiquitin ligase complex / Cul7-RING ubiquitin ligase complex / ubiquitin-dependent protein catabolic process via the C-end degron rule pathway / Loss of Function of FBXW7 in Cancer and NOTCH1 Signaling / positive regulation of protein autoubiquitination / protein neddylation / NEDD8 ligase activity / Cul5-RING ubiquitin ligase complex / ubiquitin-ubiquitin ligase activity / Cul4A-RING E3 ubiquitin ligase complex / SCF complex assembly / Parkin-FBXW7-Cul1 ubiquitin ligase complex / negative regulation of catalytic activity / cullin-RING-type E3 NEDD8 transferase / cellular response to chemical stress / NEDD8 transferase activity / cullin-RING ubiquitin ligase complex / Cul7-RING ubiquitin ligase complex / ubiquitin-dependent protein catabolic process via the C-end degron rule pathway / Loss of Function of FBXW7 in Cancer and NOTCH1 Signaling / positive regulation of protein autoubiquitination / protein neddylation / NEDD8 ligase activity / Cul5-RING ubiquitin ligase complex / ubiquitin-ubiquitin ligase activity / Cul4A-RING E3 ubiquitin ligase complex /  SCF複合体 / Cul2-RING ubiquitin ligase complex / negative regulation of type I interferon production / Cul4B-RING E3 ubiquitin ligase complex / ubiquitin ligase complex scaffold activity / SCF-dependent proteasomal ubiquitin-dependent protein catabolic process / Cul3-RING ubiquitin ligase complex / Prolactin receptor signaling / protein monoubiquitination / cullin family protein binding / Nuclear events stimulated by ALK signaling in cancer / positive regulation of RNA polymerase II transcription preinitiation complex assembly / protein K48-linked ubiquitination / SCF複合体 / Cul2-RING ubiquitin ligase complex / negative regulation of type I interferon production / Cul4B-RING E3 ubiquitin ligase complex / ubiquitin ligase complex scaffold activity / SCF-dependent proteasomal ubiquitin-dependent protein catabolic process / Cul3-RING ubiquitin ligase complex / Prolactin receptor signaling / protein monoubiquitination / cullin family protein binding / Nuclear events stimulated by ALK signaling in cancer / positive regulation of RNA polymerase II transcription preinitiation complex assembly / protein K48-linked ubiquitination /  ubiquitin ligase complex / positive regulation of TORC1 signaling / ubiquitin ligase complex / positive regulation of TORC1 signaling /  T細胞 / TBP-class protein binding / T細胞 / TBP-class protein binding /  Regulation of BACH1 activity / MAP3K8 (TPL2)-dependent MAPK1/3 activation / intrinsic apoptotic signaling pathway / Regulation of BACH1 activity / MAP3K8 (TPL2)-dependent MAPK1/3 activation / intrinsic apoptotic signaling pathway /  post-translational protein modification / SCF-beta-TrCP mediated degradation of Emi1 / NIK-->noncanonical NF-kB signaling / Degradation of DVL / Dectin-1 mediated noncanonical NF-kB signaling / Recognition of DNA damage by PCNA-containing replication complex / Degradation of GLI1 by the proteasome / Activation of NF-kappaB in B cells / Negative regulation of NOTCH4 signaling / animal organ morphogenesis / Iron uptake and transport / cellular response to amino acid stimulus / GSK3B and BTRC:CUL1-mediated-degradation of NFE2L2 / Vif-mediated degradation of APOBEC3G / Hedgehog 'on' state / DNA Damage Recognition in GG-NER / Degradation of GLI2 by the proteasome / GLI3 is processed to GLI3R by the proteasome / FBXL7 down-regulates AURKA during mitotic entry and in early mitosis / RING-type E3 ubiquitin transferase / Degradation of beta-catenin by the destruction complex / negative regulation of canonical Wnt signaling pathway / Oxygen-dependent proline hydroxylation of Hypoxia-inducible Factor Alpha / Dual Incision in GG-NER / G1/S transition of mitotic cell cycle / NOTCH1 Intracellular Domain Regulates Transcription / Transcription-Coupled Nucleotide Excision Repair (TC-NER) / Formation of TC-NER Pre-Incision Complex / CLEC7A (Dectin-1) signaling / SCF(Skp2)-mediated degradation of p27/p21 / Constitutive Signaling by NOTCH1 PEST Domain Mutants / Constitutive Signaling by NOTCH1 HD+PEST Domain Mutants / Regulation of expression of SLITs and ROBOs / Formation of Incision Complex in GG-NER / FCERI mediated NF-kB activation / Interleukin-1 signaling / Orc1 removal from chromatin / Dual incision in TC-NER / Gap-filling DNA repair synthesis and ligation in TC-NER / Regulation of RAS by GAPs / protein polyubiquitination / positive regulation of protein catabolic process / Regulation of RUNX2 expression and activity / Cyclin D associated events in G1 / cellular response to UV / KEAP1-NFE2L2 pathway / post-translational protein modification / SCF-beta-TrCP mediated degradation of Emi1 / NIK-->noncanonical NF-kB signaling / Degradation of DVL / Dectin-1 mediated noncanonical NF-kB signaling / Recognition of DNA damage by PCNA-containing replication complex / Degradation of GLI1 by the proteasome / Activation of NF-kappaB in B cells / Negative regulation of NOTCH4 signaling / animal organ morphogenesis / Iron uptake and transport / cellular response to amino acid stimulus / GSK3B and BTRC:CUL1-mediated-degradation of NFE2L2 / Vif-mediated degradation of APOBEC3G / Hedgehog 'on' state / DNA Damage Recognition in GG-NER / Degradation of GLI2 by the proteasome / GLI3 is processed to GLI3R by the proteasome / FBXL7 down-regulates AURKA during mitotic entry and in early mitosis / RING-type E3 ubiquitin transferase / Degradation of beta-catenin by the destruction complex / negative regulation of canonical Wnt signaling pathway / Oxygen-dependent proline hydroxylation of Hypoxia-inducible Factor Alpha / Dual Incision in GG-NER / G1/S transition of mitotic cell cycle / NOTCH1 Intracellular Domain Regulates Transcription / Transcription-Coupled Nucleotide Excision Repair (TC-NER) / Formation of TC-NER Pre-Incision Complex / CLEC7A (Dectin-1) signaling / SCF(Skp2)-mediated degradation of p27/p21 / Constitutive Signaling by NOTCH1 PEST Domain Mutants / Constitutive Signaling by NOTCH1 HD+PEST Domain Mutants / Regulation of expression of SLITs and ROBOs / Formation of Incision Complex in GG-NER / FCERI mediated NF-kB activation / Interleukin-1 signaling / Orc1 removal from chromatin / Dual incision in TC-NER / Gap-filling DNA repair synthesis and ligation in TC-NER / Regulation of RAS by GAPs / protein polyubiquitination / positive regulation of protein catabolic process / Regulation of RUNX2 expression and activity / Cyclin D associated events in G1 / cellular response to UV / KEAP1-NFE2L2 pathway /  Regulation of PLK1 Activity at G2/M Transition / Regulation of PLK1 Activity at G2/M Transition /  分裂促進因子活性化タンパク質キナーゼ / 分裂促進因子活性化タンパク質キナーゼ /  ubiquitin protein ligase activity / ubiquitin protein ligase activity /  Circadian Clock / positive regulation of proteasomal ubiquitin-dependent protein catabolic process / Antigen processing: Ubiquitination & Proteasome degradation / Downstream TCR signaling / protein-macromolecule adaptor activity / Circadian Clock / positive regulation of proteasomal ubiquitin-dependent protein catabolic process / Antigen processing: Ubiquitination & Proteasome degradation / Downstream TCR signaling / protein-macromolecule adaptor activity /  Neddylation / ubiquitin-dependent protein catabolic process / Neddylation / ubiquitin-dependent protein catabolic process /  精子形成 / proteasome-mediated ubiquitin-dependent protein catabolic process / secretory granule lumen / positive regulation of canonical NF-kappaB signal transduction / RNA polymerase II-specific DNA-binding transcription factor binding / ficolin-1-rich granule lumen / cell population proliferation / Potential therapeutics for SARS 精子形成 / proteasome-mediated ubiquitin-dependent protein catabolic process / secretory granule lumen / positive regulation of canonical NF-kappaB signal transduction / RNA polymerase II-specific DNA-binding transcription factor binding / ficolin-1-rich granule lumen / cell population proliferation / Potential therapeutics for SARS類似検索 - 分子機能 | |||||||||
| 生物種 |   Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 |  電子顕微鏡法 / 電子顕微鏡法 /  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 2.7 Å クライオ電子顕微鏡法 / 解像度: 2.7 Å | |||||||||
 データ登録者 データ登録者 | Baek, K. / Schulman, B.A. | |||||||||
| 資金援助 |  ドイツ, European Union, 2件 ドイツ, European Union, 2件
| |||||||||
 引用 引用 |  ジャーナル: Cell / 年: 2023 ジャーナル: Cell / 年: 2023タイトル: Systemwide disassembly and assembly of SCF ubiquitin ligase complexes. 著者: Kheewoong Baek / Daniel C Scott / Lukas T Henneberg / Moeko T King / Matthias Mann / Brenda A Schulman /   要旨: Cells respond to environmental cues by remodeling their inventories of multiprotein complexes. Cellular repertoires of SCF (SKP1-CUL1-F box protein) ubiquitin ligase complexes, which mediate much ...Cells respond to environmental cues by remodeling their inventories of multiprotein complexes. Cellular repertoires of SCF (SKP1-CUL1-F box protein) ubiquitin ligase complexes, which mediate much protein degradation, require CAND1 to distribute the limiting CUL1 subunit across the family of ∼70 different F box proteins. Yet, how a single factor coordinately assembles numerous distinct multiprotein complexes remains unknown. We obtained cryo-EM structures of CAND1-bound SCF complexes in multiple states and correlated mutational effects on structures, biochemistry, and cellular assays. The data suggest that CAND1 clasps idling catalytic domains of an inactive SCF, rolls around, and allosterically rocks and destabilizes the SCF. New SCF production proceeds in reverse, through SKP1-F box allosterically destabilizing CAND1. The CAND1-SCF conformational ensemble recycles CUL1 from inactive complexes, fueling mixing and matching of SCF parts for E3 activation in response to substrate availability. Our data reveal biogenesis of a predominant family of E3 ligases, and the molecular basis for systemwide multiprotein complex assembly. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  7z8r.cif.gz 7z8r.cif.gz | 345.4 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb7z8r.ent.gz pdb7z8r.ent.gz | 271.7 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  7z8r.json.gz 7z8r.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/z8/7z8r https://data.pdbj.org/pub/pdb/validation_reports/z8/7z8r ftp://data.pdbj.org/pub/pdb/validation_reports/z8/7z8r ftp://data.pdbj.org/pub/pdb/validation_reports/z8/7z8r | HTTPS FTP |
|---|
-関連構造データ
| 関連構造データ |  14561MC  7z8tC  7z8vC  7zbwC  7zbzC  8cdjC  8cdkC M: このデータのモデリングに利用したマップデータ C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
| #1: タンパク質 |  / CUL-1 / CUL-1分子量: 89800.367 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)   Homo sapiens (ヒト) / 遺伝子: CUL1 / 発現宿主: Homo sapiens (ヒト) / 遺伝子: CUL1 / 発現宿主:   Trichoplusia ni (イラクサキンウワバ) / 参照: UniProt: Q13616 Trichoplusia ni (イラクサキンウワバ) / 参照: UniProt: Q13616 | ||
|---|---|---|---|
| #2: タンパク質 | 分子量: 137386.281 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)   Homo sapiens (ヒト) / 遺伝子: CAND1, KIAA0829, TIP120, TIP120A / 発現宿主: Homo sapiens (ヒト) / 遺伝子: CAND1, KIAA0829, TIP120, TIP120A / 発現宿主:   Escherichia coli BL21(DE3) (大腸菌) / 参照: UniProt: Q86VP6 Escherichia coli BL21(DE3) (大腸菌) / 参照: UniProt: Q86VP6 | ||
| #3: タンパク質 | 分子量: 12089.677 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)   Homo sapiens (ヒト) / 遺伝子: RBX1, RNF75, ROC1 / 発現宿主: Homo sapiens (ヒト) / 遺伝子: RBX1, RNF75, ROC1 / 発現宿主:   Trichoplusia ni (イラクサキンウワバ) / 参照: UniProt: P62877 Trichoplusia ni (イラクサキンウワバ) / 参照: UniProt: P62877 | ||
| #4: 化合物 | | 研究の焦点であるリガンドがあるか | Y | |
-実験情報
-実験
| 実験 | 手法:  電子顕微鏡法 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法:  単粒子再構成法 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: CAND1-CUL1-RBX1 / タイプ: COMPLEX / Entity ID: #1-#3 / 由来: RECOMBINANT |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 由来(組換発現) | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 緩衝液 | pH: 7.5 |
| 試料 | 濃度: 2 mg/ml / 包埋: NO / シャドウイング: NO / 染色 : NO / 凍結 : NO / 凍結 : YES : YES |
急速凍結 | 凍結剤: ETHANE |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源 : :  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD Bright-field microscopy / 最大 デフォーカス(公称値): 2000 nm / 最小 デフォーカス(公称値): 500 nm Bright-field microscopy / 最大 デフォーカス(公称値): 2000 nm / 最小 デフォーカス(公称値): 500 nm |
| 撮影 | 電子線照射量: 60 e/Å2 フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) |
- 解析
解析
| ソフトウェア | 名称: PHENIX / バージョン: 1.19.2_4158: / 分類: 精密化 | ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||
3次元再構成 | 解像度: 2.7 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 351565 / 対称性のタイプ: POINT | ||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー



































 PDBj
PDBj








