+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-4115 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Israeli acute paralysis virus heated to 63 degree - empty particle | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | IAPV / Dicistroviridae / empty particle / Virus | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報 | |||||||||
| 生物種 |  Israeli acute paralysis virus (ウイルス) Israeli acute paralysis virus (ウイルス) | |||||||||
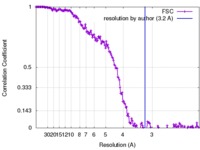
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.2 Å | |||||||||
 データ登録者 データ登録者 | Mullapudi E / Fuzik T | |||||||||
| 資金援助 |  チェコ, チェコ,  ドイツ, 2件 ドイツ, 2件
| |||||||||
 引用 引用 |  ジャーナル: J Virol / 年: 2017 ジャーナル: J Virol / 年: 2017タイトル: Cryo-electron Microscopy Study of the Genome Release of the Dicistrovirus Israeli Acute Bee Paralysis Virus. 著者: Edukondalu Mullapudi / Tibor Füzik / Antonín Přidal / Pavel Plevka /  要旨: Viruses of the family Dicistroviridae can cause substantial economic damage by infecting agriculturally important insects. Israeli acute bee paralysis virus (IAPV) causes honeybee colony collapse ...Viruses of the family Dicistroviridae can cause substantial economic damage by infecting agriculturally important insects. Israeli acute bee paralysis virus (IAPV) causes honeybee colony collapse disorder in the United States. High-resolution molecular details of the genome delivery mechanism of dicistroviruses are unknown. Here we present a cryo-electron microscopy analysis of IAPV virions induced to release their genomes in vitro We determined structures of full IAPV virions primed to release their genomes to a resolution of 3.3 Å and of empty capsids to a resolution of 3.9 Å. We show that IAPV does not form expanded A particles before genome release as in the case of related enteroviruses of the family Picornaviridae The structural changes observed in the empty IAPV particles include detachment of the VP4 minor capsid proteins from the inner face of the capsid and partial loss of the structure of the N-terminal arms of the VP2 capsid proteins. Unlike the case for many picornaviruses, the empty particles of IAPV are not expanded relative to the native virions and do not contain pores in their capsids that might serve as channels for genome release. Therefore, rearrangement of a unique region of the capsid is probably required for IAPV genome release. IMPORTANCE: Honeybee populations in Europe and North America are declining due to pressure from pathogens, including viruses. Israeli acute bee paralysis virus (IAPV), a member of the family ...IMPORTANCE: Honeybee populations in Europe and North America are declining due to pressure from pathogens, including viruses. Israeli acute bee paralysis virus (IAPV), a member of the family Dicistroviridae, causes honeybee colony collapse disorder in the United States. The delivery of virus genomes into host cells is necessary for the initiation of infection. Here we present a structural cryo-electron microscopy analysis of IAPV particles induced to release their genomes. We show that genome release is not preceded by an expansion of IAPV virions as in the case of related picornaviruses that infect vertebrates. Furthermore, minor capsid proteins detach from the capsid upon genome release. The genome leaves behind empty particles that have compact protein shells. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_4115.map.gz emd_4115.map.gz | 37.7 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-4115-v30.xml emd-4115-v30.xml emd-4115.xml emd-4115.xml | 15.5 KB 15.5 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_4115_fsc.xml emd_4115_fsc.xml | 18.6 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_4115.png emd_4115.png | 290.5 KB | ||
| Filedesc metadata |  emd-4115.cif.gz emd-4115.cif.gz | 5.9 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-4115 http://ftp.pdbj.org/pub/emdb/structures/EMD-4115 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-4115 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-4115 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_4115_validation.pdf.gz emd_4115_validation.pdf.gz | 348.3 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_4115_full_validation.pdf.gz emd_4115_full_validation.pdf.gz | 347.4 KB | 表示 | |
| XML形式データ |  emd_4115_validation.xml.gz emd_4115_validation.xml.gz | 14.6 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-4115 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-4115 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-4115 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-4115 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_4115.map.gz / 形式: CCP4 / 大きさ: 137.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_4115.map.gz / 形式: CCP4 / 大きさ: 137.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 1.07 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Israeli acute paralysis virus
| 全体 | 名称:  Israeli acute paralysis virus (ウイルス) Israeli acute paralysis virus (ウイルス) |
|---|---|
| 要素 |
|
-超分子 #1: Israeli acute paralysis virus
| 超分子 | 名称: Israeli acute paralysis virus / タイプ: virus / ID: 1 / 親要素: 0 / 含まれる分子: all / NCBI-ID: 294365 / 生物種: Israeli acute paralysis virus / ウイルスタイプ: VIRION / ウイルス・単離状態: OTHER / ウイルス・エンベロープ: No / ウイルス・中空状態: No |
|---|---|
| 宿主 | 生物種:  |
-分子 #1: VP1
| 分子 | 名称: VP1 / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Israeli acute paralysis virus (ウイルス) Israeli acute paralysis virus (ウイルス) |
| 分子量 | 理論値: 23.776541 KDa |
| 配列 | 文字列: INIGNKTNEN VISFFDSTDA ETQNHNALMK GCGEFIVNLR TLLRTFRTIT DNWILQANTK TPITDLTNTT DAQGRDYMSY LSYLYRFYR GGRRYKFFNT TPLKQSQTCY IRSFLIPRNY SADEINVDGP SHITYPVINP VHEVEVPFYS QYRKIPIAST S DKGYDSSL ...文字列: INIGNKTNEN VISFFDSTDA ETQNHNALMK GCGEFIVNLR TLLRTFRTIT DNWILQANTK TPITDLTNTT DAQGRDYMSY LSYLYRFYR GGRRYKFFNT TPLKQSQTCY IRSFLIPRNY SADEINVDGP SHITYPVINP VHEVEVPFYS QYRKIPIAST S DKGYDSSL MYFSNTATTQ IVARAGNDDF TFGWMIGPPQ LQGESRSVAP |
-分子 #2: VP2
| 分子 | 名称: VP2 / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Israeli acute paralysis virus (ウイルス) Israeli acute paralysis virus (ウイルス) |
| 分子量 | 理論値: 33.260754 KDa |
| 配列 | 文字列: SKPRNQQQVC PLQNVPAWGY SLYKGIDMSV PLAYDPNNEL GDLKDVFPSA VDEMAIGYVC GNPAVKHVLT WKTTDAIQKP IANGDDWGG VIPVGMPCYS KSIRTTRISA TENRETEVMD AAPCEYVANM FSYWRATMCY RITVVKTAFH TGRLEIFFEP G VIPVKPTV ...文字列: SKPRNQQQVC PLQNVPAWGY SLYKGIDMSV PLAYDPNNEL GDLKDVFPSA VDEMAIGYVC GNPAVKHVLT WKTTDAIQKP IANGDDWGG VIPVGMPCYS KSIRTTRISA TENRETEVMD AAPCEYVANM FSYWRATMCY RITVVKTAFH TGRLEIFFEP G VIPVKPTV NNIGPDQDRL TGAVAPSDNN YKYILDLTND TEVTIRVPFV SNKMFLKTAG IYGANSENNW NFHESFSGFL CI RPVTKLM APDTVSDNVS IVVWKWAEDV VVVEPKPLTS GPTQVYRPPP TASTAVEVLN VEL |
-分子 #3: Structural polyprotein
| 分子 | 名称: Structural polyprotein / タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Israeli acute paralysis virus (ウイルス) Israeli acute paralysis virus (ウイルス) |
| 分子量 | 理論値: 26.482732 KDa |
| 配列 | 文字列: SENSVETQEI TTFHDVETPN RIDTPMAQDT SSARNMDDTH SIIQFLQRPV LIDNIEIIAG TTADANKPLS RYVLDQQNSQ KYVRSWTLP STVLRAGGKA QKLANFKYLR CDVQVKLVLN ANPFVAGRMY LAYSPYDDKV DTARSVLQTS RAGVTGYPGV E LDFQLDNS ...文字列: SENSVETQEI TTFHDVETPN RIDTPMAQDT SSARNMDDTH SIIQFLQRPV LIDNIEIIAG TTADANKPLS RYVLDQQNSQ KYVRSWTLP STVLRAGGKA QKLANFKYLR CDVQVKLVLN ANPFVAGRMY LAYSPYDDKV DTARSVLQTS RAGVTGYPGV E LDFQLDNS VEMTIPYASF QEAYDLVTGT EDFVQLYLFP ITPVLGPKSE SESSKVDISV YMWLSNISLV IPTYRINP |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.4 |
|---|---|
| グリッド | モデル: Quantifoil R2/1 / 材質: COPPER / メッシュ: 200 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 298 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: FEI FALCON II (4k x 4k) 検出モード: INTEGRATING / デジタル化 - 画像ごとのフレーム数: 1-7 / 撮影したグリッド数: 1 / 実像数: 1500 / 平均露光時間: 1.0 sec. / 平均電子線量: 21.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 100.0 µm / 最大 デフォーカス(補正後): 3.0 µm / 最小 デフォーカス(補正後): 1.0 µm / 倍率(補正後): 75000 / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 3.0 µm / 最小 デフォーカス(公称値): 1.0 µm / 倍率(公称値): 75000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 詳細 | initial rigid body fit was done by Chimera, then the model was refined using realspace refinement in Phenix and finaly reciprocal refined in REFMAC. |
|---|---|
| 精密化 | 空間: RECIPROCAL / プロトコル: RIGID BODY FIT |
| 得られたモデル |  PDB-5lwi: |
 ムービー
ムービー コントローラー
コントローラー