+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of Kap114 bound to H2A-H2B | |||||||||
 マップデータ マップデータ | sharpened | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Karyopherin Beta Nuclear Transport Histone Histone Chaperone / PROTEIN TRANSPORT-STRUCTURAL PROTEIN complex | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報HATs acetylate histones / SIRT1 negatively regulates rRNA expression / Condensation of Prophase Chromosomes / Activated PKN1 stimulates transcription of AR (androgen receptor) regulated genes KLK2 and KLK3 / Assembly of the ORC complex at the origin of replication / HDACs deacetylate histones / Recruitment and ATM-mediated phosphorylation of repair and signaling proteins at DNA double strand breaks / Oxidative Stress Induced Senescence / replication fork protection complex / RMTs methylate histone arginines ...HATs acetylate histones / SIRT1 negatively regulates rRNA expression / Condensation of Prophase Chromosomes / Activated PKN1 stimulates transcription of AR (androgen receptor) regulated genes KLK2 and KLK3 / Assembly of the ORC complex at the origin of replication / HDACs deacetylate histones / Recruitment and ATM-mediated phosphorylation of repair and signaling proteins at DNA double strand breaks / Oxidative Stress Induced Senescence / replication fork protection complex / RMTs methylate histone arginines / nuclear import signal receptor activity / NLS-bearing protein import into nucleus / RNA Polymerase I Promoter Escape / Estrogen-dependent gene expression / heterochromatin organization / Ub-specific processing proteases / mRNA transport / nucleosomal DNA binding /  核膜孔 / 核膜孔 /  small GTPase binding / structural constituent of chromatin / protein import into nucleus / small GTPase binding / structural constituent of chromatin / protein import into nucleus /  ヌクレオソーム / ヌクレオソーム /  核膜 / chromatin organization / protein heterodimerization activity / 核膜 / chromatin organization / protein heterodimerization activity /  DNA修復 / regulation of DNA-templated transcription / DNA修復 / regulation of DNA-templated transcription /  DNA binding / DNA binding /  細胞核 / 細胞核 /  細胞質基質 / 細胞質基質 /  細胞質 細胞質類似検索 - 分子機能 | |||||||||
| 生物種 |   Saccharomyces cerevisiae S288C (パン酵母) Saccharomyces cerevisiae S288C (パン酵母) | |||||||||
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 3.21 Å クライオ電子顕微鏡法 / 解像度: 3.21 Å | |||||||||
 データ登録者 データ登録者 | Jiou J / Chook YM | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Proc Natl Acad Sci U S A / 年: 2023 ジャーナル: Proc Natl Acad Sci U S A / 年: 2023タイトル: Mechanism of RanGTP priming H2A-H2B release from Kap114 in an atypical RanGTP•Kap114•H2A-H2B complex. 著者: Jenny Jiou / Joy M Shaffer / Natalia E Bernades / Ho Yee Joyce Fung / Juliana Kikumoto Dias / Sheena D'Arcy / Yuh Min Chook /  要旨: Previously, we showed that the nuclear import receptor Importin-9 wraps around the H2A-H2B core to chaperone and transport it from the cytoplasm to the nucleus. However, unlike most nuclear import ...Previously, we showed that the nuclear import receptor Importin-9 wraps around the H2A-H2B core to chaperone and transport it from the cytoplasm to the nucleus. However, unlike most nuclear import systems where RanGTP dissociates cargoes from their importins, RanGTP binds stably to the Importin-9•H2A-H2B complex, and formation of the ternary RanGTP•Importin-9•H2A-H2B complex facilitates H2A-H2B release to the assembling nucleosome. It was unclear how RanGTP and the cargo H2A-H2B can bind simultaneously to an importin, and how interactions of the three components position H2A-H2B for release. Here, we show cryo-EM structures of Importin-9•RanGTP and of its yeast homolog Kap114, including Kap114•RanGTP, Kap114•H2A-H2B, and RanGTP•Kap114•H2A-H2B, to explain how the conserved Kap114 binds H2A-H2B and RanGTP simultaneously and how the GTPase primes histone transfer to the nucleosome. In the ternary complex, RanGTP binds to the N-terminal repeats of Kap114 in the same manner as in the Kap114/Importin-9•RanGTP complex, and H2A-H2B binds via its acidic patch to the Kap114 C-terminal repeats much like in the Kap114/Importin-9•H2A-H2B complex. Ran binds to a different conformation of Kap114 in the ternary RanGTP•Kap114•H2A-H2B complex. Here, Kap114 no longer contacts the H2A-H2B surface proximal to the H2A docking domain that drives nucleosome assembly, positioning it for transfer to the assembling nucleosome or to dedicated H2A-H2B chaperones in the nucleus. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_28782.map.gz emd_28782.map.gz | 143.9 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-28782-v30.xml emd-28782-v30.xml emd-28782.xml emd-28782.xml | 19 KB 19 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_28782.png emd_28782.png | 65 KB | ||
| その他 |  emd_28782_half_map_1.map.gz emd_28782_half_map_1.map.gz emd_28782_half_map_2.map.gz emd_28782_half_map_2.map.gz | 262.7 MB 262.7 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-28782 http://ftp.pdbj.org/pub/emdb/structures/EMD-28782 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-28782 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-28782 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_28782.map.gz / 形式: CCP4 / 大きさ: 282.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_28782.map.gz / 形式: CCP4 / 大きさ: 282.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | sharpened | ||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.5295 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: half-A
| ファイル | emd_28782_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | half-A | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
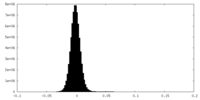
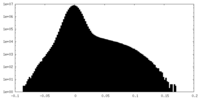
| 密度ヒストグラム |
-ハーフマップ: half-B
| ファイル | emd_28782_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | half-B | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
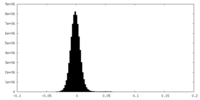
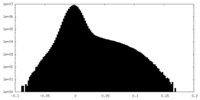
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Complex of Kap114 bound to H2A-H2B dimer
| 全体 | 名称: Complex of Kap114 bound to H2A-H2B dimer |
|---|---|
| 要素 |
|
-超分子 #1: Complex of Kap114 bound to H2A-H2B dimer
| 超分子 | 名称: Complex of Kap114 bound to H2A-H2B dimer / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:   Saccharomyces cerevisiae S288C (パン酵母) Saccharomyces cerevisiae S288C (パン酵母) |
-分子 #1: Importin subunit beta-5
| 分子 | 名称: Importin subunit beta-5 / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Saccharomyces cerevisiae S288C (パン酵母) / 株: ATCC 204508 / S288c Saccharomyces cerevisiae S288C (パン酵母) / 株: ATCC 204508 / S288c |
| 分子量 | 理論値: 114.019695 KDa |
| 組換発現 | 生物種:   Escherichia coli 'BL21-Gold(DE3)pLysS AG' (大腸菌) Escherichia coli 'BL21-Gold(DE3)pLysS AG' (大腸菌) |
| 配列 | 文字列: MDINELIIGA QSADKHTREV AETQLLQWCD SDASQVFKAL ANVALQHEAS LESRQFALLS LRKLITMYWS PGFESYRSTS NVEIDVKDF IREVLLKLCL NDNENTKIKN GASYCIVQIS AVDFPDQWPQ LLTVIYDAIS HQHSLNAMSL LNEIYDDVVS E EMFFEGGI ...文字列: MDINELIIGA QSADKHTREV AETQLLQWCD SDASQVFKAL ANVALQHEAS LESRQFALLS LRKLITMYWS PGFESYRSTS NVEIDVKDF IREVLLKLCL NDNENTKIKN GASYCIVQIS AVDFPDQWPQ LLTVIYDAIS HQHSLNAMSL LNEIYDDVVS E EMFFEGGI GLATMEIVFK VLNTETSTLI AKIAALKLLK ACLLQMSSHN EYDEASRKSF VSQCLATSLQ ILGQLLTLNF GN VDVISQL KFKSIIYENL VFIKNDFSRK HFSSELQKQF KIMAIQDLEN VTHINANVET TESEPLLETV HDCSIYIVEF LTS VCTLQF SVEEMNKIIT SLTILCQLSS ETREIWTSDF NTFVSKETGL AASYNVRDQA NEFFTSLPNP QLSLIFKVVS NDIE HSTCN YSTLESLLYL LQCILLNDDE ITGENIDQSL QILIKTLENI LVSQEIPELI LARAILTIPR VLDKFIDALP DIKPL TSAF LAKSLNLALK SDKELIKSAT LIAFTYYCYF AELDSVLGPE VCSETQEKVI RIINQVSSDA EEDTNGALME VLSQVI SYN PKEPHSRKEI LQAEFHLVFT ISSEDPANVQ VVVQSQECLE KLLDNINMDN YKNYIELCLP SFINVLDSNN ANNYRYS PL LSLVLEFITV FLKKKPNDGF LPDEINQYLF EPLAKVLAFS TEDETLQLAT EAFSYLIFNT DTRAMEPRLM DIMKVLER L LSLEVSDSAA MNVGPLVVAI FTRFSKEIQP LIGRILEAVV VRLIKTQNIS TEQNLLSVLC FLTCNDPKQT VDFLSSFQI DNTDALTLVM RKWIEAFEVI RGEKRIKENI VALSNLFFLN DKRLQKVVVN GNLIPYEGDL IITRSMAKKM PDRYVQVPLY TKIIKLFVS ELSFQSKQPN PEQLITSDIK QEVVNANKDD DNDDWEDVDD VLDYDKLKEY IDDDVDEEAD DDSDDITGLM D VKESVVQL LVRFFKEVAS KDVSGFHCIY ETLSDSERKV LSEALL UniProtKB:  Importin subunit beta-5 Importin subunit beta-5 |
-分子 #2: Histone H2A.2
| 分子 | 名称: Histone H2A.2 / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Saccharomyces cerevisiae S288C (パン酵母) / 株: ATCC 204508 / S288c Saccharomyces cerevisiae S288C (パン酵母) / 株: ATCC 204508 / S288c |
| 分子量 | 理論値: 13.88198 KDa |
| 組換発現 | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 配列 | 文字列: SGGKGGKAGS AAKASQSRSA KAGLTFPVGR VHRLLRRGNY AQRIGSGAPV YLTAVLEYLA AEILELAGNA ARDNKKTRII PRHLQLAIR NDDELNKLLG NVTIAQGGVL PNIHQNLLPK KSAKTAKASQ EL UniProtKB: Histone H2A.2 |
-分子 #3: Histone H2B.2
| 分子 | 名称: Histone H2B.2 / タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Saccharomyces cerevisiae S288C (パン酵母) / 株: ATCC 204508 / S288c Saccharomyces cerevisiae S288C (パン酵母) / 株: ATCC 204508 / S288c |
| 分子量 | 理論値: 14.133145 KDa |
| 組換発現 | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 配列 | 文字列: SSAAEKKPAS KAPAEKKPAA KKTSTSVDGK KRSKVRKETY SSYIYKVLKQ THPDTGISQK SMSILNSFVN DIFERIATEA SKLAAYNKK STISAREIQT AVRLILPGEL AKHAVSEGTR AVTKYSSSTQ A UniProtKB: Histone H2B.2 |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 4.0 mg/mL | ||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 7.5 構成要素:
詳細: 20 mM Tris pH 7.5, 300 mM NaCl, 2 mM MgCl2, 1 mM TCEP, and 0.1% NP-40 | ||||||||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 95 % / チャンバー内温度: 4 K / 装置: FEI VITROBOT MARK IV | ||||||||||||||||||
| 詳細 | 1 Kap114 to 1.2 H2A-H2B ratio |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 1.5 µm Bright-field microscopy / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 1.5 µm |
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 平均電子線量: 50.0 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: PDB ENTRY PDBモデル - PDB ID: |
|---|---|
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 3.21 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 554529 |
 ムービー
ムービー コントローラー
コントローラー






















 Z
Z Y
Y X
X