+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-11633 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Aquifex aeolicus lumazine synthase-derived nucleocapsid variant NC-2 (180-mer) | |||||||||
 マップデータ マップデータ | half map 1 | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード |  capsid (カプシド) / capsid (カプシド) /  design (デザイン) / virus mimic / design (デザイン) / virus mimic /  VIRUS LIKE PARTICLE (ウイルス様粒子) VIRUS LIKE PARTICLE (ウイルス様粒子) | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報 6,7-dimethyl-8-ribityllumazine synthase / 6,7-dimethyl-8-ribityllumazine synthase /  6,7-dimethyl-8-ribityllumazine synthase activity / 6,7-dimethyl-8-ribityllumazine synthase activity /  riboflavin synthase complex / bacterial-type RNA polymerase core enzyme binding / riboflavin biosynthetic process / riboflavin synthase complex / bacterial-type RNA polymerase core enzyme binding / riboflavin biosynthetic process /  RNA polymerase binding / RNA stem-loop binding / transcription antitermination factor activity, RNA binding / regulation of DNA-templated transcription elongation / transcription antitermination ... RNA polymerase binding / RNA stem-loop binding / transcription antitermination factor activity, RNA binding / regulation of DNA-templated transcription elongation / transcription antitermination ... 6,7-dimethyl-8-ribityllumazine synthase / 6,7-dimethyl-8-ribityllumazine synthase /  6,7-dimethyl-8-ribityllumazine synthase activity / 6,7-dimethyl-8-ribityllumazine synthase activity /  riboflavin synthase complex / bacterial-type RNA polymerase core enzyme binding / riboflavin biosynthetic process / riboflavin synthase complex / bacterial-type RNA polymerase core enzyme binding / riboflavin biosynthetic process /  RNA polymerase binding / RNA stem-loop binding / transcription antitermination factor activity, RNA binding / regulation of DNA-templated transcription elongation / transcription antitermination / DNA-templated transcription termination / RNA polymerase binding / RNA stem-loop binding / transcription antitermination factor activity, RNA binding / regulation of DNA-templated transcription elongation / transcription antitermination / DNA-templated transcription termination /  single-stranded RNA binding / regulation of transcription by RNA polymerase II / single-stranded RNA binding / regulation of transcription by RNA polymerase II /  DNA binding / DNA binding /  RNA binding / RNA binding /  細胞質基質 細胞質基質類似検索 - 分子機能 | |||||||||
| 生物種 |   Escherichia virus lambda (ウイルス) / Escherichia virus lambda (ウイルス) /    Aquifex aeolicus VF5 (バクテリア) Aquifex aeolicus VF5 (バクテリア) | |||||||||
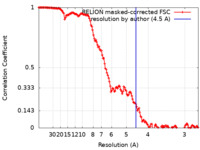
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 4.5 Å クライオ電子顕微鏡法 / 解像度: 4.5 Å | |||||||||
 データ登録者 データ登録者 | Tetter S / Hilvert D | |||||||||
| 資金援助 | 1件
| |||||||||
 引用 引用 |  ジャーナル: Science / 年: 2021 ジャーナル: Science / 年: 2021タイトル: Evolution of a virus-like architecture and packaging mechanism in a repurposed bacterial protein. 著者: Stephan Tetter / Naohiro Terasaka / Angela Steinauer / Richard J Bingham / Sam Clark / Andrew J P Scott / Nikesh Patel / Marc Leibundgut / Emma Wroblewski / Nenad Ban / Peter G Stockley / ...著者: Stephan Tetter / Naohiro Terasaka / Angela Steinauer / Richard J Bingham / Sam Clark / Andrew J P Scott / Nikesh Patel / Marc Leibundgut / Emma Wroblewski / Nenad Ban / Peter G Stockley / Reidun Twarock / Donald Hilvert /   要旨: Viruses are ubiquitous pathogens of global impact. Prompted by the hypothesis that their earliest progenitors recruited host proteins for virion formation, we have used stringent laboratory evolution ...Viruses are ubiquitous pathogens of global impact. Prompted by the hypothesis that their earliest progenitors recruited host proteins for virion formation, we have used stringent laboratory evolution to convert a bacterial enzyme that lacks affinity for nucleic acids into an artificial nucleocapsid that efficiently packages and protects multiple copies of its own encoding messenger RNA. Revealing remarkable convergence on the molecular hallmarks of natural viruses, the accompanying changes reorganized the protein building blocks into an interlaced 240-subunit icosahedral capsid that is impermeable to nucleases, and emergence of a robust RNA stem-loop packaging cassette ensured high encapsidation yields and specificity. In addition to evincing a plausible evolutionary pathway for primordial viruses, these findings highlight practical strategies for developing nonviral carriers for diverse vaccine and delivery applications. #1:  ジャーナル: Biorxiv / 年: 2021 ジャーナル: Biorxiv / 年: 2021タイトル: Evolution of a virus-like architecture and packaging mechanism in a repurposed bacterial protein 著者: Tetter S / Terasaka N / Steinauer A / Bingham RJ / Clark S / Scott AJP / Patel N / Leibundgut M / Wroblewski E / Ban N / Stockley PG / Twarock R / Hilvert D | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_11633.map.gz emd_11633.map.gz | 31 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-11633-v30.xml emd-11633-v30.xml emd-11633.xml emd-11633.xml | 22 KB 22 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_11633_fsc.xml emd_11633_fsc.xml | 14.1 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_11633.png emd_11633.png | 79 KB | ||
| マスクデータ |  emd_11633_msk_1.map emd_11633_msk_1.map | 244.1 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-11633.cif.gz emd-11633.cif.gz | 6.3 KB | ||
| その他 |  emd_11633_additional_1.map.gz emd_11633_additional_1.map.gz emd_11633_half_map_1.map.gz emd_11633_half_map_1.map.gz emd_11633_half_map_2.map.gz emd_11633_half_map_2.map.gz | 194.1 MB 194.2 MB 194.9 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-11633 http://ftp.pdbj.org/pub/emdb/structures/EMD-11633 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-11633 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-11633 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_11633.map.gz / 形式: CCP4 / 大きさ: 244.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_11633.map.gz / 形式: CCP4 / 大きさ: 244.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | half map 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.375 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
| ファイル |  emd_11633_msk_1.map emd_11633_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: map from 3D autorefinement in Relion
| ファイル | emd_11633_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | map from 3D autorefinement in Relion | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: map from 3D autorefinement in Relion
| ファイル | emd_11633_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | map from 3D autorefinement in Relion | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: half map 2
| ファイル | emd_11633_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | half map 2 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Aquifex aeolicus lumazine synthase-derived nucleocapsid variant N...
| 全体 | 名称: Aquifex aeolicus lumazine synthase-derived nucleocapsid variant NC-2 (180-mer) |
|---|---|
| 要素 |
|
-超分子 #1: Aquifex aeolicus lumazine synthase-derived nucleocapsid variant N...
| 超分子 | 名称: Aquifex aeolicus lumazine synthase-derived nucleocapsid variant NC-2 (180-mer) タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:   Escherichia virus lambda (ウイルス) Escherichia virus lambda (ウイルス) |
-分子 #1: Antitermination protein N,6,7-dimethyl-8-ribityllumazine synthase...
| 分子 | 名称: Antitermination protein N,6,7-dimethyl-8-ribityllumazine synthase,6,7-dimethyl-8-ribityllumazine synthase タイプ: protein_or_peptide / ID: 1 / コピー数: 180 / 光学異性体: LEVO / EC番号:  6,7-dimethyl-8-ribityllumazine synthase 6,7-dimethyl-8-ribityllumazine synthase |
|---|---|
| 由来(天然) | 生物種:    Aquifex aeolicus VF5 (バクテリア) Aquifex aeolicus VF5 (バクテリア) |
| 分子量 | 理論値: 21.41534 KDa |
| 組換発現 | 生物種:   Escherichia coli BL21(DE3) (大腸菌) Escherichia coli BL21(DE3) (大腸菌) |
| 配列 | 文字列: MGNAKTRRRE RRAEKQAQWK AANAGAGAGA MATPHFDYIA SVVSKGLANL SLELRKPVTF DIITADTLEQ AIERAGTKHG NKGWEAALS AIEMANLFKS LRGTGHHHHH HGSSMEIYEG KLTAEGLRFG IVASRFNHAL VDRLVEGAID CIVRHGGREE D ITLVRVPG ...文字列: MGNAKTRRRE RRAEKQAQWK AANAGAGAGA MATPHFDYIA SVVSKGLANL SLELRKPVTF DIITADTLEQ AIERAGTKHG NKGWEAALS AIEMANLFKS LRGTGHHHHH HGSSMEIYEG KLTAEGLRFG IVASRFNHAL VDRLVEGAID CIVRHGGREE D ITLVRVPG SWEIPVAAGE LARKEDIDAV IAFGDLIRG UniProtKB:  Antitermination protein N, Antitermination protein N,  6,7-dimethyl-8-ribityllumazine synthase, 6,7-dimethyl-8-ribityllumazine synthase,  6,7-dimethyl-8-ribityllumazine synthase 6,7-dimethyl-8-ribityllumazine synthase |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.4 |
|---|---|
| グリッド | モデル: Quantifoil R2/2 / 材質: COPPER / メッシュ: 400 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 15 sec. / 前処理 - 雰囲気: AIR |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 22 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.6 µm / 最小 デフォーカス(公称値): 0.8 µm / 倍率(公称値): 130000 Bright-field microscopy / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.6 µm / 最小 デフォーカス(公称値): 0.8 µm / 倍率(公称値): 130000 |
| 試料ステージ | ホルダー冷却材: NITROGEN |
| 撮影 | フィルム・検出器のモデル: FEI FALCON III (4k x 4k) 検出モード: INTEGRATING / 撮影したグリッド数: 1 / 実像数: 848 / 平均電子線量: 60.0 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー


















 Z
Z Y
Y X
X