+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of MLE in complex with SL7UUC RNA and ADP | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード |  RNA helicase (ヘリカーゼ) / RNA helicase (ヘリカーゼ) /  RNA BINDING PROTEIN (RNA結合タンパク質) RNA BINDING PROTEIN (RNA結合タンパク質) | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報RIP-mediated NFkB activation via ZBP1 / X chromosome located dosage compensation complex, transcription activating / 3'-5' DNA/RNA helicase activity / DEx/H-box helicases activate type I IFN and inflammatory cytokines production / male courtship behavior, veined wing generated song production / regulation of cytoplasmic translation / regulatory region RNA binding /  遺伝子量補償 / PKR-mediated signaling / MSL complex ...RIP-mediated NFkB activation via ZBP1 / X chromosome located dosage compensation complex, transcription activating / 3'-5' DNA/RNA helicase activity / DEx/H-box helicases activate type I IFN and inflammatory cytokines production / male courtship behavior, veined wing generated song production / regulation of cytoplasmic translation / regulatory region RNA binding / 遺伝子量補償 / PKR-mediated signaling / MSL complex ...RIP-mediated NFkB activation via ZBP1 / X chromosome located dosage compensation complex, transcription activating / 3'-5' DNA/RNA helicase activity / DEx/H-box helicases activate type I IFN and inflammatory cytokines production / male courtship behavior, veined wing generated song production / regulation of cytoplasmic translation / regulatory region RNA binding /  遺伝子量補償 / PKR-mediated signaling / MSL complex / dosage compensation by hyperactivation of X chromosome / positive regulation of DNA topoisomerase (ATP-hydrolyzing) activity / 遺伝子量補償 / PKR-mediated signaling / MSL complex / dosage compensation by hyperactivation of X chromosome / positive regulation of DNA topoisomerase (ATP-hydrolyzing) activity /  多糸染色体 / 3'-5' RNA helicase activity / 多糸染色体 / 3'-5' RNA helicase activity /  regulation of mRNA processing / axon extension / regulation of mRNA processing / axon extension /  lncRNA binding / DNA duplex unwinding / 3'-5' DNA helicase activity / nuclear chromosome / positive regulation of heterochromatin formation / lncRNA binding / DNA duplex unwinding / 3'-5' DNA helicase activity / nuclear chromosome / positive regulation of heterochromatin formation /  X染色体 / X染色体 /  DNA helicase activity / DNA helicase activity /  helicase activity / determination of adult lifespan / helicase activity / determination of adult lifespan /  double-stranded RNA binding / double-stranded RNA binding /  染色体 / 染色体 /  double-stranded DNA binding / double-stranded DNA binding /  RNA helicase activity / RNA helicase activity /  ヘリカーゼ / ヘリカーゼ /  ribonucleoprotein complex / ribonucleoprotein complex /  chromatin binding / chromatin binding /  クロマチン / クロマチン /  核小体 / 核小体 /  ATP hydrolysis activity / positive regulation of transcription by RNA polymerase II / ATP hydrolysis activity / positive regulation of transcription by RNA polymerase II /  RNA binding / RNA binding /  ATP binding / ATP binding /  細胞核 / 細胞核 /  細胞質基質 細胞質基質類似検索 - 分子機能 | |||||||||
| 生物種 |   Drosophila melanogaster (キイロショウジョウバエ) Drosophila melanogaster (キイロショウジョウバエ) | |||||||||
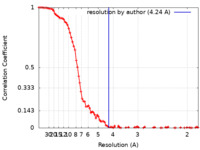
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 4.24 Å クライオ電子顕微鏡法 / 解像度: 4.24 Å | |||||||||
 データ登録者 データ登録者 | Jagtap PKA / Hennig J | |||||||||
| 資金援助 |  ドイツ, 1件 ドイツ, 1件
| |||||||||
 引用 引用 |  ジャーナル: Mol Cell / 年: 2023 ジャーナル: Mol Cell / 年: 2023タイトル: Structural basis of RNA-induced autoregulation of the DExH-type RNA helicase maleless. 著者: Pravin Kumar Ankush Jagtap / Marisa Müller / Anna E Kiss / Andreas W Thomae / Karine Lapouge / Martin Beck / Peter B Becker / Janosch Hennig /  要旨: RNA unwinding by DExH-type helicases underlies most RNA metabolism and function. It remains unresolved if and how the basic unwinding reaction of helicases is regulated by auxiliary domains. We ...RNA unwinding by DExH-type helicases underlies most RNA metabolism and function. It remains unresolved if and how the basic unwinding reaction of helicases is regulated by auxiliary domains. We explored the interplay between the RecA and auxiliary domains of the RNA helicase maleless (MLE) from Drosophila using structural and functional studies. We discovered that MLE exists in a dsRNA-bound open conformation and that the auxiliary dsRBD2 domain aligns the substrate RNA with the accessible helicase tunnel. In an ATP-dependent manner, dsRBD2 associates with the helicase module, leading to tunnel closure around ssRNA. Furthermore, our structures provide a rationale for blunt-ended dsRNA unwinding and 3'-5' translocation by MLE. Structure-based MLE mutations confirm the functional relevance of our model for RNA unwinding. Our findings contribute to our understanding of the fundamental mechanics of auxiliary domains in DExH helicase MLE, which serves as a model for its human ortholog and potential therapeutic target, DHX9/RHA. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_17711.map.gz emd_17711.map.gz | 31.5 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-17711-v30.xml emd-17711-v30.xml emd-17711.xml emd-17711.xml | 16.2 KB 16.2 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_17711_fsc.xml emd_17711_fsc.xml | 11.8 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_17711.png emd_17711.png | 23.9 KB | ||
| Filedesc metadata |  emd-17711.cif.gz emd-17711.cif.gz | 6.2 KB | ||
| その他 |  emd_17711_half_map_1.map.gz emd_17711_half_map_1.map.gz emd_17711_half_map_2.map.gz emd_17711_half_map_2.map.gz | 59.4 MB 59.4 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-17711 http://ftp.pdbj.org/pub/emdb/structures/EMD-17711 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-17711 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-17711 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8pjjMC  8b9gC  8b9iC  8b9jC  8b9kC  8b9lC  8pjbC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_17711.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_17711.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 0.932 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: #2
| ファイル | emd_17711_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_17711_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Complex of MLE, SL7UUC and ADP
| 全体 | 名称: Complex of MLE, SL7UUC and ADP |
|---|---|
| 要素 |
|
-超分子 #1: Complex of MLE, SL7UUC and ADP
| 超分子 | 名称: Complex of MLE, SL7UUC and ADP / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#2 |
|---|---|
| 分子量 | 理論値: 150 KDa |
-超分子 #2: Dosage compensation regulator
| 超分子 | 名称: Dosage compensation regulator / タイプ: complex / ID: 2 / 親要素: 1 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:   Drosophila melanogaster (キイロショウジョウバエ) Drosophila melanogaster (キイロショウジョウバエ) |
-超分子 #3: SL7UUC RNA
| 超分子 | 名称: SL7UUC RNA / タイプ: complex / ID: 3 / 親要素: 1 / 含まれる分子: #2 |
|---|---|
| 由来(天然) | 生物種:   Drosophila melanogaster (キイロショウジョウバエ) Drosophila melanogaster (キイロショウジョウバエ) |
-分子 #1: Dosage compensation regulator
| 分子 | 名称: Dosage compensation regulator / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO / EC番号:  ヘリカーゼ ヘリカーゼ |
|---|---|
| 由来(天然) | 生物種:   Drosophila melanogaster (キイロショウジョウバエ) Drosophila melanogaster (キイロショウジョウバエ) |
| 分子量 | 理論値: 130.335961 KDa |
| 組換発現 | 生物種:   Spodoptera frugiperda (ツマジロクサヨトウ) Spodoptera frugiperda (ツマジロクサヨトウ) |
| 配列 | 文字列: MDIKSFLYQF CAKSQIEPKF DIRQTGPKNR QRFLCEVRVE PNTYIGVGNS TNKKDAEKNA CRDFVNYLVR VGKLNTNDVP ADAGASGGG PRTGLEGAGM AGGSGQQKRV FDGQSGPQDL GEAYRPLNHD GGDGGNRYSV IDRIQEQRDM NEAEAFDVNA A IHGNWTIE ...文字列: MDIKSFLYQF CAKSQIEPKF DIRQTGPKNR QRFLCEVRVE PNTYIGVGNS TNKKDAEKNA CRDFVNYLVR VGKLNTNDVP ADAGASGGG PRTGLEGAGM AGGSGQQKRV FDGQSGPQDL GEAYRPLNHD GGDGGNRYSV IDRIQEQRDM NEAEAFDVNA A IHGNWTIE NAKERLNIYK QTNNIRDDYK YTPVGPEHAR SFLAELSIYV PALNRTVTAR ESGSNKKSAS KSCALSLVRQ LF HLNVIEP FSGTLKKKKD EQLKPYPVKL SPNLINKIDE VIKGLDLPVV NPRNIKIELD GPPIPLIVNL SRIDSSQQDG EKR QESSVI PWAPPQANWN TWHACNIDEG ELATTSIDDL SMDYERSLRD RRQNDNEYRQ FLEFREKLPI AAMRSEILTA INDN PVVII RGNTGCGKTT QIAQYILDDY ICSGQGGYAN IYVTQPRRIS AISVAERVAR ERCEQLGDTV GYSVRFESVF PRPYG AILF CTVGVLLRKL EAGLRGVSHI IVDEIHERDV NSDFLLVILR DMVDTYPDLH VILMSATIDT TKFSKYFGIC PVLEVP GRA FPVQQFFLED IIQMTDFVPS AESRRKRKEV EDEEQLLSED KDEAEINYNK VCEDKYSQKT RNAMAMLSES DVSFELL EA LLMHIKSKNI PGAILVFLPG WNLIFALMKF LQNTNIFGDT SQYQILPCHS QIPRDEQRKV FEPVPEGVTK IILSTNIA E TSITIDDIVF VIDICKARMK LFTSHNNLTS YATVWASKTN LEQRKGRAGR VRPGFCFTLC SRARFQALED NLTPEMFRT PLHEMALTIK LLRLGSIHHF LSKALEPPPV DAVIEAEVLL REMRCLDAND ELTPLGRLLA RLPIEPRLGK MMVLGAVFGC ADLMAIMAS YSSTFSEVFS LDIGQRRLAN HQKALSGTKC SDHVAMIVAS QMWRREKQRG EHMEARFCDW KGLQMSTMNV I WDAKQQLL DLLQQAGFPE ECMISHEVDE RIDGDDPVLD VSLALLCLGL YPNICVHKEK RKVLTTESKA ALLHKTSVNC SN LAVTFPY PFFVFGEKIR TRAVSCKQLS MVSPLQVILF GSRKIDLAAN NIVRVDNWLN FDIEPELAAK IGALKPALED LIT VACDNP SDILRLEEPY AQLVKVVKDL CVKSAGDFGL QR UniProtKB: Dosage compensation regulator |
-分子 #2: SL7UUC RNA
| 分子 | 名称: SL7UUC RNA / タイプ: rna / ID: 2 / コピー数: 1 |
|---|---|
| 由来(天然) | 生物種:   Drosophila melanogaster (キイロショウジョウバエ) Drosophila melanogaster (キイロショウジョウバエ) |
| 分子量 | 理論値: 19.011131 KDa |
| 配列 | 文字列: GUGUAAAAUG UUGCUAGCAA AUAUAUAUGC UAGUAACGUU UUACGCCCUC UUUCUUUCUU |
-分子 #3: ADENOSINE-5'-DIPHOSPHATE
| 分子 | 名称: ADENOSINE-5'-DIPHOSPHATE / タイプ: ligand / ID: 3 / コピー数: 1 / 式: ADP |
|---|---|
| 分子量 | 理論値: 427.201 Da |
| Chemical component information |  ChemComp-ADP: |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.6 mg/mL |
|---|---|
| 緩衝液 | pH: 7.5 |
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: OTHER / 撮影モード: BRIGHT FIELD Bright-field microscopy / 最大 デフォーカス(公称値): 1.8 µm / 最小 デフォーカス(公称値): 0.8 µm Bright-field microscopy / 最大 デフォーカス(公称値): 1.8 µm / 最小 デフォーカス(公称値): 0.8 µm |
| 撮影 | フィルム・検出器のモデル: FEI FALCON IV (4k x 4k) 平均電子線量: 52.6 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー











 Z
Z Y
Y X
X