+検索条件
-Structure paper
| タイトル | Allosteric control of type I-A CRISPR-Cas3 complexes and establishment as effective nucleic acid detection and human genome editing tools. |
|---|---|
| ジャーナル・号・ページ | Mol Cell, Vol. 82, Issue 15, Page 2754-22768.e5, Year 2022 |
| 掲載日 | 2022年8月4日 |
 著者 著者 | Chunyi Hu / Dongchun Ni / Ki Hyun Nam / Sonali Majumdar / Justin McLean / Henning Stahlberg / Michael P Terns / Ailong Ke /    |
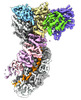
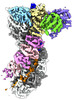
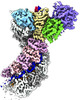
| PubMed 要旨 | Type I CRISPR-Cas systems typically rely on a two-step process to degrade DNA. First, an RNA-guided complex named Cascade identifies the complementary DNA target. The helicase-nuclease fusion enzyme ...Type I CRISPR-Cas systems typically rely on a two-step process to degrade DNA. First, an RNA-guided complex named Cascade identifies the complementary DNA target. The helicase-nuclease fusion enzyme Cas3 is then recruited in trans for processive DNA degradation. Contrary to this model, here, we show that type I-A Cascade and Cas3 function as an integral effector complex. We provide four cryoelectron microscopy (cryo-EM) snapshots of the Pyrococcus furiosus (Pfu) type I-A effector complex in different stages of DNA recognition and degradation. The HD nuclease of Cas3 is autoinhibited inside the effector complex. It is only allosterically activated upon full R-loop formation, when the entire targeted region has been validated by the RNA guide. The mechanistic insights inspired us to convert Pfu Cascade-Cas3 into a high-sensitivity, low-background, and temperature-activated nucleic acid detection tool. Moreover, Pfu CRISPR-Cas3 shows robust bi-directional deletion-editing activity in human cells, which could find usage in allele-specific inactivation of disease-causing mutations. |
 リンク リンク |  Mol Cell / Mol Cell /  PubMed:35835111 / PubMed:35835111 /  PubMed Central PubMed Central |
| 手法 | EM (単粒子) |
| 解像度 | 3.3 - 6.6 Å |
| 構造データ | EMDB-26081, PDB-7tr6: EMDB-26082, PDB-7tr8: EMDB-26083, PDB-7tr9: EMDB-26084, PDB-7tra: 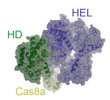 EMDB-26097: Cas3-Cas8 complex from type I-A CRISPR-Cas system |
| 化合物 |  ChemComp-NI: |
| 由来 |
|
 キーワード キーワード |  RNA BINDING PROTEIN (RNA結合タンパク質) / RNA BINDING PROTEIN (RNA結合タンパク質) /  CRISPR (CRISPR) / cascade / type I-A / CRISPR (CRISPR) / cascade / type I-A /  genome editing (ゲノム編集) / genome editing (ゲノム編集) /  Cas3 / DNA targeting Cas3 / DNA targeting |
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア 万見文献について
万見文献について