+検索条件
-Structure paper
| タイトル | Neutralization of SARS-CoV-2 by Destruction of the Prefusion Spike. |
|---|---|
| ジャーナル・号・ページ | Cell Host Microbe, Vol. 28, Issue 3, Page 445-454.e6, Year 2020 |
| 掲載日 | 2020年9月9日 |
 著者 著者 | Jiandong Huo / Yuguang Zhao / Jingshan Ren / Daming Zhou / Helen M E Duyvesteyn / Helen M Ginn / Loic Carrique / Tomas Malinauskas / Reinis R Ruza / Pranav N M Shah / Tiong Kit Tan / Pramila Rijal / Naomi Coombes / Kevin R Bewley / Julia A Tree / Julika Radecke / Neil G Paterson / Piyada Supasa / Juthathip Mongkolsapaya / Gavin R Screaton / Miles Carroll / Alain Townsend / Elizabeth E Fry / Raymond J Owens / David I Stuart /   |
| PubMed 要旨 | There are as yet no licensed therapeutics for the COVID-19 pandemic. The causal coronavirus (SARS-CoV-2) binds host cells via a trimeric spike whose receptor binding domain (RBD) recognizes ...There are as yet no licensed therapeutics for the COVID-19 pandemic. The causal coronavirus (SARS-CoV-2) binds host cells via a trimeric spike whose receptor binding domain (RBD) recognizes angiotensin-converting enzyme 2, initiating conformational changes that drive membrane fusion. We find that the monoclonal antibody CR3022 binds the RBD tightly, neutralizing SARS-CoV-2, and report the crystal structure at 2.4 Å of the Fab/RBD complex. Some crystals are suitable for screening for entry-blocking inhibitors. The highly conserved, structure-stabilizing CR3022 epitope is inaccessible in the prefusion spike, suggesting that CR3022 binding facilitates conversion to the fusion-incompetent post-fusion state. Cryogenic electron microscopy (cryo-EM) analysis confirms that incubation of spike with CR3022 Fab leads to destruction of the prefusion trimer. Presentation of this cryptic epitope in an RBD-based vaccine might advantageously focus immune responses. Binders at this epitope could be useful therapeutically, possibly in synergy with an antibody that blocks receptor attachment. |
 リンク リンク |  Cell Host Microbe / Cell Host Microbe /  PubMed:32585135 / PubMed:32585135 /  PubMed Central PubMed Central |
| 手法 | EM (単粒子) / X線回折 |
| 解像度 | 2.42 - 4.36 Å |
| 構造データ | EMDB-10863, PDB-6yor: EMDB-11119, PDB-6z97:  PDB-6yla:  PDB-6ym0: |
| 化合物 |  ChemComp-DMS: 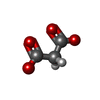 ChemComp-MLI:  ChemComp-NAG:  ChemComp-1PE: 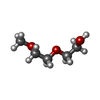 ChemComp-PG0:  ChemComp-HOH: |
| 由来 |
|
 キーワード キーワード |  VIRAL PROTEIN (ウイルスタンパク質) / VIRAL PROTEIN (ウイルスタンパク質) /  SARS-CoV-2 Spike protein / RBD / CR3022 / SARS-CoV-2 Spike protein / RBD / CR3022 /  complex / complex /  SARS-CoV-2 (SARSコロナウイルス2) / receptor binding domain (RBD) / Vagabond / SARS-CoV-2 Spike glycoprotein SARS-CoV-2 (SARSコロナウイルス2) / receptor binding domain (RBD) / Vagabond / SARS-CoV-2 Spike glycoprotein |
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア 万見文献について
万見文献について









