+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of R2 with 3'UTR and DNA in binding state | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | R2 complex / RNA BINDING PROTEIN/RNA/DNA / RNA BINDING PROTEIN-RNA-DNA complex | |||||||||
| 機能・相同性 | Zinc finger C2H2 type domain profile. / Zinc finger C2H2 type domain signature. / Zinc finger C2H2-type / Reverse transcriptase (RNA-dependent DNA polymerase) /  Reverse transcriptase domain / Reverse transcriptase (RT) catalytic domain profile. / Reverse transcriptase domain / Reverse transcriptase (RT) catalytic domain profile. /  RNA-directed DNA polymerase activity / DNA/RNA polymerase superfamily / Reverse transcriptase-like protein RNA-directed DNA polymerase activity / DNA/RNA polymerase superfamily / Reverse transcriptase-like protein 機能・相同性情報 機能・相同性情報 | |||||||||
| 生物種 |   Bombyx mori (カイコ) Bombyx mori (カイコ) | |||||||||
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 3.6 Å クライオ電子顕微鏡法 / 解像度: 3.6 Å | |||||||||
 データ登録者 データ登録者 | Deng P / Tan S / Wang J / Liu JJ | |||||||||
| 資金援助 |  中国, 1件 中国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Cell / 年: 2023 ジャーナル: Cell / 年: 2023タイトル: Structural RNA components supervise the sequential DNA cleavage in R2 retrotransposon. 著者: Pujuan Deng / Shun-Qing Tan / Qi-Yu Yang / Liangzheng Fu / Yachao Wu / Han-Zhou Zhu / Lei Sun / Zhangbin Bao / Yi Lin / Qiangfeng Cliff Zhang / Haoyi Wang / Jia Wang / Jun-Jie Gogo Liu /  要旨: Retroelements are the widespread jumping elements considered as major drivers for genome evolution, which can also be repurposed as gene-editing tools. Here, we determine the cryo-EM structures of ...Retroelements are the widespread jumping elements considered as major drivers for genome evolution, which can also be repurposed as gene-editing tools. Here, we determine the cryo-EM structures of eukaryotic R2 retrotransposon with ribosomal DNA target and regulatory RNAs. Combined with biochemical and sequencing analysis, we reveal two essential DNA regions, Drr and Dcr, required for recognition and cleavage. The association of 3' regulatory RNA with R2 protein accelerates the first-strand cleavage, blocks the second-strand cleavage, and initiates the reverse transcription starting from the 3'-tail. Removing 3' regulatory RNA by reverse transcription allows the association of 5' regulatory RNA and initiates the second-strand cleavage. Taken together, our work explains the DNA recognition and RNA supervised sequential retrotransposition mechanisms by R2 machinery, providing insights into the retrotransposon and application reprogramming. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_35347.map.gz emd_35347.map.gz | 28.8 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-35347-v30.xml emd-35347-v30.xml emd-35347.xml emd-35347.xml | 19.3 KB 19.3 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_35347.png emd_35347.png | 84.2 KB | ||
| その他 |  emd_35347_half_map_1.map.gz emd_35347_half_map_1.map.gz emd_35347_half_map_2.map.gz emd_35347_half_map_2.map.gz | 28.3 MB 28.3 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-35347 http://ftp.pdbj.org/pub/emdb/structures/EMD-35347 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-35347 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-35347 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_35347.map.gz / 形式: CCP4 / 大きさ: 30.5 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_35347.map.gz / 形式: CCP4 / 大きさ: 30.5 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 1.0979 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: #2
| ファイル | emd_35347_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
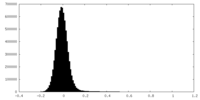
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_35347_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
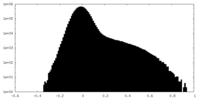
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : R2 complex
| 全体 | 名称: R2 complex |
|---|---|
| 要素 |
|
-超分子 #1: R2 complex
| 超分子 | 名称: R2 complex / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#2, #4, #3 |
|---|---|
| 由来(天然) | 生物種:   Bombyx mori (カイコ) Bombyx mori (カイコ) |
| 分子量 | 理論値: 177.28 KDa |
-分子 #1: DNA (60-MER)
| 分子 | 名称: DNA (60-MER) / タイプ: dna / ID: 1 / コピー数: 1 / 分類: DNA |
|---|---|
| 由来(天然) | 生物種:   Bombyx mori (カイコ) Bombyx mori (カイコ) |
| 分子量 | 理論値: 18.550889 KDa |
| 配列 | 文字列: (DC)(DA)(DA)(DG)(DC)(DG)(DC)(DG)(DG)(DG) (DT)(DA)(DA)(DA)(DC)(DG)(DG)(DC)(DG)(DG) (DG)(DA)(DG)(DT)(DA)(DA)(DC)(DT)(DA) (DT)(DG)(DA)(DC)(DT)(DC)(DT)(DC)(DT)(DT) (DA) (DA)(DG)(DG)(DT)(DA) ...文字列: (DC)(DA)(DA)(DG)(DC)(DG)(DC)(DG)(DG)(DG) (DT)(DA)(DA)(DA)(DC)(DG)(DG)(DC)(DG)(DG) (DG)(DA)(DG)(DT)(DA)(DA)(DC)(DT)(DA) (DT)(DG)(DA)(DC)(DT)(DC)(DT)(DC)(DT)(DT) (DA) (DA)(DG)(DG)(DT)(DA)(DG)(DC)(DC) (DA)(DA)(DA)(DT)(DG)(DC)(DC)(DT)(DC)(DG) (DT)(DC) |
-分子 #2: DNA (60-MER)
| 分子 | 名称: DNA (60-MER) / タイプ: dna / ID: 2 / コピー数: 1 / 分類: DNA |
|---|---|
| 由来(天然) | 生物種:   Bombyx mori (カイコ) Bombyx mori (カイコ) |
| 分子量 | 理論値: 18.434783 KDa |
| 配列 | 文字列: (DG)(DA)(DC)(DG)(DA)(DG)(DG)(DC)(DA)(DT) (DT)(DT)(DG)(DG)(DC)(DT)(DA)(DC)(DC)(DT) (DT)(DA)(DA)(DG)(DA)(DG)(DA)(DG)(DT) (DC)(DA)(DT)(DA)(DG)(DT)(DT)(DA)(DC)(DT) (DC) (DC)(DC)(DG)(DC)(DC) ...文字列: (DG)(DA)(DC)(DG)(DA)(DG)(DG)(DC)(DA)(DT) (DT)(DT)(DG)(DG)(DC)(DT)(DA)(DC)(DC)(DT) (DT)(DA)(DA)(DG)(DA)(DG)(DA)(DG)(DT) (DC)(DA)(DT)(DA)(DG)(DT)(DT)(DA)(DC)(DT) (DC) (DC)(DC)(DG)(DC)(DC)(DG)(DT)(DT) (DT)(DA)(DC)(DC)(DC)(DG)(DC)(DG)(DC)(DT) (DT)(DG) |
-分子 #3: Reverse transcriptase-like protein
| 分子 | 名称: Reverse transcriptase-like protein / タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Bombyx mori (カイコ) Bombyx mori (カイコ) |
| 分子量 | 理論値: 123.36243 KDa |
| 組換発現 | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 配列 | 文字列: MMASTALSLM GRCNPDGCTR GKHVTAAPMD GPRGPSSLAG TFGWGLAIPA GEPCGRVCSP ATVGFFPVAK KSNKENRPEA SGLPLESER TGDNPTVRGS AGADPVGQDA PGWTCQFCER TFSTNRGLGV HKRRAHPVET NTDAAPMMVK RRWHGEEIDL L ARTEARLL ...文字列: MMASTALSLM GRCNPDGCTR GKHVTAAPMD GPRGPSSLAG TFGWGLAIPA GEPCGRVCSP ATVGFFPVAK KSNKENRPEA SGLPLESER TGDNPTVRGS AGADPVGQDA PGWTCQFCER TFSTNRGLGV HKRRAHPVET NTDAAPMMVK RRWHGEEIDL L ARTEARLL AERGQCSGGD LFGALPGFGR TLEAIKGQRR REPYRALVQA HLARFGSQPG PSSGGCSAEP DFRRASGAEE AG EERCAED AAAYDPSAVG QMSPDAARVL SELLEGAGRR RACRAMRPKT AGRRNDLHDD RTASAHKTSR QKRRAEYARV QEL YKKCRS RAAAEVIDGA CGGVGHSLEE METYWRPILE RVSDAPGPTP EALHALGRAE WHGGNRDYTQ LWKPISVEEI KASR FDWRT SPGPDGIRSG QWRAVPVHLK AEMFNAWMAR GEIPEILRQC RTVFVPKVER PGGPGEYRPI SIASIPLRHF HSILA RRLL ACCPPDARQR GFICADGTLE NSAVLDAVLG DSRKKLRECH VAVLDFAKAF DTVSHEALVE LLRLRGMPEQ FCGYIA HLY DTASTTLAVN NEMSSPVKVG RGVRQGDPLS PILFNVVMDL ILASLPERVG YRLEMELVSA LAYAYDLVLL AGSKVGM QE SISAVDCVGR QMGLRLNCRK SAVLSMIPDG HRKKHHYLTE RTFNIGGKPL RQVSCVERWR YLGVDFEASG CVTLEHSI S SALNNISRAP LKPQQRLEIL RAHLIPRFQH GFVLGNISDD RLRMLDVQIR KAVGQWLRLP ADVPKAYYHA AVQDGGLAI PSVRATIPDL IVRRFGGLDS SPWSVARAAA KSDKIRKKLR WAWKQLRRFS RVDSTTQRPS VRLFWREHLH ASVDGRELRE STRTPTSTK WIRERCAQIT GRDFVQFVHT HINALPSRIR GSRGRRGGGE SSLTCRAGCK VRETTAHILQ QCHRTHGGRI L RHNKIVSF VAKAMEENKW TVELEPRLRT SVGLRKPAII ASRDGVGVIV DVQVVSGQRS LDELHREKRN KYGNHGELVE LV AGRLGLP KAECVRATSC TISWRGVWSL TSYKELRSII GLREPTLQIV PILALRGSHM NWTRFNQMTS VMGGGVG UniProtKB: Reverse transcriptase-like protein |
-分子 #4: 3'UTR
| 分子 | 名称: 3'UTR / タイプ: rna / ID: 4 / コピー数: 1 |
|---|---|
| 由来(天然) | 生物種:   Bombyx mori (カイコ) Bombyx mori (カイコ) |
| 分子量 | 理論値: 16.048569 KDa |
| 配列 | 文字列: GUAGAUCAGG CCCGUCUGAU CCAAUUUCGC CGGCGUACCC GGCGAUGAAA |
-分子 #5: ZINC ION
| 分子 | 名称: ZINC ION / タイプ: ligand / ID: 5 / コピー数: 2 / 式: ZN |
|---|---|
| 分子量 | 理論値: 65.409 Da |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 8 |
|---|---|
| グリッド | モデル: Quantifoil R1.2/1.3 / 支持フィルム - 材質: GRAPHENE OXIDE / 支持フィルム - トポロジー: HOLEY |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 298 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 50.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / Cs: 0.01 mm / 最大 デフォーカス(公称値): 1.5 µm / 最小 デフォーカス(公称値): 1.0 µm / 倍率(公称値): 64000 Bright-field microscopy / Cs: 0.01 mm / 最大 デフォーカス(公称値): 1.5 µm / 最小 デフォーカス(公称値): 1.0 µm / 倍率(公称値): 64000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 平均電子線量: 50.0 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: NONE / 詳細: ab-initial in cryosparc |
|---|---|
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD / ソフトウェア - 名称: RELION (ver. 3.1) |
| 最終 3次元分類 | クラス数: 3 / ソフトウェア - 名称: cryoSPARC (ver. 3.31) |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD / ソフトウェア - 名称: cryoSPARC (ver. 3.31) |
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 3.6 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 89089 |
-原子モデル構築 1
| 精密化 | 空間: REAL / プロトコル: BACKBONE TRACE |
|---|---|
| 得られたモデル |  PDB-8ibw: |
 ムービー
ムービー コントローラー
コントローラー














 Z
Z Y
Y X
X